- 事例No.PC-TUKS254357
-

Nanopore MinION Mk1D対応省スペースワークステーション
用途:Oxford Nanopore MinION Mk1D、シーケンス解析参考価格:416900円お客さまからのご相談内容
Oxford Nanopore MinION Mk1D の推奨要件を満たすスペックで、卓上設置が可能なPCを導入したい。予算は47万円以内。
OSはUbuntu 24.04 LTS、メモリ32GB、ストレージ2TB SSD、CPUはIntel i7 (12コア以上) を条件とする。
GPUはNVIDIA RTX 5090か、ラップトップ向けGPUを希望するが、難しい場合は最小要件でも可。
拡張性よりも省スペース性を重視したい。テガラからのご提案
GPUの選定と予算調整
推奨要件を満たす構成を検討しました。
RTX 5090を採用する場合は、ご予算の47万円を大幅に上回ります。
そのため、今回のご提案ではOxford Nanopore MinION Mk1D の最小要件を満たすGeForce RTX 5060Ti (16GB) を選定しています。
CPUはIntel Core Ultra 7 (8+12コア) 、メモリ32GB、ストレージ2TB SSDを搭載。性能と予算のバランスを実現した構成です。コンパクト筐体の採用
省スペース性を重視した「Define7 Compact」を採用しています。
サイズは幅210mm×高さ474mm×奥行427mmで、限られたスペースでも快適に運用可能です。一方で、筐体サイズおよびエアフロー設計の制約から、発熱量が大きい高消費電力のGPUや、カードサイズの大きいGPUの搭載は推奨していません。
高いGPU性能を重視される場合は、十分なエアフローを確保できる、より大型筐体の採用が前提となります。このような分野で活躍されている方へ
- ゲノム解析
- 分子生物学
- 臨床検査
- バイオインフォマティクス
- 医療情報学
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 7 265K 3.90GHz(8C/8T)+3.30GHz(12C/12T) メモリ 合計32GB DDR5 6400 16GB x 2 ストレージ1 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5060Ti 16GB ネットワーク 2.5Gbx1,Wi-Fi 7 筐体+電源 ミドルタワー型筐体+850W Cybenetics Gold OS Ubuntu 24.04 キーワード
MinION Mk1Dとは
MinION Mk1Dは、Oxford Nanopore Technologies社が提供するポータブルなDNA/RNAシーケンサー。
リアルタイムで長鎖リードの取得が可能で、ゲノム解析、メタゲノム解析、トランスクリプトーム解析など幅広い分野に対応。USB接続で動作し、フィールドワークやラボでの迅速な遺伝子解析に最適。ナノポア技術により、従来のシーケンサーでは困難だった構造変異やエピジェネティクス解析にも対応可能。事例追加日:2025/12/15
- 事例No.PC-T52S254279
-

Cell Ranger対応バイオインフォマティクス用ワークステーション
用途:RNA-seq解析、Cell Ranger、R/RStudio参考価格:1963500円お客さまからのご相談内容
PC-11781を見ての問い合わせ。
Cell Ranger を用いてシングルセルRNA-seq データ解析を、ローカルで実行可能な環境を導入したい。
解析規模は3万細胞×20サンプルで、これらを同時または順次処理を想定。R/RStudioやSeuratなどの下流解析も快適に動作させたい。
予算は200万円以内で、ストレージはシステム用・データ用・バックアップ用をそれぞれ確保することを希望する。テガラからのご提案
CPUについて
Cell Rangerの並列処理性能を最大限に活かすため、32コア構成のXeon Gold 6530を2基搭載し、合計64コアの2CPUマシンとしました。
メモリ構成について
本構成では16GBメモリを16枚搭載し、各CPUのメモリチャンネルをすべて活用する設計としています。
総メモリ容量は256GBで、Cell Rangerの推奨要件を満たしています。
加えて、ご要望のRやSeuratなどの下流解析も快適にご利用いただけます。ただし、解析規模や内容によっては、より大容量のメモリが推奨される場合があります。
今回の構成ではスロットがすべて埋まっているため、増設する際は容量の大きいモジュールへ交換が必要です。ストレージについて
システム用に2TB M.2、解析で扱うデータの保存用に4TB M.2、バックアップ用途として外付け12TB HDDを追加し、データ保護を強化。
将来的なデータ増加に備え、NASや追加ストレージのご提案も可能です。さらに今回は、ライフサイエンス研究者様応援キャンペーンのご利用で、10TB HDD を無償で1枚追加しております。
大規模なシングルセル解析では、サンプル数やデータ量が急速に増加します。
本キャンペーンは、追加費用なしでストレージを確保できる絶好の機会です。
キャンペーンの詳細は以下のリンクから※本キャンペーンは終了しました

GPUについて
今回は、機械学習やGPUアクセラレータを考慮しないため、画面描画用としてエントリークラスの RTX A400 を採用しました。
このような分野で活躍されている方へ
- ゲノム解析
- バイオインフォマティクス
- 分子生物学
- 免疫学
- 医薬学研究
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon Gold 6530 2.10GHz(TB 4.00GHz) 32C/64T ×2基構成 メモリ 合計256GB DDR5 5600 REG ECC 16GB x 16 ストレージ1 2TB SSD M.2 NVMe Gen4 ストレージ2 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (10GBase-T x2) 筐体+電源 タワー型筐体+1500W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit ストレージ3 外付けHDD 1ドライブモデル 12TB (RAIDなし) ストレージ4 10TB HDD S-ATA (ライフサイエンスキャンペーン) その他 ライフサイエンスキャンペーン ストレージサービス キーワード
Cell Rangerとは
Cell Rangerは、10x GenomicsのChromiumプラットフォームで得られる単一細胞RNAシーケンスデータを、一括で解析できるソフトです。
リードのマッピングから細胞×遺伝子マトリクス作成、クラスタリングまで自動化され、専門的なバイオインフォマティクス知識がなくても高品質な前処理や標準解析が可能です。大学や研究機関、製薬企業の研究者が、細胞多様性解析や細胞型同定、免疫レパートリー解析に広く利用しています。事例追加日:2025/11/27
- 事例No.PC-TUKS254328
-

MinION Mk1D用ワークステーション
用途:ナノポアシーケンシング解析 (MinION Mk1D)参考価格:982300円お客さまからのご相談内容
Oxford Nanopore Technologies社のMinION Mk1Dによるナノポアシーケンシング解析を予定している。
具体的な解析内容は未定だが、まずは予算申請用として見積もりを取得したい。テガラからのご提案
MinION Mk1Dに最適化した構成
MinION Mk1Dの公式要件に準拠し、USB Type-C接続やUbuntu 24.04対応など、シーケンシング環境に必要な条件を満たす構成としました。
Thunderbolt4やUSB 10Gbpsなどの高速I/Oに対応し、外部デバイスとの接続性も確保しています。
MinKNOWによるリアルタイム制御やデータストリーミングにも対応できるよう、CPU・メモリ・ストレージを強化しました。参考:MinION Mk1D IT requirements | Oxford Nanopore Technologies
CPUとメモリについて
CPUには20コア構成のIntel Core Ultra 7 265Kを採用しており、解析処理やデータ転送などの高負荷な作業にも十分対応できます。
メモリは64GBを搭載。MinKNOWの推奨要件である32GBを上回るメモリ容量を確保することで、解析処理の安定性を確保しています。GPUの選定について
NVIDIA GeForce RTX 5090 (32GB) を搭載し、将来的な機械学習やベースコーリング処理にも対応可能な、高性能GPUを選定しました。
このような分野で活躍されている方へ
- バイオインフォマティクス
- 医学
- 生物学
- ゲノム解析
- 次世代シーケンサー解析
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 7 265K 3.90GHz (8C/8T) +3.30GHz (12C/12T) メモリ 合計64GB DDR5 6400 32GB x 2 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5090 32GB ネットワーク 2.5Gbx1,Wi-Fi 7 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・MinION Mk1Dとは
MinION Mk1Dは、Oxford Nanopore Technologies社が提供するポータブルなDNA/RNAシーケンサー。リアルタイムで長鎖リードの取得が可能で、ゲノム解析、メタゲノム解析、トランスクリプトーム解析など幅広い分野に対応。USB接続で動作し、フィールドワークやラボでの迅速な遺伝子解析に最適。ナノポア技術により、従来のシーケンサーでは困難だった構造変異やエピジェネティクス解析にも対応可能。・MinKNOWとは
MinKNOWは、Oxford Nanopore Technologies社のDNA/RNAシーケンサーを制御・解析するための公式ソフトウェア。
サンプルのロードからリアルタイムのデータ取得、品質評価、基本的な解析までを一括して行えるため、生命科学や微生物学、がん研究など幅広い分野の大学や企業の研究者に活用されている。シーケンスの進行状況をリアルタイムで可視化しながら実験条件を柔軟に調整できる点が大きな特徴。事例追加日:2025/10/24
- 事例No.PC-TS25J253733
-

Cell Ranger用ワークステーション
用途:次世代シーケンサー解析、顔画像解析、ビッグデータ解析参考価格:2556400円お客さまからのご相談内容
バイオインフォマティクスや次世代シーケンサー解析、顔画像解析、ビッグデータ解析などを複数名 (5名程度) で同時に行える環境を社内に整備するために、ワークステーションの導入を検討している。
Cell RangerやQiime2などの解析ツールを使用予定で、128GB以上のメモリ、GeForce RTX 2080以上のGPU、Ubuntu 22.04のOSを希望。
将来的な拡張性も考慮し、ストレージは2TB以上、複数ユーザーによる同時利用を前提とした構成にしたい。テガラからのご提案
CPUとメモリ構成について
複数名の同時解析を想定し、Intel Xeon Gold 6530 (32コア) を2基搭載し、合計64コアの高並列処理が可能な構成としました。
5名での同時使用を想定する場合、一人当たり12コア前後使用できる計算です。メモリは512GBのDDR5 ECCを搭載しています。
Cell Rangerの最小要件は64GBですが、複数名の同時解析に対応するため、余裕を持った容量を確保しています。GPUの選定について
当初ご希望のRTX 2080は世代的に古く、最新の解析環境との互換性に懸念があるため、GeForce RTX 5080 16GBを採用しました。
TensorFlowなどの深層学習フレームワークとの互換性も高く、VRAM不足によるCPU処理への切り替えを防ぐ構成です。ストレージと拡張性について
ストレージは、システム用に1TB、データ保存用に8TBのNVMe Gen4 SSDを搭載しています。
システム領域と、各ユーザーのデータ保存領域を、別々のストレージに分けてマウントする想定です。
SSDは空き容量が減ると速度が低下しやすいため、システム用SSDの空き容量の減少を抑えることで、処理速度の安定性を保っています。OSとサポートについて
OSはUbuntu 22.04を採用。Linux環境でのバイオ系解析ツールとの親和性が高く、弊社でも多数の納入実績があります。
なお、Ubuntu 22.04のサポートは2027年4月までであるため、将来的なアップグレードも視野に入れた構成としています。このような分野で活躍されている方へ
- バイオインフォマティクス
- 次世代シーケンサー解析
- 顔画像解析
- ビッグデータ解析
- 統計解析
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon Gold 6530 2.10GHz(TB 4.00GHz) 32C/64T x2 メモリ 合計512GB DDR5 5600 REG ECC 32GB x 16 ストレージ1 1TB SSD M.2 NVMe Gen4 ストレージ2 8TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5080 16GB ネットワーク on board (10GBase-T x2) 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 22.04 キーワード
・Cell Rangerとは
Cell Rangerは10x Genomics社によるソフトウェアパイプラインの1種。シングルセルRNAシークエンスデータの処理、クラスタリング、遺伝子表現量の量化を行うことができる。 10x Genomics Chromeを使って生成されたシングルセルRNAシークエンスデータを処理したり、 遺伝子表現クラスタリングを行いシングルセルのサブポピュレーションを同定することが可能。その他、バーチャルリファレンスにマッピングし遺伝子を量化しての表現行列作成にも対応。事例追加日:2025/10/14
- 事例No.PC-25000268
-

次世代シーケンス (NGS) データ解析用ワークステーション
用途:ゲノムアセンブリ、多型解析 (Hifiasm、BWA-MEM2、GATK、Braker3、YaHSなど) 、RNA-seq解析 (HISAT2, STAR, RSEMなど) (※Helixerを使用する場合、GPUの交換が必要です)参考価格:1490500円お客さまからのご相談内容
事例No.PC-12218を見ての問い合わせ。
予算100万円から150万円で、ゲノムアセンブリ、NGSデータ解析を含めた多型解析やRNA-seq解析に使用可能なマシンの購入を検討している。
将来に向けて、メモリの拡張性などを確保したい。テガラからのご提案
事例No.PC-12218をベースにして、構成を検討しました。
拡張性のあるメモリ構成
CPUは2025年5月時点の最新モデル「Xeon W7-3545 24コア」をご予算に合わせて採用しました。
メモリは合計256GB (32GB×8枚) を搭載しています。
空きスロットが8つありますので、同じ32GBメモリモジュールを8枚追加いただくことで「合計512GB」へ増設が可能です。
GPUは、画面描画用として「NVIDIA T400 4GB」の後継機種「RTX A400 4GB」を選択しました。(ご参考)
VRAMの容量を重視するソフトウェア (Helixerなど) をご利用の場合は、GPUメモリを優先した構成をご提案可能です。
Helixerは、GPUに11 GB以上のVRAMが要求されております。
Helixerの公式GitHubは こちら (※外部ページに飛びます)本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
お客様のご要望に応じて柔軟にお見積もりをご提案しております。
掲載内容とは異なるご用途やご予算の場合でも、どうぞお気軽にご相談ください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W7-3545 2.70GHz (TB3.0時 最大4.8GHz) 24C/48T メモリ 合計256GB DDR5 5600 REG ECC 32GB x8 ストレージ1 4TB SSD M.2 NVMe Gen4 ストレージ2 16TB HDD S-ATA ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 タワー型筐体 1000W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・多型解析 (Polymorphism Analysis) とは
生物個体間のDNA配列の違い (多型) を検出・解析する手法。 個体差の遺伝的要因を探るほか、系統関係や進化過程の推定に活用される。・Helixerとは
Helixerは、深層学習 (Deep Learning) と隠れマルコフモデル (HMM) を組み合わせた、真核生物ゲノムの構造的アノテーション (遺伝子構造の予測) を行うオープンソースのツール。
GPUを活用することで、高速な処理が可能。・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。
・GATKとは
GATK (Genome Analysis Toolkit) は、次世代シーケンサーから出力された塩基配列データからバリアントの解析 (遺伝子の変異解析) を行うための解析ツール群。内包するツールは、個別に使用することも連携させて使用することもできる。
事例追加日:2025/05/15
- 事例No.PC-12218
-

NGS解析用ワークステーション (2024年11月版)
用途:RNA-seq解析 (Trinity) 、ゲノム解析 (SPAdes、Platanus、Racon、medaka、FALCON、Canu)参考価格:1191300円お客さまからのご相談内容
NGS関連の予算申請のため、解析用PCの必要スペックを相談したい。
用途は、推定280Mbの2倍体生物のゲノムアセンブリで、RNA-seqの解析まで研究を広げる予定がある。予算は100万~120万ほどで、OSはLinux (Ubuntu) を希望。RNA-seq解析ではTrinityの利用を予定している。
ゲノム解析に関しては、アセンブリングに一番スペックが必要になると推測しており、使用ソフトウェアは、ハプロイドのサンプルではSPAdes、Platanus、Racon、medaka、ディプロイドのサンプルではFALCONかCanuを想定。
10Gb程度のデータからアセンブリング~シンテニー解析を行うつもりだが、詳細なソフトまでは決めかねている。
以上の条件に合致するマシンを、予算内で提案して欲しい。
テガラからのご提案
解析用PCの選定においては、計算に十分なメモリ容量の確保を重視するのが一般的な考え方です。そのため、スペック選定の順番とコスト比重は、まずメモリを必要量確保し、残った予算で解析用のCPUやデータ用ストレージを検討する流れとなります。
本件では、10Gb程度のデータから始めるというお話ですので、ご予算120万円の範囲である程度の解析を行うことができる構成をご提案しています。構成のポイントはメモリの拡張性で、「後から+768GBまでは増設できる」点が特徴です。扱うデータ量を段階的に増やす過程で、メモリ不足が発生した場合に増設できる余地のある構成になっています。
注意点として、本事例の構成は解析が可能なメモリ容量を重視しているため、処理速度そのものを重視した構成ではありません。処理速度について条件がある場合は、お気軽にご相談ください。
参考:Trinityのメモリについての表記(Running Trinity · trinityrnaseq/trinityrnaseq Wiki · GitHub)







通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-3435X 3.10GHz(TB3.0時4.70GHz) 16C/32T メモリ 合計 256GB DDR5 4800 REG ECC 32GB × 8 ストレージ1 1TB SSD M.2 NVMe Gen4 ストレージ2 16TB HDD S-ATA ビデオ NVIDIA T400 4GB (MiniDisplayPort x3) ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 タワー型筐体 + 1000W OS Ubuntu 22.04 ■キーワード
・Trinityとは
Trinityは、トランスクリプトームのde novoアセンブリを行うためのソフトウェア。リファレンスゲノムが利用できない生物種や、新規転写産物の発見を目的とする場合に有効。RNA-Seqのリード(短い塩基配列)を使って、元のmRNA配列を復元することができる。
・SPAdesとは
SPAdesは、ゲノム配列のde novoアセンブリを行うためのソフトウェア。次世代シーケンサー (NGS) データを用いてゲノム配列を再構築するためのアセンブラで、特にバクテリアゲノムのアセンブリに適している。シングルセルシーケンシング (SCS) データにも対応している。
参考:GitHub – ablab/spades: SPAdes Genome Assembler ※外部サイトに飛びます
・Platanusとは
Platanusは、ゲノム配列のde novoアセンブリを行うためのソフトウェア。特に高度に異質性のあるゲノムのアセンブリに適したツールで、次世代シーケンサーのショートリードデータを使用して、高精度なゲノム配列を再構築することができる。
参考:GitHub – rkajitani/Platanus_B: De novo genome assembler for bacterial genomes ※外部サイトに飛びます
・Raconとは
Raconは、ロングリードシーケンスデータを用いたde novoゲノムアセンブリにおいて、高速かつ正確なコンセンサス配列を生成するためのツール。エラー率の高いロングリードから高品質なコンセンサス配列を迅速に生成することを目的としており、特にPacBioやOxford Nanopore Technologiesのデータに適している。
・medakaとは
medakaは、次世代シーケンシングデータの解析、特にDNAの変異検出に使用されるツール。主にOxford Nanopore Technologies (ONT)のロングリードシーケンスデータを対象としたポリッシングと変異検出のためのツールでで、特に、de novoアセンブリの後処理や、既知のリファレンスゲノムに対する変異コールに適している。
参考:GitHub – nanoporetech/medaka: Sequence correction provided by ONT Research ※外部サイトに飛びます
・FALCONとは
FALCONは、PacBioのロングリードシーケンスデータを用いたde novoゲノムアセンブリを行うためのソフトウェア。Pacific Biosciences (PacBio) 社が開発したde novoゲノムアセンブラーで、大規模で複雑なゲノムのアセンブリに適している。
・canuとは
Canuは、ロングリードシーケンスデータを用いたde novoゲノムアセンブリを行うためのソフトウェア。PacBioやOxford Nanopore Technologiesのロングリードデータに特化したde novoアセンブラーで、大規模で複雑なゲノムのアセンブリに適している。
事例追加日:2024/11/06
- 事例No.PC-12146
-

シーケンス解析・DeepLeaning用マシン
用途:WES (全エクソームシーケンス)解析、ロングリードシーケンス解析、DeepLeaning参考価格:1474000円お客さまからのご相談内容
WES (全エクソームシーケンス) やロングリードのシーケンス解析に加えて、DeepLearningでも使用可能なマシンの購入を検討している。
予算は150万円以内で、居室の電源は100V。オンプレミス環境で使用し、将来的にはビデオカードやメモリの増設を考えている。
CUDAToolkitのプリインストールが希望で、現地設置を含めた内容で提案して欲しい。テガラからのご提案
ご連絡いただいた用途に合わせてPC構成を検討しました。
ご使用目的とご予算に合わせた構成
GPUを用いた解析処理を想定して、性能とコストの両面でメリットのある「GeForce RTX4090 24GB」を採用しました。
CPUは、ご予算の範囲内で選択できる製品の中でも特にコア数が多い「Ryzen Threadripper 7960X 24コア」を選択しています。将来的なスペック増強に対する注意点
100V電源環境では、消費電力の関係から2枚目のGPU (RTX4090) の搭載が難しいため、GPU増設を考慮しない構成にてご提案しています。
200V環境でのご利用や、別GPUの利用を想定される場合にはご相談ください。メモリに関しては、4つ存在するメモリスロットを全て使用しており、空きスロットがございません。そのため,メモリ容量を増やす場合は初期搭載の32GBメモリモジュールを取り外し、より容量の大きいモジュールに交換する方法での対応を想定しています。
なお、本件では初期状態でのスペックや設置環境などの条件を優先したご案内としておりますが、拡張性を重視したご相談も承っています。
様々なサポートのご提案
「若手研究支援キャンペーン」の対象でしたので、キャンペーン特典としてあんしん+3年保証 (標準1年保証) を無料で付与した内容でご提案しました。
キャンペーン特典は、以下のA・Bいずれかをご選択いただけます。特典A 研究開発向けのオーダーメイドPCや各種関連サービスを5%割引 特典B PCの延長保証を3年分無料で付与 (標準保証期間:1年) また、お客様のご要望にあわせて、現地設置サポートを含めた内容でご提案しました。現地への搬入・設置のご要望は、是非お気軽にご相談ください。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。







通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen Threadripper 7960X (4.20GHz 24コア) メモリ 128GB REG ECC (32GBx4枚) ストレージ1 2TB SSD M.2 NVMe Gen4 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA Geforce RTX4090 24GB ネットワーク on board (2.5GBase-T x1) Wi-Fi x1 筐体+電源 タワー型筐体 + 1200W OS Ubuntu 22.04 その他 CUDA Toolkit 11 プリインストール
※参考価格は「あんしん+3年保証の無料付与」と現地設置作業(有償)を含めた価格です。■キーワード
・WES (Whole Exome Sequencing) とは
ゲノムのエクソンと呼ばれるタンパク質翻訳領域を対象に、シーケンス解析を行う技術。このタンパク質翻訳領域に遺伝子疾患の原因となる変異が、多く存在することが知られている。WGS(全ゲノムシーケンス)と比較して、解析対象の範囲が狭い分、コストや解析時間を削減できる。
事例追加日:2024/09/18
- 事例No.PC-11668
-

Omics解析向けワークステーション
用途:R、Python3、SAMtoolsやBWA、STARを用いた基本的なオミクス解析、Higlassを用いたHi-Cデータの可視化参考価格:1556500円お客さまからのご相談内容
現在使用しているバイオインフォマティクス専用ワークステーションの買い替えを検討している。
具体的な用途として、基本的なOmics解析に用いるSAMtoolsやSTAR、Hi-Cデータの可視化に用いるHiglassをスムーズに運用したい。
これらの用途を前提に、現在使っているPCと同等かそれ以上のスペックの構成を予算80万~160万円の範囲で提案してほしい。なお、現在使用しているPCのスペックは以下の通り。
CPU Intel Xeon E5-2640 v4 ×2(20コア/40スレッド) メモリ 256GB REG ECC ビデオ NVIDIA Quadro P620 OS Ubuntu 22.04 テガラからのご提案
お客さまご希望の条件に沿った構成をご提案しました。
ご予算内でCPUスペックを重視した構成
ご予算に合わせて、現在ご利用のマシンよりもスペックのグレードを高めた構成です。
CPUはXeon Gold 5418Yを2基搭載し、現在ご利用のマシン (20コア) の2倍以上である48コアを実現しています。
メモリ搭載量は現在のマシンと同じ256GBですが、メモリスロットの空きが8スロット分あるため、将来のメモリ増設に対応しています。
ストレージ容量は、解析用途であることを踏まえて、余裕を見た4TBのM.2 NVMe Gen4 SSDを選定しています。
NVMe接続の製品のため、SATA接続のHDDやSSDと比較して高速なデータの読み込み/書き込みが期待できます。合計48コアのCPUと256GBのメモリ容量により、計算量が大きくなりやすいバイオインフォマティクス解析でも迅速な計算処理が見込めます。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon Gold 5418Y (2.00GHz 24コア) ×2 メモリ 256GB REG ECC ストレージ 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA T1000 8GB ネットワーク on board (10GBase-T x2) 筐体+電源 ミドルタワー型筐体 + 1000W OS Ubuntu 22.04 ■キーワード
・Omics解析とは
Omics解析は、生物学や医学の分野で広く使用されるデータ駆動型のアプローチ。Omicsとはゲノミクス、プロテオミクス、トランスクリプトミクスなど、生物学的なデータを収集・解析するための技術の総称。
Omics解析では、高スループットの実験技術や次世代シーケンシングなどの先端技術が活用される。これにより生成される大量のデータは、統計学的な手法やデータマイニングの手法を用いて解析され、疾患のメカニズム解析や新たなバイオマーカーの同定、個別化医療への応用などが可能となる。・Hi-C法とは
3C(Chromosome Conformation Capture; 染色体立体配座捕捉)法を発展させた全ゲノム解析手法。細胞核内ゲノム3次元構造において空間的に近接する任意のゲノムDNA断片のペアを、次世代シーケンサーを用いて網羅的に検出し、ゲノム3次元構造を推定・解析できる。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・STARとは
STAR は RNA-Seqで得られたリード(生データ)をリファレンス配列にマッピングするプログラム。Github上で公開されており、要求されるスペックは高いものの、高速なマッピング速度を有している。
・HiGlassとは
HiGlassとは大規模な Hi-C およびその他のゲノム データ セットを高速に可視化できるデータビューア。他のオミックスデータと連携させつつ、探索的データ解析ができる。
事例追加日:2024/06/26
- 事例No.PC-11922
-

ddRAD-Seq解析用ワークステーション
用途:Stacksを用いた大容量シーケンスリードのデータ解析、ADMIXTURE・BayesAssを用いた集団遺伝学解析参考価格:600600円お客さまからのご相談内容
次世代シーケンサー (Illumina NovaSeqX) によるddRAD-Seq解析用のワークステーションの導入を検討している。
具体的な用途としては、主に下記を想定している。・解析ソフトStacksによる大容量シーケンスリードのデータ解析
・数万SNPsを対象としたADMIXTURE、 PCA、BayesAss等の集団遺伝学解析現在は、以前テグシスにて購入した下記構成のPCを利用しているが、計算がとても速い一方で、実施する処理の規模が大きくないためにスペックを十分に活かしきれていない。
そのため、この構成よりも多少スペックが落ちても構わないので、予算70-80万円程度を前提に最適な構成を提案して欲しい。■利用しているPCの構成 CPU AMD Ryzen Threadripper3 3970X (3.70GHz 32コア) メモリ 256GB ストレージ1 500GB SSD S-ATA ストレージ2 8TB HDD S-ATA ビデオ NVIDIA T400 2GB ネットワーク on board(10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー型筐体 + 850W OS Ubuntu 20.04 テガラからのご提案
お客さまご希望の条件に沿った構成をご提案しました。
ご予算内で解析処理性能を重視した構成
ご予算70万~80万円の条件を前提に、現在ご利用のマシンからスペックをスケールダウンした構成です。
CPUは2024年6月時点で最新であるRyzen 7000シリーズの最上位モデルAMD Ryzen9 7950Xを搭載しています。
ストレージなどの基本的な構成は現在ご利用いただいているマシンを踏襲しつつ、スペックが解析速度に大きく影響するCPUとメモリ容量に重点的にご予算を割くようにパーツを選定しています。
16コア/32スレッドを搭載したCPUと192GBのメモリ容量により、ご予算内で検討可能な構成の中でも、特に高速な解析処理の実行が期待できます。
なお、CPUコア数・メモリ容量ともにこのシステムの上限となります。より性能の高いマシンや将来的なアップグレードを想定した構成をご希望の場合にはご相談ください。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7950X (4.50GHz 16コア) メモリ 192GB ストレージ1 500GB SSD S-ATA ストレージ2 8TB HDD S-ATA ビデオ NVIDIA T400 4GB ネットワーク on board(2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー型筐体 + 850W OS Ubuntu 22.04 ■キーワード
・ddRAD-Seq解析とは
ddRAD-Seq (double digest restriction-site associated DNA sequencing) 解析は、次世代シーケンシング技術を用いて制限酵素認識サイトの近隣領域を解析する手法であるRAD-seq (Restriction-site Associated DNA Sequencing) 解析の一種。モデル以外の種からゲノム規模のデータを配列決定できるため、大量の遺伝子マーカーの開発を迅速かつ効率的に行うことができる。
・Stacksとは
Stacksは、Illumina プラットフォームによって生成されるような短い読み取りシーケンスから遺伝子座を構築するためのソフトウェアパイプライン。RAD-seqなどの制限酵素ベースのデータを用いて遺伝地図を構築し、集団ゲノミクスや系統解析を行うために開発された。
・ADMIXUTUREとは
ADMIXTUREは、多座 SNP 遺伝子型データセットから個々の祖先を最大尤度で推定するためのソフトウェア。高速数値最適化アルゴリズムを使用することにより、推定値を迅速に計算することができる。
・BayesAssとは
BayesAssは、連鎖していない多座遺伝子型を使用して集団間の最近の移住率を推測するためのプログラム。マルコフ連鎖モンテカルロ法を用いて集団間最近の移住率の事後確率を推定することができる。
事例追加日:2024/06/17
- 事例No.PC-11132
-

NGSデータ処理とマルチオミクス解析用マシン
用途:アンプリコンシーケンス解析のデータ処理・マルチオミクスの統合解析参考価格:779900円お客さまからのご相談内容
アンプリコンシーケンス解析のデータ処理とマルチオミクスの統合解析用ワークステーションの導入を考えている。
Rパッケージ (WGCNA、 lavaan、 ggplot、 arules、 imagerなど) やigraph、QIIME2を使用する予定。
写真の解析も行う予定だが、データ量としては多くない (週に450MB程度) 。CPUで処理・解析を行うことを考えているため、CPUの性能を重視している。希望する条件は以下の通り。
・CPU:性能を重視
・メモリ:128GB以上
・ストレージ:512GB程度
・OS:なし
・使用するソフトウェア:Rパッケージ (WGCNA、 lavaan、 ggplot、 arules、 imagerなど) 、igraph、QIIME2
・予算:80万円程度テガラからのご提案
お客さまご希望の条件に沿った構成をご提案しました。
2023年10月時点で最新のXeon W-2400シリーズを搭載した構成です。
ご予算内に収まる製品の中で最も上位のモデルであるIntel Xeon W5-2465X (16コア) を選択しています。
なお、Rでマルチスレッド動作を行うためには、並列化パッケージを導入する必要があります。並列化パッケージ未導入の状態でRプログラムを実行した場合はシングルスレッド動作になるため、コア数を有効に活用することができませんのでご注意ください。メモリ搭載量は128GBとしていますが、空きスロットが4スロットあるため、今後メモリを増設することも可能です。
週に450MB程度の画像解析を行う場合、それほど高いGPU性能は要求されないと考えられます。
そのため、ビデオカードはワークステーション向けのエントリーモデルであるNVIDIA T400 4GBを選択していますが、ご希望に応じて変更も可能です。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2465X (3.10GHz 16コア) メモリ 128GB REG ECC ストレージ 500GB SSD M.2 ビデオ NVIDIA T400 4GB ネットワーク on board (2.5GbE x1, 10GbE x1) 筐体+電源 タワー型筐体 + 1000W OS なし キーワード
・アンプリコンシーケンス解析とは
アンプリコンシーケンス解析は、特定のDNAまたはRNA領域を高速にシーケンスする分子生物学手法。特定のプライマーを使って遺伝子、遺伝子領域、またはフラグメントをPCR反応で増幅し、次世代シーケンサーでシーケンスする。微生物学、遺伝学、生態学など多くの分野で使用され、遺伝子多型、微生物の同定、疾患関連の変異、環境の多様性の調査などに応用される。得られたデータをバイオインフォマティクスツールで解析し、生物学的情報を取得する。・Omics解析とは
Omics解析は、生物学や医学の分野で広く使用されるデータ駆動型のアプローチ。Omicsとはゲノミクス、プロテオミクス、トランスクリプトミクスなど、生物学的なデータを収集・解析するための技術の総称。
Omics解析では、高スループットの実験技術や次世代シーケンシングなどの先端技術が活用される。これにより生成される大量のデータは、統計学的な手法やデータマイニングの手法を用いて解析され、疾患のメカニズム解析や新たなバイオマーカーの同定、個別化医療への応用などが可能となる。・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。
多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。・igraphとは
igraphはグラフの作成やネットワーク分析のためのオープンソースライブラリ。C/C++、 R、 Python、 Mathematicaでのプログラミングに対応している。・QIIME2とは
QIIME2は微生物叢分析のためのオープンソースのソフトウェアパッケージ。データと分析の透明性を重視しており、専用のwebサイト「QIIME2 View」から簡単に分析データを確認することができる。プラグインによって定期的に新たな機能が追加されている。事例追加日:2023/10/31
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
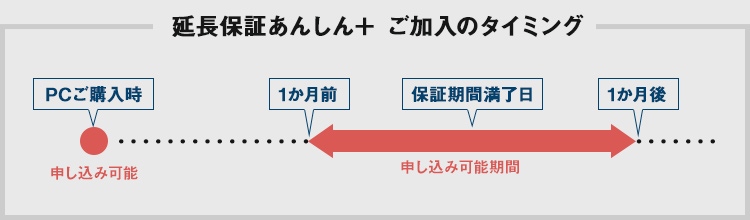
| 「あんしん+」 もしもの時の延長保証サービス |
|
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 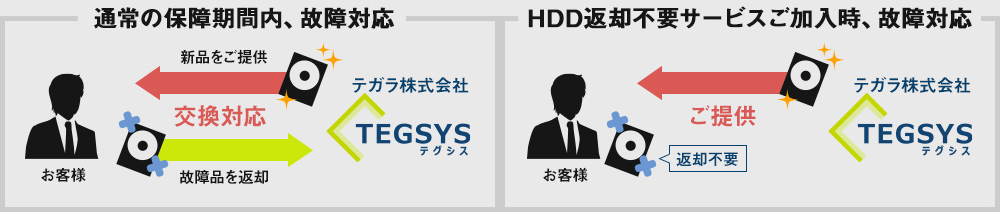
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。