- 事例No.PC-TS2J253952
-

大規模ゲノム解析向け2CPU・512GBメモリ搭載ワークステーション
用途:NGSゲノム解析、RNA-seq解析 (VCFtools、PLINK2、RFMIX2)参考価格:1794100円お客さまからのご相談内容
ゲノムデータを用いた集団遺伝学・ゲノム進化学解析に適したワークステーションを導入したい。
主な作業として、1万人規模の全ゲノムデータの解析 (VCF形式でRFMIX2やVCFtools、PLINK2などを利用)。
さらには、RNA-seq データのリファレンスゲノムへのマッピング・データ間比較解析を想定している。
CPU 32コア以上、メモリ256または512GB、4TB SSDを備えた構成を基準に、100〜150万円の範囲で、これらの要件に合う最適な構成を相談したい。テガラからのご提案
CPU構成について
PLINK2やVCFtoolsはマルチスレッド並列処理が中心のため、コア数の確保が処理時間に大きく影響します。
そこで、Intel Xeon 6517P (16コア) を2基搭載し、合計32コア環境を構築しました。併せて、2CPU構成とすることで、各CPUが8チャネルずつ、合計16チャネルのメモリ帯域を並列に利用可能です。
これにより、大規模データを扱うゲノム解析でも、安定した並列処理性能を発揮します。メモリ構成について
1万人規模の全ゲノムデータ (VCFファイル) を解析する場合、メモリ帯域と容量の確保が重要なポイントです。
本構成では、512GB (32GB×16枚) を搭載し、2CPU × 8チャネルの 最大帯域構成としました。
高スレッド処理時でも帯域飽和を抑え、CPU性能を十分に引き出せる設計となっています。ストレージとGPUについて
ストレージは4TBのM.2 NVMe Gen4 SSDを搭載し、VCF や BAM など大容量データの高速な読み書き性能を確保しました。
また、主要な解析ツールはCPU処理が主体であるため、高性能GPUは採用せず、画面表示用としてNVIDIA RTX A400 (4GB) を選択しています。このような分野で活躍されている方へ
- ゲノム科学
- 計算生物学
- バイオインフォマティクス
- 進化遺伝学
- RNA解析
テガラのオーダーメイド PC 製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。







通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon 6517P 3.20GHz(TB 4.20GHz) 16C/32T ×2基構成 メモリ 合計512GB DDR5 5600 REG ECC 32GB x 16 ストレージ 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (10GbE x2) 筐体+電源 タワー型筐体+1000W 80PLUS PLATINUM OS Ubuntu 24.04 保証 HDD返却不要サービス 1年 キーワード
VCFtoolsとは
VCFtoolsは、VCF形式のゲノム変異データを効率的に加工・抽出・統計解析できるコマンドラインツール群です。
大規模シーケンスデータの品質管理やフィルタリングに広く利用され、国際プロジェクトでも活用されています。PLINK2とは
PLINK2は、GWASや集団構造解析など全ゲノム規模の統計解析を実行できる総合解析ツールです。
医療ゲノム研究や創薬研究、バイオバンク解析などで世界的に利用されており、大規模データへの対応力と計算効率の高さが特長です。
VCFやBCF形式にも対応し、研究開発現場での実用性に優れています。RFMIX2とは
RFMIX2は、混合集団における局所祖先推定を高精度で行うための解析ソフトウェアです。
機械学習を活用し、染色体上の各領域の祖先起源を推定できるため、人類遺伝学や疾患関連解析で活用されています。
祖先情報を組み込んだ高度な解析を可能にする点が、大学や企業研究者から評価されています。事例追加日:2026/2/27
- 事例No.PC-TUKS254357
-

Nanopore MinION Mk1D対応省スペースワークステーション
用途:Oxford Nanopore MinION Mk1D、シーケンス解析参考価格:416900円お客さまからのご相談内容
Oxford Nanopore MinION Mk1D の推奨要件を満たすスペックで、卓上設置が可能なPCを導入したい。予算は47万円以内。
OSはUbuntu 24.04 LTS、メモリ32GB、ストレージ2TB SSD、CPUはIntel i7 (12コア以上) を条件とする。
GPUはNVIDIA RTX 5090か、ラップトップ向けGPUを希望するが、難しい場合は最小要件でも可。
拡張性よりも省スペース性を重視したい。テガラからのご提案
GPUの選定と予算調整
推奨要件を満たす構成を検討しました。
RTX 5090を採用する場合は、ご予算の47万円を大幅に上回ります。
そのため、今回のご提案ではOxford Nanopore MinION Mk1D の最小要件を満たすGeForce RTX 5060Ti (16GB) を選定しています。
CPUはIntel Core Ultra 7 (8+12コア) 、メモリ32GB、ストレージ2TB SSDを搭載。性能と予算のバランスを実現した構成です。コンパクト筐体の採用
省スペース性を重視した「Define7 Compact」を採用しています。
サイズは幅210mm×高さ474mm×奥行427mmで、限られたスペースでも快適に運用可能です。一方で、筐体サイズおよびエアフロー設計の制約から、発熱量が大きい高消費電力のGPUや、カードサイズの大きいGPUの搭載は推奨していません。
高いGPU性能を重視される場合は、十分なエアフローを確保できる、より大型筐体の採用が前提となります。このような分野で活躍されている方へ
- ゲノム解析
- 分子生物学
- 臨床検査
- バイオインフォマティクス
- 医療情報学
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 7 265K 3.90GHz(8C/8T)+3.30GHz(12C/12T) メモリ 合計32GB DDR5 6400 16GB x 2 ストレージ1 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5060Ti 16GB ネットワーク 2.5Gbx1,Wi-Fi 7 筐体+電源 ミドルタワー型筐体+850W Cybenetics Gold OS Ubuntu 24.04 キーワード
MinION Mk1Dとは
MinION Mk1Dは、Oxford Nanopore Technologies社が提供するポータブルなDNA/RNAシーケンサー。
リアルタイムで長鎖リードの取得が可能で、ゲノム解析、メタゲノム解析、トランスクリプトーム解析など幅広い分野に対応。USB接続で動作し、フィールドワークやラボでの迅速な遺伝子解析に最適。ナノポア技術により、従来のシーケンサーでは困難だった構造変異やエピジェネティクス解析にも対応可能。事例追加日:2025/12/15
- 事例No.PC-TUKS254328
-

MinION Mk1D用ワークステーション
用途:ナノポアシーケンシング解析 (MinION Mk1D)参考価格:982300円お客さまからのご相談内容
Oxford Nanopore Technologies社のMinION Mk1Dによるナノポアシーケンシング解析を予定している。
具体的な解析内容は未定だが、まずは予算申請用として見積もりを取得したい。テガラからのご提案
MinION Mk1Dに最適化した構成
MinION Mk1Dの公式要件に準拠し、USB Type-C接続やUbuntu 24.04対応など、シーケンシング環境に必要な条件を満たす構成としました。
Thunderbolt4やUSB 10Gbpsなどの高速I/Oに対応し、外部デバイスとの接続性も確保しています。
MinKNOWによるリアルタイム制御やデータストリーミングにも対応できるよう、CPU・メモリ・ストレージを強化しました。参考:MinION Mk1D IT requirements | Oxford Nanopore Technologies
CPUとメモリについて
CPUには20コア構成のIntel Core Ultra 7 265Kを採用しており、解析処理やデータ転送などの高負荷な作業にも十分対応できます。
メモリは64GBを搭載。MinKNOWの推奨要件である32GBを上回るメモリ容量を確保することで、解析処理の安定性を確保しています。GPUの選定について
NVIDIA GeForce RTX 5090 (32GB) を搭載し、将来的な機械学習やベースコーリング処理にも対応可能な、高性能GPUを選定しました。
このような分野で活躍されている方へ
- バイオインフォマティクス
- 医学
- 生物学
- ゲノム解析
- 次世代シーケンサー解析
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 7 265K 3.90GHz (8C/8T) +3.30GHz (12C/12T) メモリ 合計64GB DDR5 6400 32GB x 2 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5090 32GB ネットワーク 2.5Gbx1,Wi-Fi 7 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・MinION Mk1Dとは
MinION Mk1Dは、Oxford Nanopore Technologies社が提供するポータブルなDNA/RNAシーケンサー。リアルタイムで長鎖リードの取得が可能で、ゲノム解析、メタゲノム解析、トランスクリプトーム解析など幅広い分野に対応。USB接続で動作し、フィールドワークやラボでの迅速な遺伝子解析に最適。ナノポア技術により、従来のシーケンサーでは困難だった構造変異やエピジェネティクス解析にも対応可能。・MinKNOWとは
MinKNOWは、Oxford Nanopore Technologies社のDNA/RNAシーケンサーを制御・解析するための公式ソフトウェア。
サンプルのロードからリアルタイムのデータ取得、品質評価、基本的な解析までを一括して行えるため、生命科学や微生物学、がん研究など幅広い分野の大学や企業の研究者に活用されている。シーケンスの進行状況をリアルタイムで可視化しながら実験条件を柔軟に調整できる点が大きな特徴。事例追加日:2025/10/24
- 事例No.PC-TUKJ253537
-

遺伝子多型解析用ワークステーション
用途:植物ゲノムデータ解析、遺伝子多型解析 (SNP解析)参考価格:529100円お客さまからのご相談内容
植物の全ゲノムシークエンスデータについて、遺伝子多型解析以降の解析をするためのPCを検討中。
予算は50万円程度。
将来的にはショートリードシークエンサーやロングリードシークエンサーも視野に入れている。テガラからのご提案
メモリについて
植物の全ゲノム解析では、扱うデータ量が非常に大きくなるため、計算速度以上に「メモリ容量」が重要になります。
特に、マッピングやアセンブリ、遺伝子多型解析などの処理では、大量の配列データを一度に読み込み、保持しながら計算を進める必要があります。そのため、十分なメモリを確保することで、より大規模なデータの解析が可能になり、処理効率も向上します。
今回の構成では128GBのメモリを搭載。空きスロットを確保しており、最大256GBまで拡張できる設計です。
これにより、将来的なロングリードシークエンス解析にも対応できます。ストレージについて
入力データや中間ファイルが非常に大きくなることを想定し、今回は2TBのNVMe Gen5 SSDを選定しました。
高速な読み書き性能により、I/Oのボトルネックを軽減し、処理の途切れを防ぐことで、安定した解析環境を実現します。
また、必要に応じて外付けドライブやHDDの増設も可能な構成となっており、柔軟なデータ保存・管理が可能です。なお、ストレージの増設をご自身で予定されている場合は、作業のしやすさを考慮した内部レイアウトで納品いたします。
パーツの変更や追加をご検討されている際は、事前にご相談いただけますと、より適切な構成でご提案・対応が可能です。GPUについて
近年では、深層学習を用いたバリアント解析やGPU対応のアセンブリツールの登場により、ゲノム解析におけるGPU活用の機会が増加しています。
ただし、マッピングやSNP解析などの工程はCPUベースで処理されるため、解析内容や用途に応じた構成選定が重要です。今回の構成ではGPUに依存しない解析が中心となるため、描画処理や基本的なグラフィック出力を目的として、NVIDIA RTX A400を選定しています。
GPUを積極的に活用する解析をご予定の場合は、より高性能なGPUの検討や、増設を見据えた構成設計もご相談いただけます。このような分野で活躍されている方へ
- 植物育種
- ゲノム解析
- バイオインフォマティクス
- 農業研究
- 分子生物学
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 9 285K 3.70GHz(8C/8T) + 3.20GHz(16C/16T) メモリ 合計128GB DDR5 6400 64GB x 2 ストレージ 2TB SSD M.2 NVMe Gen5 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board(2.5GBase-T x1) Wi-Fi,Bluetooth 筐体+電源 ミドルタワー型筐体+1000W 80PLUS PLATINUM OS Ubuntu 24.04 事例追加日:2025/9/22
- 事例No.PC-TW2M253153
-

CLC Genomics Workbench 対応 共用ワークステーション
用途:CLC Genomics Workbench参考価格:1262800円お客さまからのご相談内容
「CLC Genomics Workbench」を使用するにあたり、予算150万円で複数の研究者が共用できるPCを導入したい。
使用ソフトウェアは共通して「CLC Genomics Workbench」だが、使用する処理は研究者ごとに異なるため、幅広いゲノム解析に対応できる構成にしたい。テガラからのご提案
Qiagen社の「CLC Genomics Workbench」に対応した共用ワークステーションとして、研究室内での多人数利用や将来的な解析規模の拡大を見据えた設計をご提案しました。
メモリ・CPU・ストレージに余裕を持たせることで、他のバイオインフォマティクス系ツールの併用や処理負荷の高いタスクにも柔軟に対応可能です。CLCの推奨環境を満たす、余裕ある構成
CLC Genomics Workbench Premium の公式サイトでは、標準利用で16 GB以上、プラグイン使用時には64 GB以上のメモリが推奨されています。
これを踏まえて、将来的な処理規模の拡大や同時利用を想定し、128 GBのメモリを実装しました。
空きスロットも4つ確保しており、最大256 GBまでの増設が可能です。CPUには、22コア/44スレッドの Intel Xeon W7-2575X を搭載。 並列処理能力に優れ、大規模データを用いる計算処理にも適しています。
GPUについては、CLC自体がグラフィックス処理を行わないため、描画と安定動作を目的にNVIDIA RTX A400を選定しました。
十分な表示性能を維持しながら、全体のコストバランスを保っています。ストレージには、高速処理用の4 TB NVMe Gen4 SSDと長期保存向けの8 TB HDDを搭載し、解析データの展開と保管を効率的に行えるようにしています。
このような分野で活躍されている方へ
- バイオインフォマティクス
- ゲノム科学
- 分子生物学
- メタゲノム解析
- トランスクリプトーム解析
導入目的や今後の研究方針に応じて、カスタマイズやソフトウェア要件への対応も承っております。
まずはお気軽にご相談ください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W7-2575X 3.00GHz (TB3.0時 最大4.8GHz) 22C/44T メモリ 合計128GB DDR5 5600 REG ECC 32GB x 4 ストレージ1 4TB SSD M.2 NVMe Gen4 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x 4) ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 ミドルタワー型筐体+1000W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit キーワード
・CLC Genomics Workbenchとは
CLC Genomics Workbench は、次世代シーケンス (NGS) データを直感的な GUI 操作で解析できる、統合型バイオインフォマティクスソフトウェアです。
医学・基礎生物学・微生物学・メタゲノム・シングルセル解析など、幅広いバイオサイエンス領域で大学・企業の研究者に活用されています。 高度な解析アルゴリズムや視覚化ツールに加え、研究用途に応じてすぐに使えるワークフローや各種プラグインが豊富に用意されており、専門的な解析にも柔軟に対応可能です。参考:QIAGEN CLC Genomics Workbench | QIAGEN Digital Insights ※外部サイトに飛びます
事例追加日:2025/9/1
- 事例No.PC-24001117
-

遺伝子解析用・構造予測向けマシン
用途:RNA-seq解析、ゲノム解析、構造予測参考価格:2054800円お客さまからのご相談内容
RNA-seq解析や遺伝子発現解析、菌叢解析 (きんそうかいせき) などの用途で仮想環境を構築して使用しているが、現行のワークステーションではスペック不足を感じるため、より高性能な構成にしたい。
現行のマシンのスペックは下記の通り。
CPU:Intel Xeon E-2124G
RAM:16GB
ストレージ:3.64TB
GPU:NVIDIA Quadro P400仮想環境ではDockerやMinicondaを使用し、WSL2上のLinuxでRStudio Serverを運用予定。将来的にはAlphaFold3などの構造予測ツールの仕様も視野に入れている。
テガラからのご提案
ゲノム解析や構造予測に対応し、仮想環境上で複数のツールを運用できる、バイオインフォマティクス研究向けの高性能マシンです。
大規模演算を支えるパーツ構成
RNA-seq解析や菌叢解析など、多様な処理を並列に実行する研究においては、ハイスペックマシン環境の有無が解析効率に直結します。
本構成では、26コア52スレッドのIntel Xeon W7-2595Xを採用。
大規模な演算処理でも安定したパフォーマンスを発揮し、Dockerのコンテナ技術を活用した複雑な運用にも適しています。さらに、256GBのDDR5 ECCメモリを搭載することで、演算の遅延を抑えることが可能です。
複数の仮想環境を同時に立ち上げても速度が低下しにくく、快適な作業環境を維持できます。グラフィックスには、24GBのGPUメモリを搭載したNVIDIA RTX 4500 Adaを採用。
AlphaFold3などの構造予測ツールに適しており、中規模までの解析であれば、適切な設定を通して安定した処理が行えます。Linux環境でのGUI操作を想定し、OS構成はWSL2からデュアルブート構成へと変更しました。
これらの構成要素により、並列解析からGPUを用いた構造予測まで、安定的かつ効率的に運用できます。
このような分野で活躍されている方へ
- バイオインフォマティクス
- 分子生物学
- 遺伝学
- 構造生物学
- 計算生命科学
本仕様は、現在のご用途だけでなく、新たな研究ニーズにも対応できる、バランスが取れた設計です。
ご予算や利用されるソフトウェア、今後の運用方針に応じたカスタマイズにも柔軟に対応可能ですので、掲載内容以外の条件でもどうぞお気軽にご相談ください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W7-2595X 2.80GHz (TB3.0時 最大4.8GHz) 26C/52T メモリ 合計256GB DDR5 5600 REG ECC 64GB x 4 ストレージ1 2TB SSD S-ATA (RAIDなし) ストレージ2 2TB SSD S-ATA (RAIDなし) ストレージ3 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX 4500 Ada 24GB (DisplayPort x 4) ネットワーク on board (2.5GbE x 1 / 10GbE x 1) 筐体+電源 ミドルタワー型筐体 1600W 80PLUS TITANIUM OS Microsoft Windows 11 Pro for WS 64bit その他 (1) 2TB SSDへそれぞれデュアルブート設定 その他 (2) Ubuntu22.04 デュアルブート設定 キーワード
・QIIME2とは
QIIME2は微生物叢分析のためのオープンソースのソフトウェアパッケージ。
データと分析の透明性を重視しており、専用のwebサイト「QIIME2 View」から簡単に分析データを確認することができる。
プラグインによって定期的に新たな機能が追加されている。・AlphaFold3とは
AlphaFold3は、DeepLearningによるタンパク質や複合体の立体構造予測を行うプログラム。
AlphaFold2と比べ、より多様な生体分子の相互作用を高精度に予測でき、構造解析の可能性を広げている。
構造予測は、創薬研究や機能解明において重要な基盤となる。事例追加日:2025/6/16
- 事例No.PC-25000238
-

バイオインフォマティクス用ワークステーション
用途:Cell Rangerでのシングルセルデータ解析/Imarisでの顕微鏡画像解析参考価格:1950300円お客さまからのご相談内容
予算200万円程度で、Cell RangerとImarisを扱うためのワークステーションを導入したい。
スペック面で優先したいのはメモリ容量で、256GB以上でできるだけ多くの容量を確保したい。
OSはUbuntuとWindowsのデュアルブートを希望し、それぞれのOSを異なるストレージにインストールしたい。
CPUはXeonを希望するが、GPUはほとんど使わないため、最低限の能力で良い。その他として、USキーボードとディスプレイ、USBハブを希望する。
テガラからのご提案
Imarisは扱うデータ容量によって、おすすめスペックが異なる
Imarisは処理する画像データの容量に応じて、求められるスペックが異なります。
目安として、メモリ容量は画像データ容量の1.5倍以上が必要であり、処理画像が複雑な場合には、RTX2000 Ada以上のハイエンドなGPUを利用するのがおすすめです。Imarisのプリインストール出荷にも対応
本事例の構成にはImarisのライセンスやインストールは含まれませんが、ご希望の際にはお気軽にご相談ください。
新規でImarisライセンスを導入する場合には、オックスフォード・インストゥルメンツ社によるデモを行い、最適なライセンスを確認した上でお見積もりをご案内いたします。
ご希望の際には、以下の情報をお知らせください。・撮影したシステム名
・撮影内容
・計測したいもの

通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX4000 Ada 20GB (DisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1000W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit その他(1) Ubuntu24.04デュアルブート設定 その他(2) 27型4K液晶ディスプレイ、USBハブ、内蔵無線LAN キーワード
・Cell Rangerとは
Cell Rangerは10x Genomics社によるソフトウェアパイプラインの1種。シングルセルRNAシークエンスデータの処理、クラスタリング、遺伝子表現量の量化を行うことができる。 10x Genomics Chromeを使って生成されたシングルセルRNAシークエンスデータを処理したり、 遺伝子表現クラスタリングを行いシングルセルのサブポピュレーションを同定することが可能。その他、バーチャルリファレンスにマッピングし遺伝子を量化しての表現行列作成にも対応。・Imarisとは
IMARISは生物学や医学研究向けの高度な画像解析ソフト。2D、3D、4Dの顕微鏡画像の可視化と分析を提供する。直感的なワークフロー、AIによるオブジェクト検出、GPU加速デコンボリューションなどの特徴がある。
参考:Microscopy Image Analysis Software – Imaris – Oxford Instruments ※外部サイトに飛びます
事例追加日:2025/04/22
- 事例No.PC-25000221
-

CLC Genomics Workbench向けワークステーション (2025年3月版)
用途:RNA-seq、Whole-Genome Bisulfite Sequencing、ChIP-seqデータの解析参考価格:977900円お客さまからのご相談内容
RNA-seqやWhole-Genome Bisulfite Sequencing、ChIP-seqデータをCLC Genomics Workbenchで解析したい。ストレスなくスムーズな処理が実現できる構成を提案して欲しい。また、できれば同じマシンでシングルセル解析も行いたいと考えている。
事例No.PC-10012のような構成を予算100万円以内で実現できるか知りたい。参考:事例No.PC-10012 CLC Genomics Workbench向けマシン (Xeon Scalable仕様)
テガラからのご提案
ご連絡いただいた条件を元に、構成を検討しました。
事例No.PC-10012と同じ2CPU構成ではご予算を超えてしまうため、コストと処理性能のバランスを取ってXeon W5-2565X 18コアの1CPU構成としました。
メモリ容量は、ご予算内で搭載可能な容量である128GB(32GB×4)としています。
メモリスロットの空きが4つありますので、同じ32GBメモリモジュールを追加いただくことで合計256GBへの増設が可能です。
メモリ容量が重要かと存じますので、メモリ容量256GBが必須の場合にはCPUやストレージのスペックを調整した構成をご提案します。実際の計算に必要なメモリ容量と照らし合わせてご検討ください。ストレージにつきましては、事例に沿って2TB SSD M.2と8TB HDD S-ATAを選択しました。
ご要望に合わせて変更可能ですので、気兼ねなくご相談ください。










通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計128GB DDR5 5600 REG ECC 32GB x 4 ストレージ1 2TB SSD M.2 NVMe Gen4 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1000W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit ■キーワード
・CLC Genomics Workbenchとは
CLC Genomics Workbenchは、次世代シークエンサーから出力される膨大なデータを解析するための統合配列解析ソフトウェア。アセンブル、マッピング、変異検出などの機能を備え、ユーザーフレンドリーなインターフェースで操作することができる。さまざまなシーケンサーのデータに対応し、ゲノム、トランスクリプトーム、メタゲノムなど多様な解析が可能。
参考: QIAGEN CLC Genomics Workbench | QIAGEN Digital Insights ※外部サイトに飛びます
事例追加日:2025/03/17
- 事例No.PC-24001310
-

バイオインフォマティクス解析向けマシン
用途:Bowtie2、STAR、BWA、samtools、Juicer/juicebox、Rを用いたHi-Cデータ、scRNAseq、scATACseqなどの解析参考価格:963600円お客さまからのご相談内容
バイオインフォマティクス解析を行うLinuxのワークステーションの購入を考えている。主な用途はHi-Cデータ、scRNAseq、scATACseqなどのデータ解析。解析に使うソフトウェアは、Bowtie2、STAR、BWA、samtools、Juicer/juicebox、R (Seurat、Singac、etc…)を想定している。
下記のような条件を考えているが、予算内で実現可能か教えて欲しい。
CPU:指定なし (クロックは下げてもコア数の方が重視。コア数は20-36程度)
メモリ:128GB-256GB (メモリ容量を重視したい) 32GB x6枚の構成を考えている。
Storage:指定なし (2TB以上)
OS:Linux OS (Ubuntu24.04 or 22.04)
設置場所:居室
予算:100万円以内テガラからのご提案
ご予算の範囲内で構成を検討しました。
GPUの優先度は低いため、CPUやメモリを重視
ご連絡いただいたソフトウェアはいずれもGPU性能を必要としないため、ビデオカードには画面出力用としてRTX A400を採用しています。GPU計算を行う予定がある場合にはご連絡ください。
メモリ構成について
ご要望にあわせて32GB x6枚の構成としていますが、本構成のメモリチャネルに合わせて4の倍数でモジュールを搭載する構成がベストです。そのため、メモリ6枚のうち2枚は、4枚搭載時に発揮される本来の最高速度よりもわずかに遅くなりますので、予めご承知おきください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計192GB DDR5 5600 REG ECC 32GB x 6 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 + 1000W 80PLUS PLATINUM OS Ubuntu 24.04 ■キーワード
・Hi-Cとは
Hi-C(High-throughput Chromosome Conformation Capture)は、シーケンシングによりゲノムの三次元構造を解析するための革新的な技術。2009年に開発された手法で、細胞核内でのDNAの空間的配置を高解像度で明らかにすることができる。
・scRNAseqとは
シングルセルRNA-seq (scRNA-seq) は個々の細胞レベルで遺伝子発現を解析可能にする技術。細胞のトランスクリプトームマッピングを行うことで、細胞間の違いを明らかにする。同種の細胞でも個々に微細な違いがあるため、このような解析手法が必要とされる。活用としては、例えばがん細胞内の異質性の解明や細胞分化のプロセス解明などが期待される。また、少ない量のRNAからの解析が可能であり、細密な解析に利用されている。
・scATACseqとは
シングルセルATAC-seq (scATACseq)は、個々の細胞レベルでクロマチンアクセシビリティを網羅的に解析する技術。細胞集団内のエピジェネティックな多様性を詳細に調べることが可能。scATAC-seqは、scRNA-seqと組み合わせることで、より包括的な細胞状態の理解が可能になる。
・Bowtie2とは
Bowtie2は、シーケンスリードを参照配列にアライメントするためのツール。哺乳類のような比較的長いゲノムのアライメントに優れている。
・STARとは
STAR は RNA-Seqで得られたリード(生データ)をリファレンス配列にマッピングするプログラム。Github上で公開されており、要求されるスペックは高いものの、高速なマッピング速度を有している。
・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。
・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約) HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・Juicerとは
Hi-Cデータを解析するためのオープンソースツール。生の配列データから正規化されたコンタクトマップを作製したり、テラバイト規模のHi-Cデータセットを処理することができる。
・JuiceBoxとは
Juicerで生成された.hicファイルを視覚化するためのアプリケーション。生成されたHi-Cマップを直感的に閲覧し、解析することができる。
参考:GitHub – aidenlab/Juicebox: Visualization and analysis software for Hi-C data – ※外部サイトに飛びます
・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。 多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。
事例追加日:2025/01/14
- 事例No.PC-11781
-

バイオインフォマティクス向けワークステーション
用途:RNA-Seq解析・シングルセルRNA-Seq解析・メタゲノム解析・ショットガンメタゲノム解析などの解析参考価格:1824900円お客さまからのご相談内容
バイオインフォマティクス解析を行うためのワークステーションを予算200万円の範囲で検討したい。
現状では使用するソフトウェア等は全く定まっていない。そのため、RNA-Seq解析・シングルセルRNA-Seq解析・メタゲノム解析・ショットガンメタゲノム解析など、一通りの解析で利用できる構成を希望する。
また、導入後にパーツ増設や換装などのアップグレードを行う可能性がある。
そのため、CPUなど後々の増設や拡張が難しいパーツの性能を重視した構成を検討したい。テガラからのご提案
お客さまご希望の条件を踏まえた構成をご提案しました。
拡張性を考慮しつつ、アップグレードが難しいパーツであるCPUのスペックを重視した構成です。様々な解析手法で活躍できるCPU性能とメモリ容量
前述の通り、CPUのコスト配分を多めに割り当てたデュアルCPU構成です。
CPUは第4世代Xeon Scalableシリーズの32コアモデル Xeon Gold 6430 x2基を選択しています。
メモリ容量は32GBx8枚で256GB、ストレージはシステムディスクとして2TB SSD M.2 NVMe Gen4を搭載しています。
GPUはご予算とのバランスを考慮して、NVIDIA T400 4GB (ワークステーション向けビデオカードのエントリーモデル) を選択しています。
合計64のCPUコア数と256GB (増設時:最大512GB) のメモリ容量によって、様々な解析手法で幅広い活用が期待できる構成です。予算内で拡張性を重視した構成
導入後のパーツ増設やアップグレードを前提として、メモリ容量やビデオカードなどの拡張性を持たせています。
メモリ用の空きスロットは8スロット分あるため、32GBメモリモジュール x8枚を追加することで、合計512GBまで容量を拡張できます。
ストレージは、初期状態ではシステムディスクのみを搭載しており、データ保存用のHDD/SSDは搭載していませんが、こちらも増設が可能です。
その他、電源容量には余裕を持たせていますので、ビデオカードのアップグレードにも対応できます。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon Gold 6430 (2.10GHz 32コア) x2 メモリ 256GB REG ECC ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA T400 4GB ネットワーク on board (10GBase-T x2) 筐体+電源 タワー型筐体 + 1500W OS Ubuntu 22.04 事例追加日:2024/05/23
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
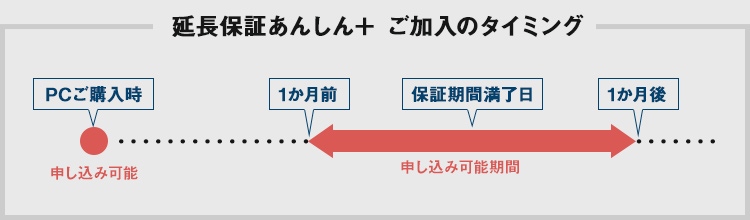
| 「あんしん+」 もしもの時の延長保証サービス |
|
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 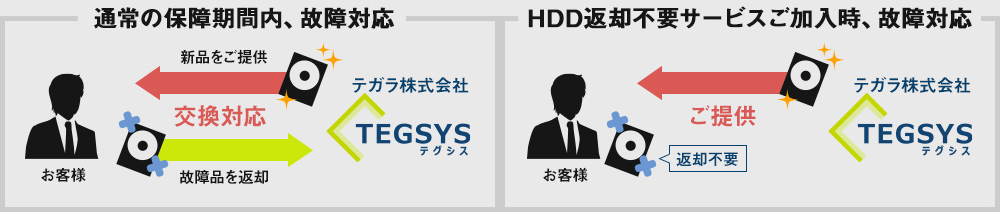
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。