- 事例No.PC-TS2J253952
-

大規模ゲノム解析向け2CPU・512GBメモリ搭載ワークステーション
用途:NGSゲノム解析、RNA-seq解析 (VCFtools、PLINK2、RFMIX2)参考価格:1794100円お客さまからのご相談内容
ゲノムデータを用いた集団遺伝学・ゲノム進化学解析に適したワークステーションを導入したい。
主な作業として、1万人規模の全ゲノムデータの解析 (VCF形式でRFMIX2やVCFtools、PLINK2などを利用)。
さらには、RNA-seq データのリファレンスゲノムへのマッピング・データ間比較解析を想定している。
CPU 32コア以上、メモリ256または512GB、4TB SSDを備えた構成を基準に、100〜150万円の範囲で、これらの要件に合う最適な構成を相談したい。テガラからのご提案
CPU構成について
PLINK2やVCFtoolsはマルチスレッド並列処理が中心のため、コア数の確保が処理時間に大きく影響します。
そこで、Intel Xeon 6517P (16コア) を2基搭載し、合計32コア環境を構築しました。併せて、2CPU構成とすることで、各CPUが8チャネルずつ、合計16チャネルのメモリ帯域を並列に利用可能です。
これにより、大規模データを扱うゲノム解析でも、安定した並列処理性能を発揮します。メモリ構成について
1万人規模の全ゲノムデータ (VCFファイル) を解析する場合、メモリ帯域と容量の確保が重要なポイントです。
本構成では、512GB (32GB×16枚) を搭載し、2CPU × 8チャネルの 最大帯域構成としました。
高スレッド処理時でも帯域飽和を抑え、CPU性能を十分に引き出せる設計となっています。ストレージとGPUについて
ストレージは4TBのM.2 NVMe Gen4 SSDを搭載し、VCF や BAM など大容量データの高速な読み書き性能を確保しました。
また、主要な解析ツールはCPU処理が主体であるため、高性能GPUは採用せず、画面表示用としてNVIDIA RTX A400 (4GB) を選択しています。このような分野で活躍されている方へ
- ゲノム科学
- 計算生物学
- バイオインフォマティクス
- 進化遺伝学
- RNA解析
テガラのオーダーメイド PC 製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。







通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon 6517P 3.20GHz(TB 4.20GHz) 16C/32T ×2基構成 メモリ 合計512GB DDR5 5600 REG ECC 32GB x 16 ストレージ 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (10GbE x2) 筐体+電源 タワー型筐体+1000W 80PLUS PLATINUM OS Ubuntu 24.04 保証 HDD返却不要サービス 1年 キーワード
VCFtoolsとは
VCFtoolsは、VCF形式のゲノム変異データを効率的に加工・抽出・統計解析できるコマンドラインツール群です。
大規模シーケンスデータの品質管理やフィルタリングに広く利用され、国際プロジェクトでも活用されています。PLINK2とは
PLINK2は、GWASや集団構造解析など全ゲノム規模の統計解析を実行できる総合解析ツールです。
医療ゲノム研究や創薬研究、バイオバンク解析などで世界的に利用されており、大規模データへの対応力と計算効率の高さが特長です。
VCFやBCF形式にも対応し、研究開発現場での実用性に優れています。RFMIX2とは
RFMIX2は、混合集団における局所祖先推定を高精度で行うための解析ソフトウェアです。
機械学習を活用し、染色体上の各領域の祖先起源を推定できるため、人類遺伝学や疾患関連解析で活用されています。
祖先情報を組み込んだ高度な解析を可能にする点が、大学や企業研究者から評価されています。事例追加日:2026/2/27
- 事例No.PC-TW3M252604
-

質量分析・RNA-Seq統合解析向けマシン
用途:質量解析、構造解析、多変量解析、統合解析、代謝マップ可視化参考価格:1788600円お客さまからのご相談内容
事例No.PC-11212を見ての問い合わせ。
100~150万円程度の予算で、質量分析データの解析に利用するワークステーションを検討している。Agilent社製の質量分析データ解析ソフト (Mass Hunter、Mass Profiler Professionalなど) を中心に、MS-DIAL、MS-Finder、SIMCAやマルチオミクス解析パッケージなども使用予定。
今後はRNA-Seqの解析データとの統合解析にも対応したい。
No.PC-11212をベースに、下記の構成を希望。OS:Windowsのみ
メモリ:128GB以上
CPU:予算内でコア数重視
ストレージ構成は事例通り
Wi-Fi機能も必要









通常24時間以内に担当者からご連絡いたします
テガラからのご提案
お客様が主に使用されるMass HunterおよびMass Profiler Professionalは、質量分析データの取得から多変量解析までを担う高機能な解析ソフトウェアです。
Mass Hunterでは16GB以上のメモリ、マルチスレッド対応CPU、1GbEまたは10GbEのネットワーク接続が必須とされています。参考:Agilent Technologies公式サイト
MHRequirements_EN上記の要件と「コア数重視」というご要望を踏まえ、本構成ではXeon W7-3565X 32コア64スレッドと256GBのメモリを搭載。十分な処理能力と将来的なメモリの拡張性を確保しました。
Wi-Fi対応機能や大容量ストレージも装備し、大学・企業研究室など多様な現場に適したシステムに仕上がっています。
大規模解析に適したパフォーマンス設計
質量分析やRNA-Seqのように、演算負荷が高く、大量のデータを扱う解析では、CPU性能とメモリ容量のバランスが重要です。
CPU性能が高ければ複雑な計算処理を短時間でこなせ、メモリ容量が十分であれば多数のデータを保持しながら並列処理も対応可能です。
※バイオインフォマティクスや機械学習などの大規模なデータを扱う分野では、メモリ容量に128GB〜256GB を選ぶケースが増えています。 (2025/6月現在)こうした理由から、32コアの高性能CPUと256GBメモリを搭載することで、大規模解析でも、安定性と作業効率の両方を実現しています。
SIMCAをはじめとする多変量解析ツールや、RNA-Seqデータとのオミクス統合解析など、解析ソフトごとに異なる計算負荷にも柔軟に対応できる設計となっています。
安定した動作環境により、日々の研究でも安心してご活用いただけます。このような分野で活躍されている方へ
- メタボローム解析
- トランスクリプトーム解析
- バイオマーカー探索
- 食品機能性評価
- 環境化学分析
本ワークステーションは、解析処理の高速化だけでなく、柔軟性や安定性にも配慮して設計されています。
重点を置きたいパーツや今後の運用方針に応じたカスタマイズにも柔軟に対応しております。掲載内容に含まれないご要望につきましても、どうぞ遠慮なくご相談ください。主な仕様
CPU Intel Xeon W7-3565X 2.50GHz (TB3.0時 最大4.8GHz) 32C/64T メモリ 合計256GB DDR5 5600 REG ECC 32GB x 8 ストレージ1 2TB SSD M.2 NVMe Gen4 (RAIDなし) ストレージ2 2TB SSD M.2 NVMe Gen4 (RAIDなし) ストレージ3 16TB HDD S-ATA ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x 4) ネットワーク on board (1GbE x 1 / 10GbE x 1) 筐体+電源 ミドルタワー型筐体 1000W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit その他(1) TPMモジュール その他(2) 内蔵無線LAN / BT キーワード
【Phase 1:データ取得・前処理】
・Mass Hunterとは
Agilent社が提供する質量分析データの取得・解析ソフトで、LC/MSやGC/MSの定性・定量処理を行う。
・MS-DIALとは
LC-MS、GC-MSなどのデータを取り込み、ピーク検出、ノイズ除去、定量解析を行う。
Agilentに限らず多様なフォーマットに対応。【Phase 2:構造解析】
・MS-Finderとは
MS-DIALで抽出されたピークリストやスペクトル情報をもとに、MS/MSスペクトルから化合物構造を推定するための無料の構造解析ソフト。
データベース照合やフラグメント解析も対応。【Phase 3:多変量解析・統計処理】
・Mass Profiler Professionalとは
Mass Hunterで処理した定量データをもとに、バイオマーカー探索やグループ間比較などの統計解析を実施。
・SIMCAとは
MS-DIALや他ソフトから得られた定量データを用い、PCA、PLSなどによる視覚的な多変量解析を実行する。
装置・メーカーに依存せず幅広く使用可能。【Phase 4:統合解析・可視化】
・マルチオミクス解析パッケージとは
質量分析データとRNA-Seqなど他のオミクス情報を統合し、代謝経路やネットワークとして可視化。
多様な解析結果を組み合わせた全体像の把握が可能な解析ツール群。事例追加日:2025/6/18
- 事例No.PC-25000268
-

次世代シーケンス (NGS) データ解析用ワークステーション
用途:ゲノムアセンブリ、多型解析 (Hifiasm、BWA-MEM2、GATK、Braker3、YaHSなど) 、RNA-seq解析 (HISAT2, STAR, RSEMなど) (※Helixerを使用する場合、GPUの交換が必要です)参考価格:1490500円お客さまからのご相談内容
事例No.PC-12218を見ての問い合わせ。
予算100万円から150万円で、ゲノムアセンブリ、NGSデータ解析を含めた多型解析やRNA-seq解析に使用可能なマシンの購入を検討している。
将来に向けて、メモリの拡張性などを確保したい。テガラからのご提案
事例No.PC-12218をベースにして、構成を検討しました。
拡張性のあるメモリ構成
CPUは2025年5月時点の最新モデル「Xeon W7-3545 24コア」をご予算に合わせて採用しました。
メモリは合計256GB (32GB×8枚) を搭載しています。
空きスロットが8つありますので、同じ32GBメモリモジュールを8枚追加いただくことで「合計512GB」へ増設が可能です。
GPUは、画面描画用として「NVIDIA T400 4GB」の後継機種「RTX A400 4GB」を選択しました。(ご参考)
VRAMの容量を重視するソフトウェア (Helixerなど) をご利用の場合は、GPUメモリを優先した構成をご提案可能です。
Helixerは、GPUに11 GB以上のVRAMが要求されております。
Helixerの公式GitHubは こちら (※外部ページに飛びます)本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
お客様のご要望に応じて柔軟にお見積もりをご提案しております。
掲載内容とは異なるご用途やご予算の場合でも、どうぞお気軽にご相談ください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W7-3545 2.70GHz (TB3.0時 最大4.8GHz) 24C/48T メモリ 合計256GB DDR5 5600 REG ECC 32GB x8 ストレージ1 4TB SSD M.2 NVMe Gen4 ストレージ2 16TB HDD S-ATA ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 タワー型筐体 1000W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・多型解析 (Polymorphism Analysis) とは
生物個体間のDNA配列の違い (多型) を検出・解析する手法。 個体差の遺伝的要因を探るほか、系統関係や進化過程の推定に活用される。・Helixerとは
Helixerは、深層学習 (Deep Learning) と隠れマルコフモデル (HMM) を組み合わせた、真核生物ゲノムの構造的アノテーション (遺伝子構造の予測) を行うオープンソースのツール。
GPUを活用することで、高速な処理が可能。・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。
・GATKとは
GATK (Genome Analysis Toolkit) は、次世代シーケンサーから出力された塩基配列データからバリアントの解析 (遺伝子の変異解析) を行うための解析ツール群。内包するツールは、個別に使用することも連携させて使用することもできる。
事例追加日:2025/05/15
- 事例No.PC-25000238
-

バイオインフォマティクス用ワークステーション
用途:Cell Rangerでのシングルセルデータ解析/Imarisでの顕微鏡画像解析参考価格:1950300円お客さまからのご相談内容
予算200万円程度で、Cell RangerとImarisを扱うためのワークステーションを導入したい。
スペック面で優先したいのはメモリ容量で、256GB以上でできるだけ多くの容量を確保したい。
OSはUbuntuとWindowsのデュアルブートを希望し、それぞれのOSを異なるストレージにインストールしたい。
CPUはXeonを希望するが、GPUはほとんど使わないため、最低限の能力で良い。その他として、USキーボードとディスプレイ、USBハブを希望する。
テガラからのご提案
Imarisは扱うデータ容量によって、おすすめスペックが異なる
Imarisは処理する画像データの容量に応じて、求められるスペックが異なります。
目安として、メモリ容量は画像データ容量の1.5倍以上が必要であり、処理画像が複雑な場合には、RTX2000 Ada以上のハイエンドなGPUを利用するのがおすすめです。Imarisのプリインストール出荷にも対応
本事例の構成にはImarisのライセンスやインストールは含まれませんが、ご希望の際にはお気軽にご相談ください。
新規でImarisライセンスを導入する場合には、オックスフォード・インストゥルメンツ社によるデモを行い、最適なライセンスを確認した上でお見積もりをご案内いたします。
ご希望の際には、以下の情報をお知らせください。・撮影したシステム名
・撮影内容
・計測したいもの

通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX4000 Ada 20GB (DisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1000W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit その他(1) Ubuntu24.04デュアルブート設定 その他(2) 27型4K液晶ディスプレイ、USBハブ、内蔵無線LAN キーワード
・Cell Rangerとは
Cell Rangerは10x Genomics社によるソフトウェアパイプラインの1種。シングルセルRNAシークエンスデータの処理、クラスタリング、遺伝子表現量の量化を行うことができる。 10x Genomics Chromeを使って生成されたシングルセルRNAシークエンスデータを処理したり、 遺伝子表現クラスタリングを行いシングルセルのサブポピュレーションを同定することが可能。その他、バーチャルリファレンスにマッピングし遺伝子を量化しての表現行列作成にも対応。・Imarisとは
IMARISは生物学や医学研究向けの高度な画像解析ソフト。2D、3D、4Dの顕微鏡画像の可視化と分析を提供する。直感的なワークフロー、AIによるオブジェクト検出、GPU加速デコンボリューションなどの特徴がある。
参考:Microscopy Image Analysis Software – Imaris – Oxford Instruments ※外部サイトに飛びます
事例追加日:2025/04/22
- 事例No.PC-25000221
-

CLC Genomics Workbench向けワークステーション (2025年3月版)
用途:RNA-seq、Whole-Genome Bisulfite Sequencing、ChIP-seqデータの解析参考価格:977900円お客さまからのご相談内容
RNA-seqやWhole-Genome Bisulfite Sequencing、ChIP-seqデータをCLC Genomics Workbenchで解析したい。ストレスなくスムーズな処理が実現できる構成を提案して欲しい。また、できれば同じマシンでシングルセル解析も行いたいと考えている。
事例No.PC-10012のような構成を予算100万円以内で実現できるか知りたい。参考:事例No.PC-10012 CLC Genomics Workbench向けマシン (Xeon Scalable仕様)
テガラからのご提案
ご連絡いただいた条件を元に、構成を検討しました。
事例No.PC-10012と同じ2CPU構成ではご予算を超えてしまうため、コストと処理性能のバランスを取ってXeon W5-2565X 18コアの1CPU構成としました。
メモリ容量は、ご予算内で搭載可能な容量である128GB(32GB×4)としています。
メモリスロットの空きが4つありますので、同じ32GBメモリモジュールを追加いただくことで合計256GBへの増設が可能です。
メモリ容量が重要かと存じますので、メモリ容量256GBが必須の場合にはCPUやストレージのスペックを調整した構成をご提案します。実際の計算に必要なメモリ容量と照らし合わせてご検討ください。ストレージにつきましては、事例に沿って2TB SSD M.2と8TB HDD S-ATAを選択しました。
ご要望に合わせて変更可能ですので、気兼ねなくご相談ください。










通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計128GB DDR5 5600 REG ECC 32GB x 4 ストレージ1 2TB SSD M.2 NVMe Gen4 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1000W 80PLUS PLATINUM OS Microsoft Windows 11 Professional 64bit ■キーワード
・CLC Genomics Workbenchとは
CLC Genomics Workbenchは、次世代シークエンサーから出力される膨大なデータを解析するための統合配列解析ソフトウェア。アセンブル、マッピング、変異検出などの機能を備え、ユーザーフレンドリーなインターフェースで操作することができる。さまざまなシーケンサーのデータに対応し、ゲノム、トランスクリプトーム、メタゲノムなど多様な解析が可能。
参考: QIAGEN CLC Genomics Workbench | QIAGEN Digital Insights ※外部サイトに飛びます
事例追加日:2025/03/17
- 事例No.PC-24001310
-

バイオインフォマティクス解析向けマシン
用途:Bowtie2、STAR、BWA、samtools、Juicer/juicebox、Rを用いたHi-Cデータ、scRNAseq、scATACseqなどの解析参考価格:963600円お客さまからのご相談内容
バイオインフォマティクス解析を行うLinuxのワークステーションの購入を考えている。主な用途はHi-Cデータ、scRNAseq、scATACseqなどのデータ解析。解析に使うソフトウェアは、Bowtie2、STAR、BWA、samtools、Juicer/juicebox、R (Seurat、Singac、etc…)を想定している。
下記のような条件を考えているが、予算内で実現可能か教えて欲しい。
CPU:指定なし (クロックは下げてもコア数の方が重視。コア数は20-36程度)
メモリ:128GB-256GB (メモリ容量を重視したい) 32GB x6枚の構成を考えている。
Storage:指定なし (2TB以上)
OS:Linux OS (Ubuntu24.04 or 22.04)
設置場所:居室
予算:100万円以内テガラからのご提案
ご予算の範囲内で構成を検討しました。
GPUの優先度は低いため、CPUやメモリを重視
ご連絡いただいたソフトウェアはいずれもGPU性能を必要としないため、ビデオカードには画面出力用としてRTX A400を採用しています。GPU計算を行う予定がある場合にはご連絡ください。
メモリ構成について
ご要望にあわせて32GB x6枚の構成としていますが、本構成のメモリチャネルに合わせて4の倍数でモジュールを搭載する構成がベストです。そのため、メモリ6枚のうち2枚は、4枚搭載時に発揮される本来の最高速度よりもわずかに遅くなりますので、予めご承知おきください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計192GB DDR5 5600 REG ECC 32GB x 6 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 + 1000W 80PLUS PLATINUM OS Ubuntu 24.04 ■キーワード
・Hi-Cとは
Hi-C(High-throughput Chromosome Conformation Capture)は、シーケンシングによりゲノムの三次元構造を解析するための革新的な技術。2009年に開発された手法で、細胞核内でのDNAの空間的配置を高解像度で明らかにすることができる。
・scRNAseqとは
シングルセルRNA-seq (scRNA-seq) は個々の細胞レベルで遺伝子発現を解析可能にする技術。細胞のトランスクリプトームマッピングを行うことで、細胞間の違いを明らかにする。同種の細胞でも個々に微細な違いがあるため、このような解析手法が必要とされる。活用としては、例えばがん細胞内の異質性の解明や細胞分化のプロセス解明などが期待される。また、少ない量のRNAからの解析が可能であり、細密な解析に利用されている。
・scATACseqとは
シングルセルATAC-seq (scATACseq)は、個々の細胞レベルでクロマチンアクセシビリティを網羅的に解析する技術。細胞集団内のエピジェネティックな多様性を詳細に調べることが可能。scATAC-seqは、scRNA-seqと組み合わせることで、より包括的な細胞状態の理解が可能になる。
・Bowtie2とは
Bowtie2は、シーケンスリードを参照配列にアライメントするためのツール。哺乳類のような比較的長いゲノムのアライメントに優れている。
・STARとは
STAR は RNA-Seqで得られたリード(生データ)をリファレンス配列にマッピングするプログラム。Github上で公開されており、要求されるスペックは高いものの、高速なマッピング速度を有している。
・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。
・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約) HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・Juicerとは
Hi-Cデータを解析するためのオープンソースツール。生の配列データから正規化されたコンタクトマップを作製したり、テラバイト規模のHi-Cデータセットを処理することができる。
・JuiceBoxとは
Juicerで生成された.hicファイルを視覚化するためのアプリケーション。生成されたHi-Cマップを直感的に閲覧し、解析することができる。
参考:GitHub – aidenlab/Juicebox: Visualization and analysis software for Hi-C data – ※外部サイトに飛びます
・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。 多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。
事例追加日:2025/01/14
- 事例No.PC-12159
-

RTX6000 Ada ×2 搭載マシン
用途:NVIDIA Parabricksの利用参考価格:5867400円お客さまからのご相談内容
NVIDIA Parabricksを使用するためのGPUマシンを導入したい。
GPUの候補は、NVIDIA RTX 6000 Ada 48GB GDDR6 x2枚を考えている。また、CPUはGPU性能を最大限に引き出せるスペックのものを希望する。メモリは1.0TB以上を必要としている。
ストレージは、以下の3つ全ての搭載を考えている。
・ストレージ1 : SSD (4TB 以上 read/write 6,000MB/s以上の高速なもの)
・ストレージ2 : SSD (4TB 以上 read/write 6,000MB/s以上の高速なもの)
・ストレージ3 : HDD (20 TB 以上)電源は、100V環境で利用できることが条件になる。OSはUbuntu 22.04 LTSをプリインストールしたい。筐体サイズは、ラックマウントも可能なタワー型を希望する。予算は600万円以内で抑えたい。
前述の通り、使用する主なソフトウェアはNVIDIA Parabricksであり、これが問題なく動作することが前提となる。
その他の要望として、筐体を縦置きで使うためのフットスタンドとラックマウントする際に使うスライドレールも見積もりに含めて欲しい。
テガラからのご提案
スペック
本構成では、GPUを2枚搭載し、高速なモデルのCPU (AMD EPYC 9554) を使用しています。
電源ユニットは容量1600W (100V環境で約1200-1300W程度) の製品を採用しており、100V環境での利用が可能です。また、ラックマウントレールキットと、縦置きのタワー筐体として利用する場合のフットスタンドもご提案に含めています。
SSDは、ご指定の速度を満たすようにGen4対応のM.2スロットにGen4 NVMeを搭載しています。
サーバーラック本体
サーバーラック本体の取り扱いやお見積もりも可能ですので、ご希望の際にはお気軽にお申し付けください。
ソフトウェアのセットアップ
本お見積もりに含まれるセットアップ内容は、OSのインストールのみです。
用途に応じて必要なソフトウェアのインストールや運用に関する周辺機器の手配も可能ですので、お気軽にご相談ください。また、据置や設置などの現地作業も承っています。お見積もりをご希望の際、基本内容(開梱、ケーブリング、起動確認)以外に必要な作業がございましたら、こちらもお気軽にご相談いただけますと幸いです。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD EPYC 9554 3.10GHz 64C/128T メモリ 合計 1152GB DDR5 4800 REG ECC 96GB × 12 ストレージ1 4TB SSD M.2 NVMe Gen4 ストレージ2 4TB SSD M.2 NVMe Gen4 ストレージ3 20TB HDD S-ATA ビデオ NVIDIA RTX6000 Ada 48GB (DisplayPort x4)× 2 ネットワーク on board (10GBase-T x2) 筐体+電源 4Uラックマウント筐体 + 1600W OS Ubuntu 22.04 その他 縦置き用フットスタンド
ラックマウントスライドレール■キーワード
・NVIDIA Parabricksとは
NVIDIA Parabricksは、ゲノム解析を高速化するためのGPU加速ツール群。特にDNAやRNAの解析において最大108倍の速度向上を実現する。CPUのみを使用した場合に比べて低い計算コストでの処理が可能で、30倍のヒトゲノム解析が約10分で完了したデータがある。病院や研究機関などの現場でのデータ解析で広く利用されている。
事例追加日:2024/10/21
- 事例No.PC-11781
-

バイオインフォマティクス向けワークステーション
用途:RNA-Seq解析・シングルセルRNA-Seq解析・メタゲノム解析・ショットガンメタゲノム解析などの解析参考価格:1824900円お客さまからのご相談内容
バイオインフォマティクス解析を行うためのワークステーションを予算200万円の範囲で検討したい。
現状では使用するソフトウェア等は全く定まっていない。そのため、RNA-Seq解析・シングルセルRNA-Seq解析・メタゲノム解析・ショットガンメタゲノム解析など、一通りの解析で利用できる構成を希望する。
また、導入後にパーツ増設や換装などのアップグレードを行う可能性がある。
そのため、CPUなど後々の増設や拡張が難しいパーツの性能を重視した構成を検討したい。テガラからのご提案
お客さまご希望の条件を踏まえた構成をご提案しました。
拡張性を考慮しつつ、アップグレードが難しいパーツであるCPUのスペックを重視した構成です。様々な解析手法で活躍できるCPU性能とメモリ容量
前述の通り、CPUのコスト配分を多めに割り当てたデュアルCPU構成です。
CPUは第4世代Xeon Scalableシリーズの32コアモデル Xeon Gold 6430 x2基を選択しています。
メモリ容量は32GBx8枚で256GB、ストレージはシステムディスクとして2TB SSD M.2 NVMe Gen4を搭載しています。
GPUはご予算とのバランスを考慮して、NVIDIA T400 4GB (ワークステーション向けビデオカードのエントリーモデル) を選択しています。
合計64のCPUコア数と256GB (増設時:最大512GB) のメモリ容量によって、様々な解析手法で幅広い活用が期待できる構成です。予算内で拡張性を重視した構成
導入後のパーツ増設やアップグレードを前提として、メモリ容量やビデオカードなどの拡張性を持たせています。
メモリ用の空きスロットは8スロット分あるため、32GBメモリモジュール x8枚を追加することで、合計512GBまで容量を拡張できます。
ストレージは、初期状態ではシステムディスクのみを搭載しており、データ保存用のHDD/SSDは搭載していませんが、こちらも増設が可能です。
その他、電源容量には余裕を持たせていますので、ビデオカードのアップグレードにも対応できます。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon Gold 6430 (2.10GHz 32コア) x2 メモリ 256GB REG ECC ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA T400 4GB ネットワーク on board (10GBase-T x2) 筐体+電源 タワー型筐体 + 1500W OS Ubuntu 22.04 事例追加日:2024/05/23
- 事例No.PC-11793
-

Cell Ranger・QuPath用ワークステーション
用途:Cell Rangerなどを用いたシングルセルRNA解析、QuPathなどを用いた空間遺伝子解析参考価格:1029600円お客さまからのご相談内容
バイオインフォマティクス用ワークステーションを、予算100万円程度で購入したい。
現在はシングルセルRNA解析などのゲノム解析をメインで行っており、今後は高画質の病理画像を併用した空間遺伝子解析も行う予定がある。マシンのスペックは、CPUのコア数とメモリ容量を重視したい。
使用するソフトウェアはCell RangerやQuPathなどを想定しており、OSはLinuxを希望する。
また、Linuxの利用には慣れていないため、可能であればCell RangerとQuPathをインストールした状態で出荷して欲しい。テガラからのご提案
予算内でCPUコア数・メモリ容量を重視した構成
ご予算の範囲内でCPUのコア数・メモリ容量を重視した構成をご提案しました。
CPUは2024年5月時点で最新のAMD Ryzen Threadripper 7000 シリーズの24コアモデルを搭載しています。
メモリは64GBモジュール x4枚で合計256GBです。
24コアのCPUと256GBのメモリ容量により、解析時の高いパフォーマンスが期待できます。なお、現時点ではCell RangerとQuPathのGPUアクセラレートへの対応は限定的なため、GPUアクセラレートを使用しない場合は、エントリークラスのビデオカードでも動作に支障はないと考えられます。そのため、ご予算を重視し、GPUアクセラレートの使用は考慮せず、エントリークラスのワークステーション向けビデオカード NVIDIA T400 4GBを選定しています。
注意点として、本マシンの電源容量は現在の構成用に選定されているため、将来的なGPU増設などの機器追加・アップグレードが考慮されていません。
GPUの増設など消費電力の大きい機器を増設する予定がある場合は、構成の変更も可能ですのでお気軽にご相談ください。Cell Ranger・QuPathの事前インストールサービス
お客様のご希望にあわせて、Cell Ranger・QuPathを事前インストールした状態で出荷いたします。
なお、QuPathはLinuxでも動作しますが、いくつかの問題が報告されています。
詳細は下記公式マニュアルをご参照ください。また、ご希望の場合はCell RangerをLinuxに、QuPathをWindowsにインストールしたデュアルブート構成とすることも可能です。
その他のソフトウェアにつきましても、事前インストールをご希望の際には気兼ねなくお申し付けください。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen Threadripper 7960X (4.20GHz 24コア) メモリ 256GB REG ECC ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA T400 4GB ネットワーク on board(2.5GbE x1 10GBase-T x1) Wi-Fi x1 筐体+電源 タワー型筐体 + 1000W OS Ubuntu 22.04 その他 Cell Ranger、 QuPathインストール ■キーワード
・Cell Rangerとは
Cell Rangerは10x Genomics社によるソフトウェアパイプラインの1種。シングルセルRNAシークエンスデータの処理、クラスタリング、遺伝子表現量の量化を行うことができる。 10x Genomics Chromeを使って生成されたシングルセルRNAシークエンスデータを処理したり、 遺伝子表現クラスタリングを行いシングルセルのサブポピュレーションを同定することが可能。その他、バーチャルリファレンスにマッピングし遺伝子を量化しての表現行列作成にも対応。・QuPathとは
QuPathは、生体画像解析のためのオープンソースソフトウェア。豊富な解析機能を備えており、スライド画像全体を総合的に可視化し、分析することができる。
事例追加日:2024/05/14
- 事例No.PC-11752
-

NVIDIA Geforce RTX4070 Super搭載 ナノポアシーケンサー解析用マシン
用途:次世代シーケンサーによる16S rRNA解析およびRNA-seq解析参考価格:806300円お客さまからのご相談内容
次世代シーケンサー (MinION Mk1B) による16S rRNA解析およびRNA-seq解析用のワークステーションの導入を検討している。予算80万円程度で最適な構成を提案してほしい。
OS環境はWSL2 (Windows Subsystem for Linux2) でUbuntuを使用する想定だが、計算パフォーマンスが向上するようであればデュアルブート構成の採用も考えている。
WSL2/デュアルブートで計算を行うことがパフォーマンスに影響するかを教えてほしい。また、メモリ容量は64GB程度、ストレージ容量は2TB以上を想定している。
テガラからのご提案
MinION Mk1Bのシステム要件はメーカー公式サイトで公開されてます。
そのため、ご予算の範囲内で推奨要件を満たす構成をご提案しました。
新製品のNVIDIA Geforce RTX4070 Superを搭載
MinION Mk1Bでの計算上重要となるビデオカードは、2024/1/17に発売された新製品のNVIDIA Geforce RTX4070 Superとしています。
7,168基のCUDAコア、56基のRTコア、および224基のTensorコアを搭載し、ご予算内に収まるビデオカードの中では高いコストパフォーマンスが期待できます。
デュアルブート構成とその利点について
LinuxディストリビューションはMinION Mk1Bが対応しているUbuntu 20.04を選択し、Windows 11とのデュアルブート構成です。
なお、2024年1月現在、MinION Mk1BのWindowsサポートはいまだWindows 10で止まっているため、MinION Mk1BはUbuntu 20.04上での利用を前提としています。また、WSL2はWindows上で動作する仮想マシンです。
通常のLinux環境とWSL2を比較した場合、仮想化されているWSL2の方が処理が行われるまでに経由するプロセスが多くなります。
そのため、Linux上で負荷の高い処理を行う場合は、デュアルブート構成としてLinuxをハードウェア上で直接動作させるほうが、パフォーマンスの面で優位です。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2445 (3.10GHz 10コア) メモリ 64GB REG ECC ストレージ1 2TB SSD S-ATA ストレージ2 2TB SSD S-ATA ビデオ NVIDIA Geforce RTX4070 Super 12GB ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 ミドルタワー型筐体 + 850W OS Microsoft Windows 11 Professional 64bit + Ubuntu 20.04 (デュアルブート構成) ■キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・16S rRNA解析とは
16S rRNA解析は、細菌の16S リボソームRNAの配列を用いて菌種の存在や割合を網羅的に推測する解析。16S rRNAは配列の保存性が高く、進化速度が遅いことから菌種の同定に有用である。この16S rRNAの配列を解析することで、菌種・菌群を培養の必要なしに検出・同定することができる。
・WSL2とは
Windows Subsystem for Linux 2 (WSL2) はWindows上でLinux向けバイナリを実行する方法の一つ。参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【1/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【2/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【3/3】事例追加日:2024/02/05
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
| 「あんしん+」 もしもの時の延長保証サービス |
|
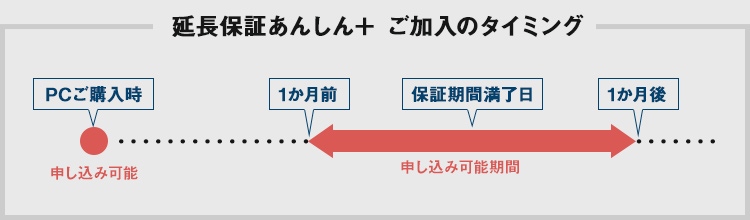
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 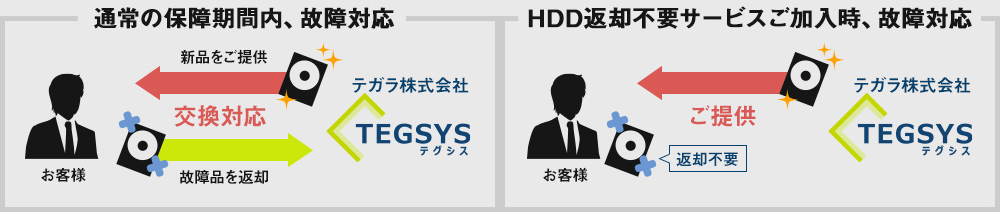
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。