- 事例No.PC-TE1J254011
-

シーケンスデータ解析/機械学習用ワークステーション (システム要件に最適化)
用途:エピジェネティクス解析、de novoアセンブリ、RNA-Seq解析、メタゲノム解析、機械学習参考価格:3261500円お客さまからのご相談内容
事例No. PC-25000268を見ての問い合わせ。ナノポアのシーケンスデータ解析と機械学習の双方に対応するワークステーションを導入したい。
エピジェネティクス解析やde novoアセンブリ、RNA-Seq解析、メタゲノム解析などを想定している。
使用するソフトウェアは、以下の通り。- 汎用解析・ML基盤:Samtools、XGBoost、LightGBM
- ゲノムアセンブリ・評価:SPAdes・BUSCO・Prodigal・FastANI・GTDB-Tk
- ナノポアベースコール:Guppy・Dorado・Remora・DeepMod2
OSはUbuntuで、予算は400万円程度を希望する。設置作業も含めた見積もりが欲しい。
通常24時間以内に担当者からご連絡いたします
テガラからのご提案
ツール要件を重視した大容量メモリ構成
本構成は「システム要件を基準に最適化した構成」としてご案内したスペックです。特に大規模アセンブリや多数サンプルのバッチ処理を想定し、CPUコア数とメモリ容量を優先。EPYC 9554 (64コア) と768GBメモリにより、メモリ負荷の大きい解析に強みを持たせています。
事例No. PC-25000268をグレードアップしつつ、機械学習にも対応できる汎用性を重視した構成は、事例No.PC- TW3J253928をご覧ください。
CPUについて
AMD EPYC 9554は64コア構成で高い並列処理性能を備え、大量のサンプルを並行処理するワークロードに適しています。CPUリソースを多く要求するゲノム解析ツールや、複数ジョブを同時実行する環境で効率を発揮します。
メモリ容量について
ご利用予定のソフトウェアには、推奨メモリ容量が256GB~512GB付近のツールが複数存在します。そのため、解析規模や将来のデータ拡張を踏まえ、余裕を持った768GBを搭載しました。長時間ジョブの安定性向上にも寄与します。
GPUの選定について
本構成では、研究用途における機械学習処理への対応を目的に NVIDIA RTX 6000 Ada (Max-Q 96GB) を搭載しています。
深層学習フレームワークとの高い親和性を持ち、モデル学習や推論処理において高い実用性を発揮します。Doradoについては、GPUアクセラレーションを利用する際に倍精度演算を前提としたハイエンドGPUが例示されています。
そこで今回は、Doradoの高精度GPU要件をそのまま満たす構成ではなく、機械学習を中心に幅広い研究用途へ柔軟に対応できる現実的かつ効果的な選択肢として、RTXシリーズを採用した構成としました。RTXシリーズは深層学習フレームワークとの相性もよく、多様な研究タスクに対応しやすい点が特長です。今後の拡張やワークフローの進化にも柔軟に応えられる構成となっています。
参考情報:Benchmarking the Oxford Nanopore Technologies basecallers on AWS
ストレージと運用性
高速アクセスが必要なワークフローに合わせ、4TB NVMe Gen5 SSD を2基搭載し、高速な一時データ処理に対応しています。
また、24TB HDD を併用することで、シーケンスデータの長期保管や再解析にも適したストレージ構成としました。
さらに、現地での設置作業 (開梱・設定・起動確認) も含めて対応し、導入後すぐに研究へ着手いただけるよう配慮しています。運用要件に寄り添った最適化
納期や予算条件を満たしつつ、求められた要件に最も合致するスペックとして構成しました。多様なツールを運用する研究環境で、安定した解析パイプラインを維持しやすい点が特長です。
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD EPYC 9554 3.1GHz 64C/128T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ1 4TB SSD M.2 NVMe Gen5 x 2 ストレージ2 24TB HDD S-ATA ビデオ NVIDIA RTX PRO6000 Max-Q 96GB ネットワーク on board (10GBase-T x2) 筐体+電源 ミドルタワー 1500W 80PLUS PLATINUM OS Ubuntu 24.04 その他 現地設置作業(開梱・設置・ケーブリング・起動確認) キーワード
・Samtoolsとは
Samtoolsは、次世代シーケンス (NGS) データの処理・解析に広く用いられる定番ツール群。BAMやCRAMなどのアライメントデータのソート、インデックス作成、フィルタリング、可視化などの高速処理が可能で、ゲノム解析ワークフローの基盤として広く利用されている。・XGBoostとは
XGBoostは、勾配ブースティング決定木 (GBDT) アルゴリズムを高速かつ高精度に実装した機械学習フレームワーク。分類・回帰・ランキングなど多用途で、ゲノム解析、疾患リスク予測、遺伝子発現解析などバイオインフォマティクス分野でも広く利用される。https://xgboost.ai/参考:XGBoost Official Site
・LightGBMとは
LightGBMは、Microsoftが開発した高速でメモリ効率の高い勾配ブースティングフレームワーク。大規模データの解析に適しており、SNP解析、メチル化データの分類、疾患予測モデルなどにも利用される。・SPAdesとは
SPAdesは、微生物ゲノムアセンブリに広く利用されるde novoアセンブラー。Illumina・Nanopore・PacBioなど複数プラットフォームを統合したハイブリッドアセンブリに対応し、高品質なコンティグ構築が可能。・BUSCOとは
BUSCOは、ゲノムアセンブリの完全性 (completeness) を評価するための代表的ツール。保存性の高いシングルコピー遺伝子セットを用い、アセンブリ品質の客観的評価が可能。・Prodigalとは
Prodigalは、微生物ゲノムに特化した遺伝子予測ツール。プロカリア遺伝子領域の高精度抽出が可能で、メタゲノム解析でも高い性能を発揮する。事例追加日:2026/2/12
- 事例No.PC-TW3J253928
-

シーケンスデータ解析/機械学習用ワークステーション (汎用構成)
用途:エピジェネティクス解析、de novoアセンブリ、RNA-Seq解析、メタゲノム解析、機械学習参考価格:3169100円お客さまからのご相談内容
事例No. PC-25000268を見ての問い合わせ。ナノポアのシーケンスデータ解析と機械学習の双方に対応するワークステーションを導入したい。
エピジェネティクス解析やde novoアセンブリ、RNA-Seq解析、メタゲノム解析などを想定している。
使用するソフトウェアは、以下の通り。- 汎用解析・ML基盤:Samtools、XGBoost、LightGBM
- ゲノムアセンブリ・評価:SPAdes・BUSCO・Prodigal・FastANI・GTDB-Tk
- ナノポアベースコール:Guppy・Dorado・Remora・DeepMod2
OSはUbuntuで、予算は350万円程前後を希望する。
通常24時間以内に担当者からご連絡いたします
テガラからのご提案
機械学習を見据えたバランス強化構成
本構成は「事例No. PC-25000268をグレードアップしつつ、機械学習にも対応できる汎用性」を重視した案としてご案内しました。Xeon W プロセッサと512GBメモリを組み合わせ、シーケンス解析に必要なスループットと、機械学習処理に必要な演算性能の両立を図っています。
システム要件を基準に最適化した構成は、事例No.PC- TE1J254011をご覧ください。
CPUについて
Intel Xeon W7-3565X (32コア) は高クロックで単一タスク性能に優れ、ツールによって負荷特性が分かれるゲノム解析と機械学習処理の双方に適した選択です。計算処理の一部がCPU性能に依存するソフトウェア環境に向いています。
GPUの選定について
本構成では、機械学習の活用を見据え、GPUを搭載しています。
シーケンス解析のワークフローではCPU主導の処理が多い一方、機械学習を取り入れる研究ではGPUの存在が大きな効果を発揮するため、研究の幅を広げる観点からもGPU追加を採用しました。Doradoについては、GPUアクセラレーションを利用する際に倍精度演算を前提としたハイエンドGPUが例示されています。
そこで今回は、Doradoの高精度GPU要件をそのまま満たす構成ではなく、機械学習を中心に幅広い研究用途へ柔軟に対応できる現実的かつ効果的な選択肢として、RTXシリーズを採用した構成としました。RTXシリーズは深層学習フレームワークとの相性もよく、多様な研究タスクに対応しやすい点が特長です。今後の拡張やワークフローの進化にも柔軟に応えられる構成となっています。
参考情報:Benchmarking the Oxford Nanopore Technologies basecallers on AWS
拡張性について
大型のミドルタワー筐体を採用することで、将来的なストレージ増設やGPUの追加にも柔軟に対応できます。研究用途の変化に合わせて活用範囲を広げやすい点が特長です。
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W7-3565X 2.50GHz (TB3.0時 最大4.8GHz) 32C/64T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ1 4TB SSD M.2 NVMe Gen5 ストレージ2 24TB HDD S-ATA ビデオ NVIDIA RTX PRO5000 48GB ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・Samtoolsとは
Samtoolsは、次世代シーケンス (NGS) データの処理・解析に広く用いられる定番ツール群。BAMやCRAMなどのアライメントデータのソート、インデックス作成、フィルタリング、可視化などの高速処理が可能で、ゲノム解析ワークフローの基盤として広く利用されている。・XGBoostとは
XGBoostは、勾配ブースティング決定木 (GBDT) アルゴリズムを高速かつ高精度に実装した機械学習フレームワーク。分類・回帰・ランキングなど多用途で、ゲノム解析、疾患リスク予測、遺伝子発現解析などバイオインフォマティクス分野でも広く利用される。https://xgboost.ai/参考:XGBoost Official Site
・LightGBMとは
LightGBMは、Microsoftが開発した高速でメモリ効率の高い勾配ブースティングフレームワーク。大規模データの解析に適しており、SNP解析、メチル化データの分類、疾患予測モデルなどにも利用される。・SPAdesとは
SPAdesは、微生物ゲノムアセンブリに広く利用されるde novoアセンブラー。Illumina・Nanopore・PacBioなど複数プラットフォームを統合したハイブリッドアセンブリに対応し、高品質なコンティグ構築が可能。・BUSCOとは
BUSCOは、ゲノムアセンブリの完全性 (completeness) を評価するための代表的ツール。保存性の高いシングルコピー遺伝子セットを用い、アセンブリ品質の客観的評価が可能。・Prodigalとは
Prodigalは、微生物ゲノムに特化した遺伝子予測ツール。プロカリア遺伝子領域の高精度抽出が可能で、メタゲノム解析でも高い性能を発揮する。事例追加日:2026/2/12
- 事例No.PC-TUKS254357
-

Nanopore MinION Mk1D対応省スペースワークステーション
用途:Oxford Nanopore MinION Mk1D、シーケンス解析参考価格:416900円お客さまからのご相談内容
Oxford Nanopore MinION Mk1D の推奨要件を満たすスペックで、卓上設置が可能なPCを導入したい。予算は47万円以内。
OSはUbuntu 24.04 LTS、メモリ32GB、ストレージ2TB SSD、CPUはIntel i7 (12コア以上) を条件とする。
GPUはNVIDIA RTX 5090か、ラップトップ向けGPUを希望するが、難しい場合は最小要件でも可。
拡張性よりも省スペース性を重視したい。テガラからのご提案
GPUの選定と予算調整
推奨要件を満たす構成を検討しました。
RTX 5090を採用する場合は、ご予算の47万円を大幅に上回ります。
そのため、今回のご提案ではOxford Nanopore MinION Mk1D の最小要件を満たすGeForce RTX 5060Ti (16GB) を選定しています。
CPUはIntel Core Ultra 7 (8+12コア) 、メモリ32GB、ストレージ2TB SSDを搭載。性能と予算のバランスを実現した構成です。コンパクト筐体の採用
省スペース性を重視した「Define7 Compact」を採用しています。
サイズは幅210mm×高さ474mm×奥行427mmで、限られたスペースでも快適に運用可能です。一方で、筐体サイズおよびエアフロー設計の制約から、発熱量が大きい高消費電力のGPUや、カードサイズの大きいGPUの搭載は推奨していません。
高いGPU性能を重視される場合は、十分なエアフローを確保できる、より大型筐体の採用が前提となります。このような分野で活躍されている方へ
- ゲノム解析
- 分子生物学
- 臨床検査
- バイオインフォマティクス
- 医療情報学
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 7 265K 3.90GHz(8C/8T)+3.30GHz(12C/12T) メモリ 合計32GB DDR5 6400 16GB x 2 ストレージ1 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5060Ti 16GB ネットワーク 2.5Gbx1,Wi-Fi 7 筐体+電源 ミドルタワー型筐体+850W Cybenetics Gold OS Ubuntu 24.04 キーワード
MinION Mk1Dとは
MinION Mk1Dは、Oxford Nanopore Technologies社が提供するポータブルなDNA/RNAシーケンサー。
リアルタイムで長鎖リードの取得が可能で、ゲノム解析、メタゲノム解析、トランスクリプトーム解析など幅広い分野に対応。USB接続で動作し、フィールドワークやラボでの迅速な遺伝子解析に最適。ナノポア技術により、従来のシーケンサーでは困難だった構造変異やエピジェネティクス解析にも対応可能。事例追加日:2025/12/15
- 事例No.PC-TUKS254328
-

MinION Mk1D用ワークステーション
用途:ナノポアシーケンシング解析 (MinION Mk1D)参考価格:982300円お客さまからのご相談内容
Oxford Nanopore Technologies社のMinION Mk1Dによるナノポアシーケンシング解析を予定している。
具体的な解析内容は未定だが、まずは予算申請用として見積もりを取得したい。テガラからのご提案
MinION Mk1Dに最適化した構成
MinION Mk1Dの公式要件に準拠し、USB Type-C接続やUbuntu 24.04対応など、シーケンシング環境に必要な条件を満たす構成としました。
Thunderbolt4やUSB 10Gbpsなどの高速I/Oに対応し、外部デバイスとの接続性も確保しています。
MinKNOWによるリアルタイム制御やデータストリーミングにも対応できるよう、CPU・メモリ・ストレージを強化しました。参考:MinION Mk1D IT requirements | Oxford Nanopore Technologies
CPUとメモリについて
CPUには20コア構成のIntel Core Ultra 7 265Kを採用しており、解析処理やデータ転送などの高負荷な作業にも十分対応できます。
メモリは64GBを搭載。MinKNOWの推奨要件である32GBを上回るメモリ容量を確保することで、解析処理の安定性を確保しています。GPUの選定について
NVIDIA GeForce RTX 5090 (32GB) を搭載し、将来的な機械学習やベースコーリング処理にも対応可能な、高性能GPUを選定しました。
このような分野で活躍されている方へ
- バイオインフォマティクス
- 医学
- 生物学
- ゲノム解析
- 次世代シーケンサー解析
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Core Ultra 7 265K 3.90GHz (8C/8T) +3.30GHz (12C/12T) メモリ 合計64GB DDR5 6400 32GB x 2 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5090 32GB ネットワーク 2.5Gbx1,Wi-Fi 7 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・MinION Mk1Dとは
MinION Mk1Dは、Oxford Nanopore Technologies社が提供するポータブルなDNA/RNAシーケンサー。リアルタイムで長鎖リードの取得が可能で、ゲノム解析、メタゲノム解析、トランスクリプトーム解析など幅広い分野に対応。USB接続で動作し、フィールドワークやラボでの迅速な遺伝子解析に最適。ナノポア技術により、従来のシーケンサーでは困難だった構造変異やエピジェネティクス解析にも対応可能。・MinKNOWとは
MinKNOWは、Oxford Nanopore Technologies社のDNA/RNAシーケンサーを制御・解析するための公式ソフトウェア。
サンプルのロードからリアルタイムのデータ取得、品質評価、基本的な解析までを一括して行えるため、生命科学や微生物学、がん研究など幅広い分野の大学や企業の研究者に活用されている。シーケンスの進行状況をリアルタイムで可視化しながら実験条件を柔軟に調整できる点が大きな特徴。事例追加日:2025/10/24
- 事例No.PC-11752
-

NVIDIA Geforce RTX4070 Super搭載 ナノポアシーケンサー解析用マシン
用途:次世代シーケンサーによる16S rRNA解析およびRNA-seq解析参考価格:806300円お客さまからのご相談内容
次世代シーケンサー (MinION Mk1B) による16S rRNA解析およびRNA-seq解析用のワークステーションの導入を検討している。予算80万円程度で最適な構成を提案してほしい。
OS環境はWSL2 (Windows Subsystem for Linux2) でUbuntuを使用する想定だが、計算パフォーマンスが向上するようであればデュアルブート構成の採用も考えている。
WSL2/デュアルブートで計算を行うことがパフォーマンスに影響するかを教えてほしい。また、メモリ容量は64GB程度、ストレージ容量は2TB以上を想定している。
テガラからのご提案
MinION Mk1Bのシステム要件はメーカー公式サイトで公開されてます。
そのため、ご予算の範囲内で推奨要件を満たす構成をご提案しました。
新製品のNVIDIA Geforce RTX4070 Superを搭載
MinION Mk1Bでの計算上重要となるビデオカードは、2024/1/17に発売された新製品のNVIDIA Geforce RTX4070 Superとしています。
7,168基のCUDAコア、56基のRTコア、および224基のTensorコアを搭載し、ご予算内に収まるビデオカードの中では高いコストパフォーマンスが期待できます。
デュアルブート構成とその利点について
LinuxディストリビューションはMinION Mk1Bが対応しているUbuntu 20.04を選択し、Windows 11とのデュアルブート構成です。
なお、2024年1月現在、MinION Mk1BのWindowsサポートはいまだWindows 10で止まっているため、MinION Mk1BはUbuntu 20.04上での利用を前提としています。また、WSL2はWindows上で動作する仮想マシンです。
通常のLinux環境とWSL2を比較した場合、仮想化されているWSL2の方が処理が行われるまでに経由するプロセスが多くなります。
そのため、Linux上で負荷の高い処理を行う場合は、デュアルブート構成としてLinuxをハードウェア上で直接動作させるほうが、パフォーマンスの面で優位です。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2445 (3.10GHz 10コア) メモリ 64GB REG ECC ストレージ1 2TB SSD S-ATA ストレージ2 2TB SSD S-ATA ビデオ NVIDIA Geforce RTX4070 Super 12GB ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 ミドルタワー型筐体 + 850W OS Microsoft Windows 11 Professional 64bit + Ubuntu 20.04 (デュアルブート構成) ■キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・16S rRNA解析とは
16S rRNA解析は、細菌の16S リボソームRNAの配列を用いて菌種の存在や割合を網羅的に推測する解析。16S rRNAは配列の保存性が高く、進化速度が遅いことから菌種の同定に有用である。この16S rRNAの配列を解析することで、菌種・菌群を培養の必要なしに検出・同定することができる。
・WSL2とは
Windows Subsystem for Linux 2 (WSL2) はWindows上でLinux向けバイナリを実行する方法の一つ。参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【1/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【2/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【3/3】事例追加日:2024/02/05
- 事例No.PC-11005
-

ナノポアシーケンサー解析用マシン (2023年05月版)
用途:Guppy、Dorado、DeepVariantを利用した遺伝子解析参考価格:1476200円お客さまからのご相談内容
事例No.PC-10347Bを見ての問い合わせ。
ナノポアシーケンサー解析の他、DeepLearningを用いたソフトウェア「DeepVariant」も使いたい。
以下のような構成を想定しているので、見積もりを提案して欲しい。・CPU:AMD Threadripper
・メモリ:128GB
・ストレージ;SSD (NVMeは必須ではない)
・GPU:RTX4090
・使用するソフトウェア:Guppy、Dorado、DeepVariantテガラからのご提案
CPUにThreadripperを採用した構成にてお見積もりしました。
ご提案のタイミングでは、従来のThreadripperシリーズが終息していましたので、Threadripper Proを搭載した構成としています。
CPUのコストは大きくなりますが、CPU性能が高くオールラウンドにお使いいただけます。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。








通常24時間以内に担当者からご連絡いたします
検索キーワード
医用画像DeepLearning,TensorFlow,Keras,Pytorch,CUDA Toolkit,ディープラーニングマシン,NVIDIA Geforce RTX4080,機械学習ソフトウェア,インストールなしOS,GPUメモリ容量ナノポアシーケンサー解析,Guppy,Dorado,DeepVariant,AMD Threadripper,バイオインフォマティクス,医学,生物学,デスクトップワークステーション,RNAシークエンスデータ主な仕様
CPU AMD Ryzen ThreadripperPRO 5965WX (3.80GHz 24コア) メモリ 128GB REG ECC ストレージ 2TB SSD M.2 ビデオ NVIDIA Geforce RTX4090 ネットワーク on board (1GbE x1 10GBase-T x1) 筐体+電源 タワー型筐体 + 1200W OS Ubuntu 20.04 キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。・Doradoとは
Doradoはナノポアシーケンシングで生成されたRNAシークエンスデータのアセンブルとアノテーションを行うために使用される遺伝子解析ソフトウェア。本事例公開時点ではα版でのリリースであり、完全版ではない。
RNAシークエンスデータを用いて高品質な塩基配列のアセンブルを行い、正確な転写産物の同定とアノテーションを行うことができ、ナノポアシーケンシングにおける問題である短いリード長と高いエラー率への最適化が行われている。・DeepVariantとは
DeepVariantはDeepLearningを活用して高品質なゲノム変異検出を行うゲノム解析ソフトウェア。ゲノム解析のために畳み込みニューラルネットワークを使用して,DNAの塩基の変異を検出する。
オープンソースで提供されており,ゲノム研究や医療分野,遺伝カウンセリングなど様々な分野で活用されている。事例追加日:2023/05/26
- 事例No.PC-10816
-

NGS解析&ナノポアシーケンサー解析用マシン
用途:MaSuRCAやGuppyを用いたハイブリッドアセンブリ、RNA-seq解析参考価格:520410円お客さまからのご相談内容
簡易的なNGS解析とナノポアシーケンサー解析を行う計画があり、そのためのPCを導入したい。
具体的にはMaSuRCAを利用した30Mb程度のハイブリッドアセンブリやRNA-seq解析を想定している。GPU版Guppy basecallerにも使うことができるのが理想で、それ以外に3Dモデル処理などの実施は考えていない。
OSはUbuntuを考えているが、WSLでUbuntuを使っても解析能力に大きな影響がなければ、Windows上で動かしたい。
その他に想定している内容は以下の通り。・CPU:12コア程度の製品を想定しているが、より良い提案があれば希望する
・ストレージ:SSDを希望する
・予算:50万円程度
・MaSuRCAのダウンロードページでは、ハードウェア要件として 「Bacteria (up to 10Mb): 16GB RAM, 8+ cores, 10GB disk space」の記載があるため、30MbであればPC-10596程度のスペックで動作するのではないかと考えているテガラからのご提案
ご要望の条件に合わせて構成を検討しました。
仕様は暫定ですが、MaSuRCAの公式リポジトリに掲載された動作要件のBacteriaとInsectの中間程度のスペックです。
OSはUbuntuのみをインストールする想定です。
Windows Subsystem for Linux 2 (WSL2)でのUbuntu利用
WSLでの利用に関しては、ソフトウェア自体は動作すると思われますが、解析能力への影響は避けられません。
WSLは基本的に仮想マシンですので、仮想化によるオーバーヘッドが生じます。Windowsを用意しなければならない理由が他にないようであれば、Ubuntuをネイティブに動作させる形での利用を推奨します。
その他の選択肢として、WindowsとUbuntuのデュアルブート環境を構築する方法があります。ご希望のお客様はご相談ください。また、本構成ではNVIDIA製ビデオカードを搭載しており、GuppyのGPU実行に対応しています。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7950X (4.50GHz 16コア) メモリ 64GB ストレージ 2TB SSD S-ATA ビデオ NVIDIA Geforce RTX3060 ネットワーク on board (2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー筐体 + 850W OS Ubuntu 20.04 キーワード
・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。・MaSuRCAとは
MaSuRCAは、高品質なペアエンド読み込みと長いリードのハイブリッドアセンブリに特化したゲノムアセンブリのためのソフトウェア。異なる読み込みタイプのデータを組み合わせてア、高速で正確なアセンブリを生成できる。・ハイブリッドアセンブリとは
ハイブリッドアセンブリとは、異なる読み込みタイプのデータを組み合わせて行うゲノムアセンブリの手法。短いペアエンド読み込みと長いリードの両方を使用することで、アセンブリの精度と連続性を向上させることができる。・WSL2とは
Windows Subsystem for Linux 2 (WSL2) はWindows上でLinux向けバイナリを実行する方法の一つ。参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【1/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【2/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【3/3】
事例追加日:2023/03/23
- 事例No.PC-10347B
-

ナノポアシーケンサー解析用マシン (GPU性能優先)
用途:Nanoporeシーケンス (ロングリードシーケンス) 解析、MinKNOW、Guppyなどの利用参考価格:921800円お客さまからのご相談内容
ナノポアシーケンサーによる長鎖のDNA解析を行うためのマシンを導入したい。
想定している条件は以下の通り。・CPU:2CPU構成が望ましい
・メモリ:64GB程度
・ストレージ:2TB以上のSSD データ保存領域にはNASを利用する
・GPU:NVIDIA RTX2060以上 予算内で最も性能の高いGPUを希望
・OS:Ubuntuインストール予定 (OSなしでの出荷を希望)
・予算:90万円程度テガラからのご提案
構成検討においては、CPUとGPUに関する条件がポイントとなります。
ご予算を加味して検討すると、両方の条件を同時に満たすことが難しいため、本事例ではGPUスペックを優先したご提案としています。
2CPU構成を優先した構成は、事例No.PC-10347Aをご覧ください。RTX4090の物理的なサイズと排熱には注意が必要
GPUのRTX4090は、世代差と製品グレードの両面からRTX2060を上回る性能を有しています。
ただし、GPUの物理的なサイズや排熱との兼ね合いから、将来的なGPU増設には対応していませんので、予めご承知おきください。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。




通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Silver 4314 (2.40GHz 16コア) メモリ 64GB REG ECC ストレージ 2TB SSD M.2 ビデオ NVIDIA Geforce RTX4090 ネットワーク on board (1000Base-T x2) 筐体+電源 ミドルタワー筐体 + 1200W OS なし キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・MinKNOWとは
ナノポアシーケンサー「MinION」でシーケンスを行うための専用ソフト。
MinION自体はUSBで直接PCにつなげるタイプのシーケンサーで、ある程度のマシンスペックが要求される。参考:Laboratory and IT Requirements (Oxford Nanopore Technologies) ※外部サイトへ飛びます
・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。事例追加日:2023/01/31
- 事例No.PC-10347A
-

ナノポアシーケンサー解析用マシン (2CPU仕様)
用途:Nanoporeシーケンス (ロングリードシーケンス) 解析、MinKNOW、Guppyなどの利用参考価格:932800円お客さまからのご相談内容
ナノポアシーケンサーによる長鎖のDNA解析を行うためのマシンを導入したい。
想定している条件は以下の通り。・CPU:2CPU構成が望ましい
・メモリ:64GB程度
・ストレージ:2TB以上のSSD データ保存領域にはNASを利用する
・GPU:NVIDIA RTX2060以上 予算内で最も性能の高いGPUを希望
・OS:Ubuntuインストール予定 (OSなしでの出荷を希望)
・予算:90万円程度テガラからのご提案
構成検討においては、CPUとGPUに関する条件がポイントとなります。
ご予算を加味して検討すると、両方の条件を同時に満たすことが難しいため、本事例では2CPU構成を優先したご提案としています。
GPUの性能を重視した構成は、事例No.PC-10347Bをご覧ください。2CPU構成のメリットは、1CPU構成と比較してコア数が多く並列処理性能が高い点と、メモリを最大で2TBまで搭載できる点です。
GPUのRTX A4000は、RTX2060と同程度のクラスですが、ビデオメモリ容量やCUDAコア数など全体的に優位性の高い製品です。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。




通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Silver 4310 (2.10GHz 12コア) x2 メモリ 64GB REG ECC ストレージ 2TB SSD M.2 ビデオ NVIDIA RTX A4000 ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 1200W OS なし キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・MinKNOWとは
ナノポアシーケンサー「MinION」でシーケンスを行うための専用ソフト。
MinION自体はUSBで直接PCにつなげるタイプのシーケンサーで、ある程度のマシンスペックが要求される。参考:Laboratory and IT Requirements (Oxford Nanopore Technologies) ※外部サイトへ飛びます
・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。事例追加日:2023/01/31
- 事例No.PC-4975
-

DNA解析装置向けのマシン
用途:DNA解析参考価格:223300円お客さまからのご相談内容
DNA解析装置 (Nanopore製)を動かすマシンを検討している。予算20~30万円以内でXeonを搭載し、バランスの取れた構成を提案してほしい。OSはUbuntu14.04を指定。
テガラからのご提案
CPUがXeonとのご指定がございましたので、30万に収まるよう構成を調整いたしました。 ビデオ出力は特にご指定がございませんでしたのでオンボードビデオとしております。アナログ出力はございませんのでご注意ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon E3-1245v5 (3.5GHz 4コア) メモリ 16GB ECC ストレージ 1TB SSD ネットワーク GigabitLAN x2 ビデオカード on board 筐体+電源 ミニタワー筐体 (180x363x370 mm フロントパネルを除く)+400W OS Ubuntu 14.04 事例追加日:2017/7/12
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
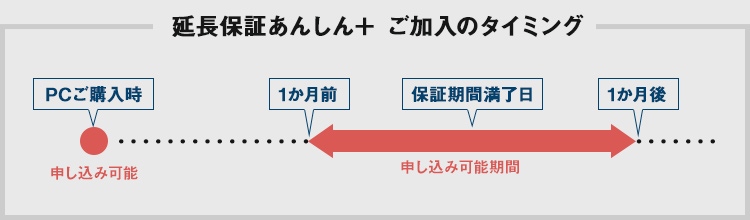
| 「あんしん+」 もしもの時の延長保証サービス |
|
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 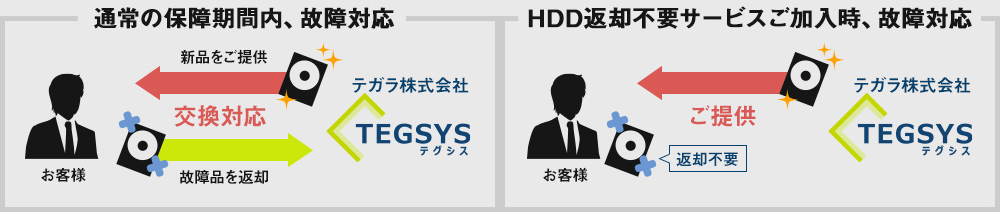
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。