- 事例No.PC-11089
-

シングルセルRNA-seq解析用マシン (2023年07月版)
用途:Cell Rangerの利用参考価格:600600円お客さまからのご相談内容
シングルセルRNA-seq用にPCを導入したい。
現在はMacを利用しており、DockerでLinux環境を作りCell Rangerを起動しているが、処理にとても時間がかかっている。
Linuxマシンで、60万円程度の構成を提案して欲しい。スペックの条件としては、メモリ128GB以上を希望する。
テガラからのご提案
Linuxマシンをご希望でしたので、ご予算内でのUbuntuマシンをご提案しました。メモリは128GBで、用途面での必要性を想定し、SSD+大容量HDDを搭載した構成としています。
Cell Ranger側の推奨スペックは、CPU 16コア+メモリ128GBです。 本構成のメモリ容量は仕様上最大ですので、より多くのメモリが必要となる可能性がある場合にはご相談ください。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Core i9-13900KS (3.20GHz 8コア + 2.40GHz 16コア) メモリ 128GB ストレージ1 2TB SSD M.2 ストレージ2 16TB HDD S-ATA ビデオ NVIDIA T400 4GB MiniDisplayPort x3 ネットワーク on board (2.5GBase-T x1) Wi-Fi x1 筐体+電源 タワー型筐体 + 850W OS Ubuntu 22.04 キーワード
・シングルセルRNA-seqとは
シングルセルRNA-seqは個々の細胞レベルで遺伝子発現を解析可能にする技術。細胞のトランスクリプトームマッピングを行うことで、細胞間の違いを明らかにする。同種の細胞でも個々に微細な違いがあるため、このような解析手法が必要とされる。活用としては、例えばがん細胞内の異質性の解明や細胞分化のプロセス解明などが期待される。また、少ない量のRNAからの解析が可能であり、細密な解析に利用されている。・Cell Rangerとは
Cell Rangerは10x Genomics社によるソフトウェアパイプラインの1種。シングルセルRNAシークエンスデータの処理、クラスタリング、遺伝子表現量の量化を行うことができる。 10x Genomics Chromeを使って生成されたシングルセルRNAシークエンスデータを処理したり、 遺伝子表現クラスタリングを行いシングルセルのサブポピュレーションを同定することが可能。その他、バーチャルリファレンスにマッピングし遺伝子を量化しての表現行列作成にも対応。事例追加日:2023/07/14
- 事例No.PC-11011
-

レセプトデータ解析用マシン
用途:VigiBase、NaviCat for SQLite、R等の利用参考価格:358600円お客さまからのご相談内容
レセプトデータベースを活用した研究を行っている。
現在、M1チップを搭載したメモリ16GBのMacbook Airを使っているが、解析に時間がかかるため予算40万円程度で専用PCを導入したい。使用するソフトはVigiBase、NaviCat for SQLite、R、JADER、Microsoft Access、EZRを予定。
長期的にはRNA-seqのカウントデータを用いた二次解析を行いたいと考えており、可能なら強度が軽めのドッキングシミュレーションにも対応できるようにアップグレードが可能な構成とすることが理想。なお、ストレージは外付けSSDを利用する予定。OSはコスト優先でWindows 11 Homeで良い。
テガラからのご提案
ご要望に合わせて構成を検討しました。
データ保存用のストレージは外付けSSDの利用を想定していますが、本体側のストレージにはメモリのオーバーフローやRなどの中間ファイルを一時的に書き込む可能性があります。そのため、システム用SSDとして速度の速いタイプの製品を選定しています。このような前提から、PC本体のストレージにデータを置くことは想定しておらず、空き容量が減ると速度が下がってしまうのでご注意ください。
マシン全体としては、ご予算内で計算用のCPUを優先しています。
ご利用予定のソフトウェアにGPUアクセラレートを利用するものはありませんので、GPUは搭載せず画面出力はオンボード機能の利用としています。予算40万円の範囲でGPUを搭載しようとすると、全体的に中途半端なスペックとなります。また、GPUは後日の追加が可能な拡張カードですので、必要になったタイミングでご検討いただく想定です。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。


通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Core i7-13700K (3.40GHz 8コア + 2.50GHz 8コア) メモリ 64GB ストレージ 1TB SSD M.2 ビデオ on board (DPx1 HDMIx1) ネットワーク on board (2.5GBase-T x1) Wi-Fi x1 筐体+電源 ミドルタワー筐体 + 850W OS Microsoft Windows 11 Home 64bit キーワード
・VigiBaseとは
VigiBaseは世界保健機関の国際薬物監視プログラムであり、医薬品の副作用情報を収集・分析するためのデータベース。医薬品の安全性に関する情報の調査や副作用のパターン傾向を分析することができる。・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。
多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。・Navicat for SQLiteとは
Navicat for SQLiteは、SQLiteデータベースの開発、管理、操作を支援するためのソフトウェア。SQLiteは軽量な関係データベース管理システム (RDBMS) であり、様々なアプリケーションやプロジェクトで使用されている。Navicat for SQLiteは、このデータベースを直感的なインターフェースで簡単に操作できるようにするために設計されている。・JADERとは
JADER (Japanese Adverse Drug Event Report database) は、日本での医薬品の副作用報告データベース。医薬品医療機器総合機構 (PMDA) が管理しており、医薬品の安全性監視と副作用情報の収集・分析を目的としている。事例追加日:2023/06/02
- 事例No.PC-10999
-

シングルセルRNA-seq解析用マシン (2023年05月版)
用途:PythonやRを利用したRNA-seq解析参考価格:698500円お客さまからのご相談内容
Windows Subsystem for Linuxを使用して、PythonやRを用いたシングルセルRNA-seq解析を実施したい。
FastQCデータからQC (Quality Control)、マッピング、定量、データ解析まで実施する予定。
現状のマシンでは、処理の実施から完了までに24時間程度かかっているため、処理時間を短縮したい。
RのParallelパッケージは使用していないので、クロック数を重視する構成が望ましい。テガラからのご提案
ご要望に合わせて構成を検討しました。
コア数よりもクロック数を重視した構成が望ましいとのことから、Core i9-13900KSを用いた構成としております。Core i9-13900KSは発熱が大きいため、本構成のCPUクーラーは通常よりも大きいサイズに換装しています。
もし、RのParallelパッケージを使用している場合や、同時に走らせる計算数を増やしたい場合には、AMDのCPU(ThreadripperPRO)を用いた構成も選択肢に入ります。その場合は、計算数や規模に合わせたメモリ容量の設定も合わせてご検討ください。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Core i9-13900KS (3.20GHz 8コア + 2.40GHz 16コア) メモリ 128GB ストレージ1 4TB SSD M.2 ストレージ2 16TB HDD S-ATA ビデオ NVIDIA T400 4GB MiniDisplayPort x3 ネットワーク on board (2.5GBase-T x1) Wi-Fi x1 筐体+電源 ミドルタワー筐体 + 850W OS Microsoft Windows 11 Professional 64bit キーワード
・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。
多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。・WSL2とは
Windows Subsystem for Linux 2 (WSL2) はWindows上でLinux向けバイナリを実行する方法の一つ。参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【1/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【2/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【3/3】
・FastQCとは
FastQCは次世代シーケンサー (NGS)のデータ解析に使われるツールの1つであり、シークエンスデータの品質チェックに利用される。NGSプラットフォームから得られるファイルの品質を評価し、品質が低い箇所や異常のある箇所を検出して報告することができる。・Pythonとは
Pythonは、Python Software Foundation (PSF) が著作権を保持する、オブジェクト指向プログラミング言語。プログラミングの構文がシンプルなため可読性が高く、目的に応じたライブラリやフレームワークといったコンポーネントが豊富に揃っていることも特徴。プログラミングの初学者から上級者に至るまで人気の言語。参考:【特集記事】プログラミング言語 Python その人気の理由は?- Python プログラミングを加速するツールたち ※弊社オウンドメディア「TEGAKARI」に飛びます
事例追加日:2023/05/26
- 事例No.PC-11005
-

ナノポアシーケンサー解析用マシン (2023年05月版)
用途:Guppy、Dorado、DeepVariantを利用した遺伝子解析参考価格:1476200円お客さまからのご相談内容
事例No.PC-10347Bを見ての問い合わせ。
ナノポアシーケンサー解析の他、DeepLearningを用いたソフトウェア「DeepVariant」も使いたい。
以下のような構成を想定しているので、見積もりを提案して欲しい。・CPU:AMD Threadripper
・メモリ:128GB
・ストレージ;SSD (NVMeは必須ではない)
・GPU:RTX4090
・使用するソフトウェア:Guppy、Dorado、DeepVariantテガラからのご提案
CPUにThreadripperを採用した構成にてお見積もりしました。
ご提案のタイミングでは、従来のThreadripperシリーズが終息していましたので、Threadripper Proを搭載した構成としています。
CPUのコストは大きくなりますが、CPU性能が高くオールラウンドにお使いいただけます。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。








通常24時間以内に担当者からご連絡いたします
検索キーワード
医用画像DeepLearning,TensorFlow,Keras,Pytorch,CUDA Toolkit,ディープラーニングマシン,NVIDIA Geforce RTX4080,機械学習ソフトウェア,インストールなしOS,GPUメモリ容量ナノポアシーケンサー解析,Guppy,Dorado,DeepVariant,AMD Threadripper,バイオインフォマティクス,医学,生物学,デスクトップワークステーション,RNAシークエンスデータ主な仕様
CPU AMD Ryzen ThreadripperPRO 5965WX (3.80GHz 24コア) メモリ 128GB REG ECC ストレージ 2TB SSD M.2 ビデオ NVIDIA Geforce RTX4090 ネットワーク on board (1GbE x1 10GBase-T x1) 筐体+電源 タワー型筐体 + 1200W OS Ubuntu 20.04 キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。・Doradoとは
Doradoはナノポアシーケンシングで生成されたRNAシークエンスデータのアセンブルとアノテーションを行うために使用される遺伝子解析ソフトウェア。本事例公開時点ではα版でのリリースであり、完全版ではない。
RNAシークエンスデータを用いて高品質な塩基配列のアセンブルを行い、正確な転写産物の同定とアノテーションを行うことができ、ナノポアシーケンシングにおける問題である短いリード長と高いエラー率への最適化が行われている。・DeepVariantとは
DeepVariantはDeepLearningを活用して高品質なゲノム変異検出を行うゲノム解析ソフトウェア。ゲノム解析のために畳み込みニューラルネットワークを使用して,DNAの塩基の変異を検出する。
オープンソースで提供されており,ゲノム研究や医療分野,遺伝カウンセリングなど様々な分野で活用されている。事例追加日:2023/05/26
- 事例No.PC-10816
-

NGS解析&ナノポアシーケンサー解析用マシン
用途:MaSuRCAやGuppyを用いたハイブリッドアセンブリ、RNA-seq解析参考価格:520410円お客さまからのご相談内容
簡易的なNGS解析とナノポアシーケンサー解析を行う計画があり、そのためのPCを導入したい。
具体的にはMaSuRCAを利用した30Mb程度のハイブリッドアセンブリやRNA-seq解析を想定している。GPU版Guppy basecallerにも使うことができるのが理想で、それ以外に3Dモデル処理などの実施は考えていない。
OSはUbuntuを考えているが、WSLでUbuntuを使っても解析能力に大きな影響がなければ、Windows上で動かしたい。
その他に想定している内容は以下の通り。・CPU:12コア程度の製品を想定しているが、より良い提案があれば希望する
・ストレージ:SSDを希望する
・予算:50万円程度
・MaSuRCAのダウンロードページでは、ハードウェア要件として 「Bacteria (up to 10Mb): 16GB RAM, 8+ cores, 10GB disk space」の記載があるため、30MbであればPC-10596程度のスペックで動作するのではないかと考えているテガラからのご提案
ご要望の条件に合わせて構成を検討しました。
仕様は暫定ですが、MaSuRCAの公式リポジトリに掲載された動作要件のBacteriaとInsectの中間程度のスペックです。
OSはUbuntuのみをインストールする想定です。
Windows Subsystem for Linux 2 (WSL2)でのUbuntu利用
WSLでの利用に関しては、ソフトウェア自体は動作すると思われますが、解析能力への影響は避けられません。
WSLは基本的に仮想マシンですので、仮想化によるオーバーヘッドが生じます。Windowsを用意しなければならない理由が他にないようであれば、Ubuntuをネイティブに動作させる形での利用を推奨します。
その他の選択肢として、WindowsとUbuntuのデュアルブート環境を構築する方法があります。ご希望のお客様はご相談ください。また、本構成ではNVIDIA製ビデオカードを搭載しており、GuppyのGPU実行に対応しています。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7950X (4.50GHz 16コア) メモリ 64GB ストレージ 2TB SSD S-ATA ビデオ NVIDIA Geforce RTX3060 ネットワーク on board (2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー筐体 + 850W OS Ubuntu 20.04 キーワード
・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。・MaSuRCAとは
MaSuRCAは、高品質なペアエンド読み込みと長いリードのハイブリッドアセンブリに特化したゲノムアセンブリのためのソフトウェア。異なる読み込みタイプのデータを組み合わせてア、高速で正確なアセンブリを生成できる。・ハイブリッドアセンブリとは
ハイブリッドアセンブリとは、異なる読み込みタイプのデータを組み合わせて行うゲノムアセンブリの手法。短いペアエンド読み込みと長いリードの両方を使用することで、アセンブリの精度と連続性を向上させることができる。・WSL2とは
Windows Subsystem for Linux 2 (WSL2) はWindows上でLinux向けバイナリを実行する方法の一つ。参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【1/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【2/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【3/3】
事例追加日:2023/03/23
- 事例No.PC-10858
-

ターボ機械開発用マシン
用途:FINE/TurboやFINE/Open with OpenLabsを用いた流体解析参考価格:1794100円お客さまからのご相談内容
FINE/TurboやFINE/Open with OpenLabsを用いた流体解析を行うためのPCを導入したい。
以下の条件に合ったPCを提案して欲しい。・CPU:28コア/56スレッド以上 クロックは2.70GHz以上
・メモリ:512GB
・ストレージ:データ用ストレージとして8TB程度確保したい
・OS:なし
・予算:180万円程度だが、コストを抑える方法があれば提案して欲しい
・その他:4Kでの画面出力を希望テガラからのご提案
ご要望を踏まえてお見積もりをご用意しました。
2CPUで合計32コアとした構成でのお見積もりです。
2CPUの場合、メモリは16枚構成にするのがベストですので、32GBモジュール x16枚としています。コストや増設を考えたメモリ選定
コストダウンを優先する場合には、メモリ帯域が落ちることを前提とした32GBモジュール x8枚構成で導入し、後から増設するという運用も考えられます。なお、その場合は8枚のメモリに対して並列アクセスすることで速度がUPするため、増設するメモリは基本的に同一型番のメモリで統一する必要があります。コストの調整に関しては、お客様が重視する要素にあわせて検討させていただきます。
4Kでの画面出力については、T400あたりのカードでも対応できますが、解析用のモデルの要素数が多い場合には、ビデオカードの性能が不足する場合があります。3D系のモデルを動かす想定でT1000を選定していますが、実際の運用方法によってはコスト削減できる部分です。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。







通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Gold 6326 (2.90GHz 16コア) x2 メモリ 512GB REG ECC (32GB x16) ストレージ1 1TB SSD M.2 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA T1000 4GB ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 1000W OS なし その他 TPMモジュール キーワード
・FINE/Turboとは
FINE/Turboは、NUMECA Internationalが開発した商用CFDソフトウェア。ターボ機械や回転体の流体解析に特化した高度な機能を提供する。流体解析に必要な前処理、解析、後処理の機能が一つにまとめられており、正確かつ迅速な解析結果を得ることができる。・FINE/Open with OpenLabsとは
FINE/Open with OpenLabsは、非構造格子に対応し、高度に自動化された汎用流体解析統合環境で、完全六面体メッシュの自動作成や128コアの並列計算が可能。また、高速化機能やカスタマイズモジュールが標準搭載されている。事例追加日:2023/03/15
- 事例No.PC-10747
-

トランスクリプトーム解析用マシン
用途:トランスクリプトーム解析、全ゲノムリシーケンス解析参考価格:950400円お客さまからのご相談内容
イネのトランスクリプトームおよびゲノムデータにおける一連のデータ解析 (前処理、マッピング、DEGsの算出等) を不満なく行うことのできるLinuxマシンを導入したい。
想定しているスペックは以下の通り。・CPU:24コア 48スレッド 以上のCPU
・メモリ:256GB
・ストレージ:SSD 1TB
・OS:Linuxイネのトランスクリプトーム解析は1サンプルが約10Gbp、全ゲノムリシーケンス解析では約45Gbp。
データの保存には外付けストレージを利用する予定。CPUはXeonがいいかと思っているが、性能やコストを含めてAMD Threadripperと比較してどうか気になっている。
OSはUbuntuかRocky Linuxを予定している。どちらが初心者に向いているか知りたい。
予算90万円以下で構成を提案して欲しい。
テガラからのご提案
ご要望の条件に合わせて構成を検討しました。
第3世代Xeon Scalableを搭載した2CPU構成で、システムの合計で24コア/48スレッドです。ストレージ
人間などと比較して、イネのゲノムサイズはそこまで大きくありませんが、解析データの容量はそれなりのサイズになると考えられます。本件では、データ保存用の外部ストレージをお客様側で用意すると伺っていますが、PC本体のみで運用する場合には、データ用のストレージを搭載することをお勧めします。
CPU
24コアのXeonとThreadripper PROで比較すると、性能面ではThreadripper PROの方が優位です。
CPU単体の価格では、相対的にはXeonよりもThreadripperPROの方が安価ですが、構成全体のトータルコストでは、ThreadripperPRO 24コア構成は100万円台前半になるため、本件ではコストを優先し安価なXeonの2CPU構成でご提案しています。なお、次世代シーケンサー解析はCPUコア数やメモリ容量が重要な処理ですので、コア数を減らしてクロック重視で計算速度を上げる考え方はあまり有効ではありません。そのため、シングルコア性能が多少低くても、コア数を確保できる構成を優先するのが望ましいとお考えください。
OS
OSに関しては、Ubuntuと比べてRocky Linuxはあまり融通が利きません。
これは、UbuntuとRocky Linux (のベースになっているRedhat Enterprise Linux) の開発思想の違いによります。Rocky LinuxのベースであるRHELは、長期運用の安定性を第一としています。
Ubuntuはワークステーション向けのディストリビューションとして優れており、最新のハードウェアを採用したワークステーションとしてパフォーマンスを重視する場合、パッケージの更新頻度やカーネルバージョンなどの面でメリットがあります。Rocky Linuxを積極的に選択する理由がない場合には、Ubuntuをお勧めいたします。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Silver 4310 (2.10GHz 12コア) x2 メモリ 256GB REG ECC ストレージ 1TB SSD S-ATA ビデオ NVIDIA T400 ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 850W OS Ubuntu 22.04 キーワード
・トランスクリプトーム解析とは
トランスクリプトームとは、組織、細胞内における遺伝子転写産物(mRNA)の全体を指す。トランスクリプトーム解析は、生体細胞内における遺伝子の発現状況を網羅的に把握する解析手法。RNA-Seq解析や遺伝子発現解析とも呼ばれる。・Ubuntuとは
Ubuntuは、Linuxディストリビューションの1つ。フリーソフトとして提供されており、グラフィカルインストーラーにより、簡単にインストールして使用することができる。参考:Ubuntu (Ubuntu Japanese Team) ※外部サイトへ飛びます
・Rocky Linuxとは
Rocky Linuxは、Linuxディストリビューションの1つ。Red Hat Enterprise Linux (RHEL)のソースコードを使用しており、互換性を持つ。フリーソフトとして提供されており、長期の定期アップデートによる安定性を特長とする。参考:Rocky Linux (Rocky Enterprise Software Foundation) ※外部サイトへ飛びます
事例追加日:2023/02/09
- 事例No.PC-10539
-

Nextseq2000システムで取得したNGSデータを解析するためのマシン
用途:RNA-Seqマッピングツール「HISAT2」「Bowtie2」、マッピング結果解析ツール「samtools」、相同性検索プログラム「BLAST」、ゲノムアセンブリ用プログラム「Velvet」の利用参考価格:2015200円お客さまからのご相談内容
Nextseq2000システムで取得したNGSデータを解析するためのマシンを導入したい。
以下の条件に近い構成を提案して欲しい。・CPU:Intel Xeon 24コア以上 x2
・メモリ:768GB程度
・ストレージ1:SSD 2TB M.2
・ストレージ2:HDD 4TB S-ATA
・OS:Ubuntu
・予算:200万円になるべく近くなるようにテガラからのご提案
ご要望のCPUコア数を満たす構成にてご提案しました。
1CPUあたり28コア x2で合計56コアとなるようにCPUを選定しています。第3世代Xeon Scalableは、メモリチャンネルが8ですので、ご要望の768GBを超える容量で最適な構成とした場合、1TBを選択する必要があります。しかし、その場合には予算を大幅に超過してしまうため、ひとまずご希望よりも少ない容量でモジュール構成を最適化した512GBをご提案し、スペックと価格感をご確認いただく流れとしました。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Gold 6338 (2.00Hz 32コア) メモリ 512GB REG ECC (32GB x16) ストレージ1 2TB SSD M.2 ストレージ2 8TB HDD S-ATA ビデオ on board (VGAx1) ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 850W OS Ubuntu 22.04 キーワード
・HISAT2とは
HISAT2は、次世代シーケンシングにおけるリード (DNAとRNAの両方) をヒトゲノムの集団および単一の参照ゲノムにマッピングするためアライメントプログラム。高速でメモリ使用量が少ない。・Bowtie2とは
Bowtie2は、シーケンスリードを参照配列にアライメントするためのツール。哺乳類のような比較的長いゲノムのアライメントに優れている。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・Velvetとは
Velvetはゲノム配列をアセンブリするためのプログラム。de Bruijnグラフに基づくde novoアセンブリのためのツールであり、高いカバレッジを持つ短いリードデータに適している。また、de Bruijnグラフを操作することで、シーケンスエラーを除去し、リピートを解消するアルゴリズムが実装されている。事例追加日:2023/01/06
- 事例No.PC-10596
-

NGS解析用マシン
用途:統計分析ソフトウェア「R」、画像解析ソフトウェア「WinRHIZO」の利用参考価格:423500円お客さまからのご相談内容
NGS解析用マシンの導入を考えている。
バイオインフォマティクスを専門にはしていないため、それほど高度な作業を行う予定はない。
WinRHIZOで画像解析したデータや遺伝子発現データをExcelやRなどで解析したり、シーケンスデータから定量データに計算させる処理を考えている。3Dモデルを動かすような処理は行わない。想定スペックは以下の通り。
・CPU:32スレッド程度
・メモリ:64GB
・ストレージ:SSD 1TB S-ATA
・OS:Windows
・予算:30万~50万円上記の想定スペックは知人からのアドバイスによるもので、自分自身はPCに詳しくない。
一般的な大手メーカー製PCと比べて、セットアップの手間が多いなどの問題はないか。また、購入した場合にはどのようなソフトが付属するのか知りたい。テガラからのご提案
ご要望に合わせて、構成をご提案しました。
CPUは、AMD Ryzen9 Threadripper 7950Xを選択し、32スレッド程度の条件を満たしています。
また、3Dモデルの表示や操作は行わないと伺いましたので、ビデオ出力はコストを優先してオンボードとしています。一般的な大手メーカー製マシンと比較した場合、納入後に行っていただくセットアップ内容には、それほど大きな違いはありません。しかし、弊社製PCにはセキュリティソフトの試用版などはバンドルされませんので、必要な場合にはご相談ください。
また、OS以外のソフトウェアに関しては、Windowsが標準で提供するもの以外は付属・インストールしておりません。そのため、利用予定のない多数のソフトウェアにマシンのリソースを占有されたり、煩わしいポップアップが表示されることなく、快適にお使いいただくことができます。
なお、現在のWindowsでは、DVDへの書き込みや読み込みが標準サポートされています。DVDビデオの作成や再生を行う場合には別途ソフトウェアが必要ですが、そのような用途での利用がない場合には追加のソフトウェアは不要です。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。




通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7950X (4.50GHz 16コア) メモリ 64GB ストレージ 1TB SSD S-ATA ビデオ on board (DisplayPort x1 HDMI x1) ネットワーク on board (2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー型筐体 + 850W OS Microsoft Windows 11 Pro 64bit キーワード
・NGS解析とは
NGS (Next Generation Sequencer:次世代シーケンサー) は、核酸 (DNAとRNA)の塩基配列情報を決定するための基盤技術。数百万のDNA分子を同時に配列決定することが可能。
NGSは高速でシークエンシングを行うことができるため、臨床サンプルの劣化の早いRNAウイルスの塩基配列同定などで用いられる。・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。
多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。参考:The R Project for Statistical Computing ※外部サイトに飛びます
・WinRHIZOとは
WinRHIZOはRegent Instruments社による画像解析ソフトウェア。植物の根長や形態、構造、色を測定・解析を行う。参考:WinRHIZO (Regent Instruments) ※外部サイトに飛びます
事例追加日:2022/12/09
- 事例No.PC-10619
-

遺伝的能力の推定計算用マシン
用途:遺伝子型の情報を使った遺伝的能力の推定計算参考価格:1959100円お客さまからのご相談内容
PC-8850Bの遺伝子発現解析用マシン (2022年9月版) を見ての問い合わせ。
ゲノムデータや統計解析を使用した計算を行うためのマシンが欲しい。
SNP (スニップ/一塩基多型) という遺伝子型の情報を使い、遺伝子的能力の推定を行う予定。
具体的には、1万x1万以上の行列を処理するため、大容量のメモリが必要。現在使用中のマシンスペックは以下の通り。
・機種はMac Pro
・CPU:Xeon E5-2697v2 2.7GHz 12コア
・メモリ:64GB使用しているプログラムはBLUPF90。
複数の計算を処理するにあたって、64GBメモリでは不足気味であることが分かっている。その他、将来的にはPythonを用いた16S リボソームRNAのデータ解析や、畜産のビッグデータを使用した機械学習も予定している。
OSは使い慣れたWindowsを希望。ストレージ容量は4TB以上が必須。
PCに詳しくないので具体的な要望を出すことは難しいが、予算内でできる限り高スペックなマシンを提案して欲しい。テガラからのご提案
ご覧いただいた事例No.PC-8850Bをベースに、構成を変更してご提案しました。
■Point
・メインの用途を考えると、CPUでの処理が主になると考えられる。
・メモリは64GBで不足「気味」なので、それ以上の容量があれば余裕をもって同じ処理を実行できると推測。CPUは、コア数とクロックのバランスのよいThreadripperPRO 5975WXを選定しました。
また、メモリは余裕をみて256GBとしています。現在お使いのマシンの4倍に相当する容量ですので、同じ処理を比較的余裕を持って実施できる想定です。その他、将来的に機械学習の手法を取り入れる可能性があることを考慮し、機械学習で利用されることの多いハイエンドGPUを搭載しています。機械学習の実装にも種類がありますので、NVIDIA GPUに対応するGPGPUフレームワークやCUDA Toolkitを介したプログラムを利用しない、またはそれほど本格的に取り組む想定ではない場合には、必ずしもこのGPUである必要はありませんので、安価な製品に変更することで価格を抑えることができます。
なお、ご利用中のMac Proと比較するとパーツの世代差が大きいため、性能の向上を体感できる構成です。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
検索キーワード
遺伝的能力推定,ゲノムデータ解析,SNP (スニップ/一塩基多型),メモリ容量,BLUPF90,16SリボソームRNA解析,機械学習,Windows OS,ストレージ容量,ThreadripperPRO主な仕様
CPU AMD Ryzen Threadripper 5975WX (3.60GHz 32コア) メモリ 256GB ストレージ1 4TB SSD S-ATA ストレージ2 16TB HDD S-ATA ビデオ NVIDIA Geforce RTX3090 ネットワーク on board (1GbE x1 10GBase-T x1) 筐体+電源 タワー型筐体 + 1000W OS Microsoft Windows 11 Pro 64bit その他 TPMモジュール キーワード
・BLUPF90系プログラムとは
BLUEPF90系プログラムは、動物飼育における混合モデル計算用の統計ソフトウェアパッケージ。
動物や植物の育種のための量的遺伝子学的アプローチで用いられる。
Fortran 90/95で記述されたプログラムは、何十万もの遺伝子型からゲノミック選抜を行うことができる。参考:BLUPF90 Family of Programs ※外部サイトに飛びます
・機械学習とは
機械学習とは、データ蓄積により特定のタスクをコンピュータ上で実行できるようになる仕組み。
コンピュータが自律的に認識・予想精度を向上させる。機械学習に関しては、弊社オウンドメディア「TEGAKARI」の関連記事をご覧ください。
参考:【特集記事】機械学習ってなんだろう ※弊社オウンドメディア「TEGAKARI」に飛びます
検索キーワード
genomic selection,genomic prediction,genome-wide association,single-step genomic BLUP,ssGBLUP,genomic relationship matrix,genome-wide,blupf90,genomic,snp,genetic evaluation,variance componentsDeep learning,Machine learning,Artificial intelligence,Neural networks,Deep neural networks,Deep stacking networks,Supervised learning,Unsupervised learning,Natural language processing,Smart manufacturing,Computational intelligence,Data analytics,learning (artificial intelligence),Information processing,Computer vision,AI,big data,programming
事例追加日:2022/12/07
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
| 「あんしん+」 もしもの時の延長保証サービス |
|
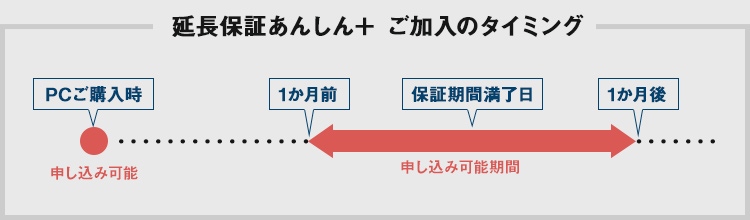
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 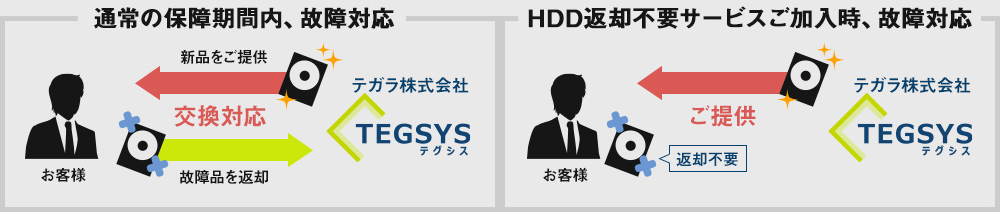
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。