- 事例No.PC-TE1J254011
-

シーケンスデータ解析/機械学習用ワークステーション (システム要件に最適化)
用途:エピジェネティクス解析、de novoアセンブリ、RNA-Seq解析、メタゲノム解析、機械学習参考価格:3261500円お客さまからのご相談内容
事例No. PC-25000268を見ての問い合わせ。ナノポアのシーケンスデータ解析と機械学習の双方に対応するワークステーションを導入したい。
エピジェネティクス解析やde novoアセンブリ、RNA-Seq解析、メタゲノム解析などを想定している。
使用するソフトウェアは、以下の通り。- 汎用解析・ML基盤:Samtools、XGBoost、LightGBM
- ゲノムアセンブリ・評価:SPAdes・BUSCO・Prodigal・FastANI・GTDB-Tk
- ナノポアベースコール:Guppy・Dorado・Remora・DeepMod2
OSはUbuntuで、予算は400万円程度を希望する。設置作業も含めた見積もりが欲しい。
通常24時間以内に担当者からご連絡いたします
テガラからのご提案
ツール要件を重視した大容量メモリ構成
本構成は「システム要件を基準に最適化した構成」としてご案内したスペックです。特に大規模アセンブリや多数サンプルのバッチ処理を想定し、CPUコア数とメモリ容量を優先。EPYC 9554 (64コア) と768GBメモリにより、メモリ負荷の大きい解析に強みを持たせています。
事例No. PC-25000268をグレードアップしつつ、機械学習にも対応できる汎用性を重視した構成は、事例No.PC- TW3J253928をご覧ください。
CPUについて
AMD EPYC 9554は64コア構成で高い並列処理性能を備え、大量のサンプルを並行処理するワークロードに適しています。CPUリソースを多く要求するゲノム解析ツールや、複数ジョブを同時実行する環境で効率を発揮します。
メモリ容量について
ご利用予定のソフトウェアには、推奨メモリ容量が256GB~512GB付近のツールが複数存在します。そのため、解析規模や将来のデータ拡張を踏まえ、余裕を持った768GBを搭載しました。長時間ジョブの安定性向上にも寄与します。
GPUの選定について
本構成では、研究用途における機械学習処理への対応を目的に NVIDIA RTX 6000 Ada (Max-Q 96GB) を搭載しています。
深層学習フレームワークとの高い親和性を持ち、モデル学習や推論処理において高い実用性を発揮します。Doradoについては、GPUアクセラレーションを利用する際に倍精度演算を前提としたハイエンドGPUが例示されています。
そこで今回は、Doradoの高精度GPU要件をそのまま満たす構成ではなく、機械学習を中心に幅広い研究用途へ柔軟に対応できる現実的かつ効果的な選択肢として、RTXシリーズを採用した構成としました。RTXシリーズは深層学習フレームワークとの相性もよく、多様な研究タスクに対応しやすい点が特長です。今後の拡張やワークフローの進化にも柔軟に応えられる構成となっています。
参考情報:Benchmarking the Oxford Nanopore Technologies basecallers on AWS
ストレージと運用性
高速アクセスが必要なワークフローに合わせ、4TB NVMe Gen5 SSD を2基搭載し、高速な一時データ処理に対応しています。
また、24TB HDD を併用することで、シーケンスデータの長期保管や再解析にも適したストレージ構成としました。
さらに、現地での設置作業 (開梱・設定・起動確認) も含めて対応し、導入後すぐに研究へ着手いただけるよう配慮しています。運用要件に寄り添った最適化
納期や予算条件を満たしつつ、求められた要件に最も合致するスペックとして構成しました。多様なツールを運用する研究環境で、安定した解析パイプラインを維持しやすい点が特長です。
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD EPYC 9554 3.1GHz 64C/128T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ1 4TB SSD M.2 NVMe Gen5 x 2 ストレージ2 24TB HDD S-ATA ビデオ NVIDIA RTX PRO6000 Max-Q 96GB ネットワーク on board (10GBase-T x2) 筐体+電源 ミドルタワー 1500W 80PLUS PLATINUM OS Ubuntu 24.04 その他 現地設置作業(開梱・設置・ケーブリング・起動確認) キーワード
・Samtoolsとは
Samtoolsは、次世代シーケンス (NGS) データの処理・解析に広く用いられる定番ツール群。BAMやCRAMなどのアライメントデータのソート、インデックス作成、フィルタリング、可視化などの高速処理が可能で、ゲノム解析ワークフローの基盤として広く利用されている。・XGBoostとは
XGBoostは、勾配ブースティング決定木 (GBDT) アルゴリズムを高速かつ高精度に実装した機械学習フレームワーク。分類・回帰・ランキングなど多用途で、ゲノム解析、疾患リスク予測、遺伝子発現解析などバイオインフォマティクス分野でも広く利用される。https://xgboost.ai/参考:XGBoost Official Site
・LightGBMとは
LightGBMは、Microsoftが開発した高速でメモリ効率の高い勾配ブースティングフレームワーク。大規模データの解析に適しており、SNP解析、メチル化データの分類、疾患予測モデルなどにも利用される。・SPAdesとは
SPAdesは、微生物ゲノムアセンブリに広く利用されるde novoアセンブラー。Illumina・Nanopore・PacBioなど複数プラットフォームを統合したハイブリッドアセンブリに対応し、高品質なコンティグ構築が可能。・BUSCOとは
BUSCOは、ゲノムアセンブリの完全性 (completeness) を評価するための代表的ツール。保存性の高いシングルコピー遺伝子セットを用い、アセンブリ品質の客観的評価が可能。・Prodigalとは
Prodigalは、微生物ゲノムに特化した遺伝子予測ツール。プロカリア遺伝子領域の高精度抽出が可能で、メタゲノム解析でも高い性能を発揮する。事例追加日:2026/2/12
- 事例No.PC-TW3J253928
-

シーケンスデータ解析/機械学習用ワークステーション (汎用構成)
用途:エピジェネティクス解析、de novoアセンブリ、RNA-Seq解析、メタゲノム解析、機械学習参考価格:3169100円お客さまからのご相談内容
事例No. PC-25000268を見ての問い合わせ。ナノポアのシーケンスデータ解析と機械学習の双方に対応するワークステーションを導入したい。
エピジェネティクス解析やde novoアセンブリ、RNA-Seq解析、メタゲノム解析などを想定している。
使用するソフトウェアは、以下の通り。- 汎用解析・ML基盤:Samtools、XGBoost、LightGBM
- ゲノムアセンブリ・評価:SPAdes・BUSCO・Prodigal・FastANI・GTDB-Tk
- ナノポアベースコール:Guppy・Dorado・Remora・DeepMod2
OSはUbuntuで、予算は350万円程前後を希望する。
通常24時間以内に担当者からご連絡いたします
テガラからのご提案
機械学習を見据えたバランス強化構成
本構成は「事例No. PC-25000268をグレードアップしつつ、機械学習にも対応できる汎用性」を重視した案としてご案内しました。Xeon W プロセッサと512GBメモリを組み合わせ、シーケンス解析に必要なスループットと、機械学習処理に必要な演算性能の両立を図っています。
システム要件を基準に最適化した構成は、事例No.PC- TE1J254011をご覧ください。
CPUについて
Intel Xeon W7-3565X (32コア) は高クロックで単一タスク性能に優れ、ツールによって負荷特性が分かれるゲノム解析と機械学習処理の双方に適した選択です。計算処理の一部がCPU性能に依存するソフトウェア環境に向いています。
GPUの選定について
本構成では、機械学習の活用を見据え、GPUを搭載しています。
シーケンス解析のワークフローではCPU主導の処理が多い一方、機械学習を取り入れる研究ではGPUの存在が大きな効果を発揮するため、研究の幅を広げる観点からもGPU追加を採用しました。Doradoについては、GPUアクセラレーションを利用する際に倍精度演算を前提としたハイエンドGPUが例示されています。
そこで今回は、Doradoの高精度GPU要件をそのまま満たす構成ではなく、機械学習を中心に幅広い研究用途へ柔軟に対応できる現実的かつ効果的な選択肢として、RTXシリーズを採用した構成としました。RTXシリーズは深層学習フレームワークとの相性もよく、多様な研究タスクに対応しやすい点が特長です。今後の拡張やワークフローの進化にも柔軟に応えられる構成となっています。
参考情報:Benchmarking the Oxford Nanopore Technologies basecallers on AWS
拡張性について
大型のミドルタワー筐体を採用することで、将来的なストレージ増設やGPUの追加にも柔軟に対応できます。研究用途の変化に合わせて活用範囲を広げやすい点が特長です。
テガラのオーダーメイドPC製作サービスは、導入時の用途に加え、将来的な研究規模の拡大を見据えたシステムの拡張にも対応しています。
各種ソフトウェア要件に応じた構成のご提案はもちろん、研究環境全体の構築に関するご相談も承っています。
お客様のニーズに合わせて最適なソリューションをご提供しますので、どうぞお気軽にお問い合わせください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W7-3565X 2.50GHz (TB3.0時 最大4.8GHz) 32C/64T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ1 4TB SSD M.2 NVMe Gen5 ストレージ2 24TB HDD S-ATA ビデオ NVIDIA RTX PRO5000 48GB ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 24.04 キーワード
・Samtoolsとは
Samtoolsは、次世代シーケンス (NGS) データの処理・解析に広く用いられる定番ツール群。BAMやCRAMなどのアライメントデータのソート、インデックス作成、フィルタリング、可視化などの高速処理が可能で、ゲノム解析ワークフローの基盤として広く利用されている。・XGBoostとは
XGBoostは、勾配ブースティング決定木 (GBDT) アルゴリズムを高速かつ高精度に実装した機械学習フレームワーク。分類・回帰・ランキングなど多用途で、ゲノム解析、疾患リスク予測、遺伝子発現解析などバイオインフォマティクス分野でも広く利用される。https://xgboost.ai/参考:XGBoost Official Site
・LightGBMとは
LightGBMは、Microsoftが開発した高速でメモリ効率の高い勾配ブースティングフレームワーク。大規模データの解析に適しており、SNP解析、メチル化データの分類、疾患予測モデルなどにも利用される。・SPAdesとは
SPAdesは、微生物ゲノムアセンブリに広く利用されるde novoアセンブラー。Illumina・Nanopore・PacBioなど複数プラットフォームを統合したハイブリッドアセンブリに対応し、高品質なコンティグ構築が可能。・BUSCOとは
BUSCOは、ゲノムアセンブリの完全性 (completeness) を評価するための代表的ツール。保存性の高いシングルコピー遺伝子セットを用い、アセンブリ品質の客観的評価が可能。・Prodigalとは
Prodigalは、微生物ゲノムに特化した遺伝子予測ツール。プロカリア遺伝子領域の高精度抽出が可能で、メタゲノム解析でも高い性能を発揮する。事例追加日:2026/2/12
- 事例No.PC-24001310
-

バイオインフォマティクス解析向けマシン
用途:Bowtie2、STAR、BWA、samtools、Juicer/juicebox、Rを用いたHi-Cデータ、scRNAseq、scATACseqなどの解析参考価格:963600円お客さまからのご相談内容
バイオインフォマティクス解析を行うLinuxのワークステーションの購入を考えている。主な用途はHi-Cデータ、scRNAseq、scATACseqなどのデータ解析。解析に使うソフトウェアは、Bowtie2、STAR、BWA、samtools、Juicer/juicebox、R (Seurat、Singac、etc…)を想定している。
下記のような条件を考えているが、予算内で実現可能か教えて欲しい。
CPU:指定なし (クロックは下げてもコア数の方が重視。コア数は20-36程度)
メモリ:128GB-256GB (メモリ容量を重視したい) 32GB x6枚の構成を考えている。
Storage:指定なし (2TB以上)
OS:Linux OS (Ubuntu24.04 or 22.04)
設置場所:居室
予算:100万円以内テガラからのご提案
ご予算の範囲内で構成を検討しました。
GPUの優先度は低いため、CPUやメモリを重視
ご連絡いただいたソフトウェアはいずれもGPU性能を必要としないため、ビデオカードには画面出力用としてRTX A400を採用しています。GPU計算を行う予定がある場合にはご連絡ください。
メモリ構成について
ご要望にあわせて32GB x6枚の構成としていますが、本構成のメモリチャネルに合わせて4の倍数でモジュールを搭載する構成がベストです。そのため、メモリ6枚のうち2枚は、4枚搭載時に発揮される本来の最高速度よりもわずかに遅くなりますので、予めご承知おきください。









通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon W5-2565X 3.20GHz (TB3.0時 最大4.8GHz) 18C/36T メモリ 合計192GB DDR5 5600 REG ECC 32GB x 6 ストレージ 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (2.5GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 + 1000W 80PLUS PLATINUM OS Ubuntu 24.04 ■キーワード
・Hi-Cとは
Hi-C(High-throughput Chromosome Conformation Capture)は、シーケンシングによりゲノムの三次元構造を解析するための革新的な技術。2009年に開発された手法で、細胞核内でのDNAの空間的配置を高解像度で明らかにすることができる。
・scRNAseqとは
シングルセルRNA-seq (scRNA-seq) は個々の細胞レベルで遺伝子発現を解析可能にする技術。細胞のトランスクリプトームマッピングを行うことで、細胞間の違いを明らかにする。同種の細胞でも個々に微細な違いがあるため、このような解析手法が必要とされる。活用としては、例えばがん細胞内の異質性の解明や細胞分化のプロセス解明などが期待される。また、少ない量のRNAからの解析が可能であり、細密な解析に利用されている。
・scATACseqとは
シングルセルATAC-seq (scATACseq)は、個々の細胞レベルでクロマチンアクセシビリティを網羅的に解析する技術。細胞集団内のエピジェネティックな多様性を詳細に調べることが可能。scATAC-seqは、scRNA-seqと組み合わせることで、より包括的な細胞状態の理解が可能になる。
・Bowtie2とは
Bowtie2は、シーケンスリードを参照配列にアライメントするためのツール。哺乳類のような比較的長いゲノムのアライメントに優れている。
・STARとは
STAR は RNA-Seqで得られたリード(生データ)をリファレンス配列にマッピングするプログラム。Github上で公開されており、要求されるスペックは高いものの、高速なマッピング速度を有している。
・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。
・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約) HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・Juicerとは
Hi-Cデータを解析するためのオープンソースツール。生の配列データから正規化されたコンタクトマップを作製したり、テラバイト規模のHi-Cデータセットを処理することができる。
・JuiceBoxとは
Juicerで生成された.hicファイルを視覚化するためのアプリケーション。生成されたHi-Cマップを直感的に閲覧し、解析することができる。
参考:GitHub – aidenlab/Juicebox: Visualization and analysis software for Hi-C data – ※外部サイトに飛びます
・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。 多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。
事例追加日:2025/01/14
- 事例No.PC-11668
-

Omics解析向けワークステーション
用途:R、Python3、SAMtoolsやBWA、STARを用いた基本的なオミクス解析、Higlassを用いたHi-Cデータの可視化参考価格:1556500円お客さまからのご相談内容
現在使用しているバイオインフォマティクス専用ワークステーションの買い替えを検討している。
具体的な用途として、基本的なOmics解析に用いるSAMtoolsやSTAR、Hi-Cデータの可視化に用いるHiglassをスムーズに運用したい。
これらの用途を前提に、現在使っているPCと同等かそれ以上のスペックの構成を予算80万~160万円の範囲で提案してほしい。なお、現在使用しているPCのスペックは以下の通り。
CPU Intel Xeon E5-2640 v4 ×2(20コア/40スレッド) メモリ 256GB REG ECC ビデオ NVIDIA Quadro P620 OS Ubuntu 22.04 テガラからのご提案
お客さまご希望の条件に沿った構成をご提案しました。
ご予算内でCPUスペックを重視した構成
ご予算に合わせて、現在ご利用のマシンよりもスペックのグレードを高めた構成です。
CPUはXeon Gold 5418Yを2基搭載し、現在ご利用のマシン (20コア) の2倍以上である48コアを実現しています。
メモリ搭載量は現在のマシンと同じ256GBですが、メモリスロットの空きが8スロット分あるため、将来のメモリ増設に対応しています。
ストレージ容量は、解析用途であることを踏まえて、余裕を見た4TBのM.2 NVMe Gen4 SSDを選定しています。
NVMe接続の製品のため、SATA接続のHDDやSSDと比較して高速なデータの読み込み/書き込みが期待できます。合計48コアのCPUと256GBのメモリ容量により、計算量が大きくなりやすいバイオインフォマティクス解析でも迅速な計算処理が見込めます。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
いただいた条件に合わせて柔軟にマシンをご提案いたしますので、掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。






通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Intel Xeon Gold 5418Y (2.00GHz 24コア) ×2 メモリ 256GB REG ECC ストレージ 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA T1000 8GB ネットワーク on board (10GBase-T x2) 筐体+電源 ミドルタワー型筐体 + 1000W OS Ubuntu 22.04 ■キーワード
・Omics解析とは
Omics解析は、生物学や医学の分野で広く使用されるデータ駆動型のアプローチ。Omicsとはゲノミクス、プロテオミクス、トランスクリプトミクスなど、生物学的なデータを収集・解析するための技術の総称。
Omics解析では、高スループットの実験技術や次世代シーケンシングなどの先端技術が活用される。これにより生成される大量のデータは、統計学的な手法やデータマイニングの手法を用いて解析され、疾患のメカニズム解析や新たなバイオマーカーの同定、個別化医療への応用などが可能となる。・Hi-C法とは
3C(Chromosome Conformation Capture; 染色体立体配座捕捉)法を発展させた全ゲノム解析手法。細胞核内ゲノム3次元構造において空間的に近接する任意のゲノムDNA断片のペアを、次世代シーケンサーを用いて網羅的に検出し、ゲノム3次元構造を推定・解析できる。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・STARとは
STAR は RNA-Seqで得られたリード(生データ)をリファレンス配列にマッピングするプログラム。Github上で公開されており、要求されるスペックは高いものの、高速なマッピング速度を有している。
・HiGlassとは
HiGlassとは大規模な Hi-C およびその他のゲノム データ セットを高速に可視化できるデータビューア。他のオミックスデータと連携させつつ、探索的データ解析ができる。
事例追加日:2024/06/26
- 事例No.PC-10706
-

次世代シーケンサー解析用ワークステーション
用途:BWA、GATK、Samtoolsの利用参考価格:1201200円お客さまからのご相談内容
バイオインフォマティクス分野で次世代シーケンサー解析を行うためのワークステーションが欲しい。解析パイプラインで使用するソフトウェアは「BWA」「GATK」「Samtools」などを予定。希望条件は以下の通り。
・CPU:32スレッド以上
・メモリ:予算内で限界まで搭載 (将来的には1TBまで増設予定)
・ストレージ:512GB~1TBのSSD NVMeタイプ
・GPU:画面が表示できればOK
・OS:インストールなし (ubuntu 20.04を予定)
・予算:120万円程度テガラからのご提案
ご希望の条件に合わせて構成を検討しました。
CPUはRyzen ThreadripperPRO 5969WX (24コア 48スレッド) を採用しています。
ストレージはNVMeタイプの1TB SSDとしています。メモリは256GB搭載しており、1TBまでの拡張が可能です。
ただし、出荷時点でのメモリモジュール構成は64GB x4枚であり、メモリの空きスロットが4つであることを踏まえると、増設だけで1TBを達成するのは難しい構成です。
初期状態のメモリを活かす場合は追加で64GB x4枚を増設し、512GBまで拡張可能です。
1TBまで拡張する場合には、既存の64GBモジュールを取り外し、128GBモジュール x8枚を搭載する必要があります。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen ThreadripperPRO 5965WX (3.80GHz 24コア) メモリ 256GB REG ECC ストレージ1 1TB SSD M.2 ビデオ NVIDIA GeForce GT710 ネットワーク on board (1GbE x1 10GBase-T x1) 筐体+電源 タワー型筐体 + 1000W OS なし キーワード
・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。・GATKとは
GATK (Genome Analysis Toolkit) は、次世代シーケンサーから出力された塩基配列データからバリアントの解析 (遺伝子の変異解析) を行うための解析ツール群。内包するツールは、個別に使用することも連携させて使用することもできる。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)事例追加日:2023/01/19
- 事例No.PC-10539
-

Nextseq2000システムで取得したNGSデータを解析するためのマシン
用途:RNA-Seqマッピングツール「HISAT2」「Bowtie2」、マッピング結果解析ツール「samtools」、相同性検索プログラム「BLAST」、ゲノムアセンブリ用プログラム「Velvet」の利用参考価格:2015200円お客さまからのご相談内容
Nextseq2000システムで取得したNGSデータを解析するためのマシンを導入したい。
以下の条件に近い構成を提案して欲しい。・CPU:Intel Xeon 24コア以上 x2
・メモリ:768GB程度
・ストレージ1:SSD 2TB M.2
・ストレージ2:HDD 4TB S-ATA
・OS:Ubuntu
・予算:200万円になるべく近くなるようにテガラからのご提案
ご要望のCPUコア数を満たす構成にてご提案しました。
1CPUあたり28コア x2で合計56コアとなるようにCPUを選定しています。第3世代Xeon Scalableは、メモリチャンネルが8ですので、ご要望の768GBを超える容量で最適な構成とした場合、1TBを選択する必要があります。しかし、その場合には予算を大幅に超過してしまうため、ひとまずご希望よりも少ない容量でモジュール構成を最適化した512GBをご提案し、スペックと価格感をご確認いただく流れとしました。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Gold 6338 (2.00Hz 32コア) メモリ 512GB REG ECC (32GB x16) ストレージ1 2TB SSD M.2 ストレージ2 8TB HDD S-ATA ビデオ on board (VGAx1) ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 850W OS Ubuntu 22.04 キーワード
・HISAT2とは
HISAT2は、次世代シーケンシングにおけるリード (DNAとRNAの両方) をヒトゲノムの集団および単一の参照ゲノムにマッピングするためアライメントプログラム。高速でメモリ使用量が少ない。・Bowtie2とは
Bowtie2は、シーケンスリードを参照配列にアライメントするためのツール。哺乳類のような比較的長いゲノムのアライメントに優れている。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・Velvetとは
Velvetはゲノム配列をアセンブリするためのプログラム。de Bruijnグラフに基づくde novoアセンブリのためのツールであり、高いカバレッジを持つ短いリードデータに適している。また、de Bruijnグラフを操作することで、シーケンスエラーを除去し、リピートを解消するアルゴリズムが実装されている。事例追加日:2023/01/06
- 事例No.PC-8561
-

次世代シーケンサー解析用マシン (Bioconda3の利用を想定)
用途:Bioconda3の利用参考価格:750200円お客さまからのご相談内容
次世代シーケンサー解析ソフト「Bioconda3」を利用するためのマシンを導入したい。
想定しているスペックは以下の通り。・CPU:Xeon 36スレッド程度
・メモリ:ECC 64~128GB
・ストレージ:SSD 1TB + HDD 6TB
・OS:Ubuntu 20.04
・その他:Bioconda3プリインストールBioconda3の他にも、BWA、GATK、STAR-Fusion、SAMtools、Bedtoolsなどを利用する予定。
予算140万円の範囲で提案して欲しい。テガラからのご提案
ご要望に合わせて36スレッドのXeon Wを採用した構成にてお見積もりしました。
HDDは6TB製品がほとんど流通しておらず、入手できた場合でもコスト面でもメリットが少ないため、代替品として8TB製品を選択しています。また、ご予算の上限には余裕がありますが、ご利用予定のソフトの中にはGPGPUを利用するものがないため、ビデオカードは画面出力のみを考慮したエントリークラスの製品としています。GPUの利用も想定する場合、より上位の製品への変更が可能です。
その他のスペックはひとまずご要望のスペックを優先した選定としていますが、ご予算上限にあわせたご提案をご希望の場合には気兼ねなくお申し付けください。なお、Bioconda3はminiconda (Anacondaのコンパクト版) のチャンネルとして導入する形ですので、Biocondaチャンネルの登録を行った状態での出荷を想定しています。
■Bioconda3
condaチャンネルのディストリビューションの1つ。
バイオインフォマティクス関連のツールが登録されたパッケージマネージャー。■miniconda
Pythonとパッケージマネージャー「conda」に加え、必要最低限のパッケージの入ったディストリビューション。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon W-2295 (3.00GHz 18コア) メモリ 128GB ストレージ1 1TB SSD M.2 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA T400 ネットワーク on board (10/100/1000Base-T x1 5G x1) 筐体+電源 ミドルタワー筐体 + 850W OS Ubuntu 20.04 その他 Bioconda3インストール設定 事例追加日:2022/10/13
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
| 「あんしん+」 もしもの時の延長保証サービス |
|
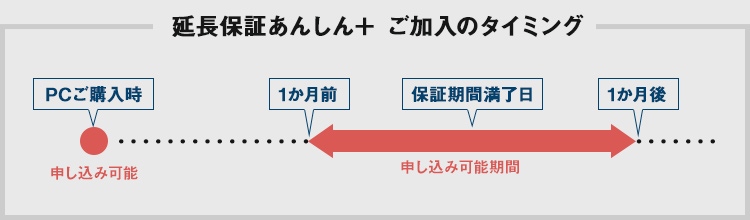
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 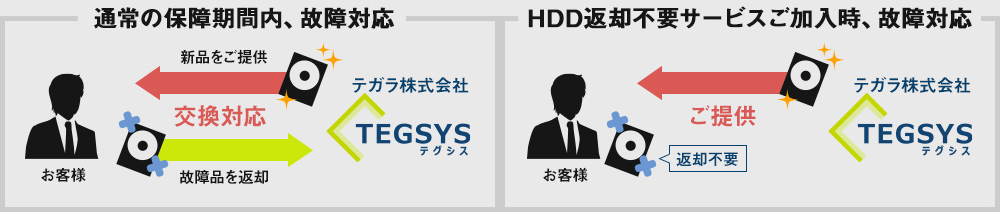
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。