- 事例No.PC-10722
-

メタゲノム解析用マシン (2023年02月版)
用途:メタゲノム解析参考価格:1790800円お客さまからのご相談内容
メタゲノム解析を行うためのPCが欲しい。
NGSデータのクオリティフィルタリングから、アッセンブルやビニング、KEGGやBLASTも利用したい。・CPU:Xeon Gold 6326程度
・メモリ:512GB
・OS:Ubuntu
・予算:180万円以内
・その他:MetaWRAPとMetaSanityを利用するメタゲノム解析で一般的に使用するプログラムは、全て使用できればと考えている。
MetaWRAPではアッセンブルが難関でかなりのメモリ容量が必要になるので,ある程度優先したい。テガラからのご提案
ご要望の条件に合わせて構成を検討しました。
MetaWRAPはCPUとメモリのスペックを高めることが重要なので、ご要望のCPU・メモリの条件はご予算ともマッチした良い選択だと思われます。また、MetaWRAPはデータベースの容量が合計数百GBとかなり大きいので、その点に注意したストレージ構成としています。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。








通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Gold 6326 (2.90GHz 16コア) メモリ 512GB ストレージ1 2TB SSD S-ATA x2 ストレージ2 8TB HDD S-ATA x2 ビデオ NVIDIA T1000 ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 850W OS Ubuntu 20.04 キーワード
・メタゲノム解析とは
メタゲノム解析とは、環境中の微生物の群集を培養することなくそのままゲノム精製して網羅的に解析する手法。遺伝子配列から環境中に生息する微生物の種類や環境的機能を知ることができる。・MetaWRAPとは
MetaWRAPは、メタゲノム解析用のソフトウェア。読み取り品質管理やアッセンブル、視覚化、分類学的プロファイリング、ビニングなど様々なタスクを処理することができる。・MetaSanityとは
MetaSanityは、微生物ゲノムを分析に適したソフトウェアスイート。ゲノム評価と機能アノテーションのための統一的なワークフローを提供し、すべての出力を単一のクエリ可能なデータベースにまとめることができる。・KEGGとは
KEGG (Kyoto Encyclopedia of Genes and Genomes)はゲノム配列決定やその他のハイスループットによって生成される大規模な分子データセットから、細胞、生物、生態系などの生命システムの高レベルの機能と有用性を理解するためのデータベースリソース。・BLASTとは
BLAST (Basic Local Alignment Search Tool) は,相同性検索を高速に行うプログラム。手元にあるシーケンスでデータベースもしくはライブラリに対して検索することにより,ある閾値以上のスコアで類似するシーケンス群を発見することができる。事例追加日:2023/02/28
- 事例No.PC-10755
-

ColabFold / RoseTTAFold用マシン
用途:ColabFold、RoseTTAFoldによるタンパク質構造解析参考価格:1003200円お客さまからのご相談内容
事例No.PC-10260Aを見ての問い合わせ。
ColabFoldとRoseTTAFoldを使用するため、事例と同程度のマシンを導入したい。
考えている条件は以下の通り。・事例No.PC-10260Aの構成をベースにする
・ストレージ:2台目のストレージを4TB SSD M.2に変更
・OS:Windows 11とUbuntuのデュアルブートを希望
・予算:予算100万円程度テガラからのご提案
ご要望の条件に合わせて構成を検討しました。
お客様がご覧になった事例No.PC-10260Aのストレージ1と2は、それぞれ別のOSをインストールするためのものです。
本件でのストレージ容量変更は、データの一次保存場所にすることが目的でしたので、OS用ストレージの容量変更ではなく、データ用ストレージとして4TB SSD M.2を2台追加しました。その他、CPUとGPUをご予算と現行スペックに合わせて変更しています。
ColabFoldのLocal版はWSL2でも動作するという情報がありますので、場合によってはUbuntu側の処理をWSL2で実装する方法も考えられるかと存じます。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7900X (4.70GHz 12コア) メモリ 64GB ストレージ1 500GB SSD S-ATA x2 ストレージ2 4TB SSD M.2 x2 ビデオ NVIDIA Geforce RTX4080 ネットワーク on board (2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー筐体 + 1000W OS Microsoft Windows 11 Professional 64bit その他 追加インストール作業 Ubuntu 20.04 LTS + CUDA Toolkit 11 キーワード
・ColabFoldとは
ColabFoldはGoogle Colab上で利用できるAlphaFold2とAlphaFold-Multimer。タンパク質構造検索ツール MMseqs2 (Many-against-Many searching) の高速な相同性検索をAlphaFold2またはRoseTTAFoldと組み合わせることで、タンパク質の構造と複合体の予測を高速化する。・RoseTTAFoldとは
RoseTTAFoldはDeepLearnigを使用して、限られた情報に基づいてタンパク質構造を予測するソフトウェア。既知のタンパク質のテンプレートを使って学習させたモデルを使い、未知のペプチド配列の立体構造を予測する。・WSL2とは
Windows Subsystem for Linux 2 (WSL2) はWindows上でLinux向けバイナリを実行する方法の一つ。参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【1/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【2/3】
参考:【記事】Windows Subsystem for Linux 2(WSL2)のGPUサポートについて【3/3】
事例追加日:2023/02/22
- 事例No.PC-10747
-

トランスクリプトーム解析用マシン
用途:トランスクリプトーム解析、全ゲノムリシーケンス解析参考価格:950400円お客さまからのご相談内容
イネのトランスクリプトームおよびゲノムデータにおける一連のデータ解析 (前処理、マッピング、DEGsの算出等) を不満なく行うことのできるLinuxマシンを導入したい。
想定しているスペックは以下の通り。・CPU:24コア 48スレッド 以上のCPU
・メモリ:256GB
・ストレージ:SSD 1TB
・OS:Linuxイネのトランスクリプトーム解析は1サンプルが約10Gbp、全ゲノムリシーケンス解析では約45Gbp。
データの保存には外付けストレージを利用する予定。CPUはXeonがいいかと思っているが、性能やコストを含めてAMD Threadripperと比較してどうか気になっている。
OSはUbuntuかRocky Linuxを予定している。どちらが初心者に向いているか知りたい。
予算90万円以下で構成を提案して欲しい。
テガラからのご提案
ご要望の条件に合わせて構成を検討しました。
第3世代Xeon Scalableを搭載した2CPU構成で、システムの合計で24コア/48スレッドです。ストレージ
人間などと比較して、イネのゲノムサイズはそこまで大きくありませんが、解析データの容量はそれなりのサイズになると考えられます。本件では、データ保存用の外部ストレージをお客様側で用意すると伺っていますが、PC本体のみで運用する場合には、データ用のストレージを搭載することをお勧めします。
CPU
24コアのXeonとThreadripper PROで比較すると、性能面ではThreadripper PROの方が優位です。
CPU単体の価格では、相対的にはXeonよりもThreadripperPROの方が安価ですが、構成全体のトータルコストでは、ThreadripperPRO 24コア構成は100万円台前半になるため、本件ではコストを優先し安価なXeonの2CPU構成でご提案しています。なお、次世代シーケンサー解析はCPUコア数やメモリ容量が重要な処理ですので、コア数を減らしてクロック重視で計算速度を上げる考え方はあまり有効ではありません。そのため、シングルコア性能が多少低くても、コア数を確保できる構成を優先するのが望ましいとお考えください。
OS
OSに関しては、Ubuntuと比べてRocky Linuxはあまり融通が利きません。
これは、UbuntuとRocky Linux (のベースになっているRedhat Enterprise Linux) の開発思想の違いによります。Rocky LinuxのベースであるRHELは、長期運用の安定性を第一としています。
Ubuntuはワークステーション向けのディストリビューションとして優れており、最新のハードウェアを採用したワークステーションとしてパフォーマンスを重視する場合、パッケージの更新頻度やカーネルバージョンなどの面でメリットがあります。Rocky Linuxを積極的に選択する理由がない場合には、Ubuntuをお勧めいたします。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Silver 4310 (2.10GHz 12コア) x2 メモリ 256GB REG ECC ストレージ 1TB SSD S-ATA ビデオ NVIDIA T400 ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 850W OS Ubuntu 22.04 キーワード
・トランスクリプトーム解析とは
トランスクリプトームとは、組織、細胞内における遺伝子転写産物(mRNA)の全体を指す。トランスクリプトーム解析は、生体細胞内における遺伝子の発現状況を網羅的に把握する解析手法。RNA-Seq解析や遺伝子発現解析とも呼ばれる。・Ubuntuとは
Ubuntuは、Linuxディストリビューションの1つ。フリーソフトとして提供されており、グラフィカルインストーラーにより、簡単にインストールして使用することができる。参考:Ubuntu (Ubuntu Japanese Team) ※外部サイトへ飛びます
・Rocky Linuxとは
Rocky Linuxは、Linuxディストリビューションの1つ。Red Hat Enterprise Linux (RHEL)のソースコードを使用しており、互換性を持つ。フリーソフトとして提供されており、長期の定期アップデートによる安定性を特長とする。参考:Rocky Linux (Rocky Enterprise Software Foundation) ※外部サイトへ飛びます
事例追加日:2023/02/09
- 事例No.PC-10347B
-

ナノポアシーケンサー解析用マシン (GPU性能優先)
用途:Nanoporeシーケンス (ロングリードシーケンス) 解析、MinKNOW、Guppyなどの利用参考価格:921800円お客さまからのご相談内容
ナノポアシーケンサーによる長鎖のDNA解析を行うためのマシンを導入したい。
想定している条件は以下の通り。・CPU:2CPU構成が望ましい
・メモリ:64GB程度
・ストレージ:2TB以上のSSD データ保存領域にはNASを利用する
・GPU:NVIDIA RTX2060以上 予算内で最も性能の高いGPUを希望
・OS:Ubuntuインストール予定 (OSなしでの出荷を希望)
・予算:90万円程度テガラからのご提案
構成検討においては、CPUとGPUに関する条件がポイントとなります。
ご予算を加味して検討すると、両方の条件を同時に満たすことが難しいため、本事例ではGPUスペックを優先したご提案としています。
2CPU構成を優先した構成は、事例No.PC-10347Aをご覧ください。RTX4090の物理的なサイズと排熱には注意が必要
GPUのRTX4090は、世代差と製品グレードの両面からRTX2060を上回る性能を有しています。
ただし、GPUの物理的なサイズや排熱との兼ね合いから、将来的なGPU増設には対応していませんので、予めご承知おきください。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。




通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Silver 4314 (2.40GHz 16コア) メモリ 64GB REG ECC ストレージ 2TB SSD M.2 ビデオ NVIDIA Geforce RTX4090 ネットワーク on board (1000Base-T x2) 筐体+電源 ミドルタワー筐体 + 1200W OS なし キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・MinKNOWとは
ナノポアシーケンサー「MinION」でシーケンスを行うための専用ソフト。
MinION自体はUSBで直接PCにつなげるタイプのシーケンサーで、ある程度のマシンスペックが要求される。参考:Laboratory and IT Requirements (Oxford Nanopore Technologies) ※外部サイトへ飛びます
・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。事例追加日:2023/01/31
- 事例No.PC-10347A
-

ナノポアシーケンサー解析用マシン (2CPU仕様)
用途:Nanoporeシーケンス (ロングリードシーケンス) 解析、MinKNOW、Guppyなどの利用参考価格:932800円お客さまからのご相談内容
ナノポアシーケンサーによる長鎖のDNA解析を行うためのマシンを導入したい。
想定している条件は以下の通り。・CPU:2CPU構成が望ましい
・メモリ:64GB程度
・ストレージ:2TB以上のSSD データ保存領域にはNASを利用する
・GPU:NVIDIA RTX2060以上 予算内で最も性能の高いGPUを希望
・OS:Ubuntuインストール予定 (OSなしでの出荷を希望)
・予算:90万円程度テガラからのご提案
構成検討においては、CPUとGPUに関する条件がポイントとなります。
ご予算を加味して検討すると、両方の条件を同時に満たすことが難しいため、本事例では2CPU構成を優先したご提案としています。
GPUの性能を重視した構成は、事例No.PC-10347Bをご覧ください。2CPU構成のメリットは、1CPU構成と比較してコア数が多く並列処理性能が高い点と、メモリを最大で2TBまで搭載できる点です。
GPUのRTX A4000は、RTX2060と同程度のクラスですが、ビデオメモリ容量やCUDAコア数など全体的に優位性の高い製品です。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。




通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Silver 4310 (2.10GHz 12コア) x2 メモリ 64GB REG ECC ストレージ 2TB SSD M.2 ビデオ NVIDIA RTX A4000 ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 1200W OS なし キーワード
・Nanopore (ナノポア) とは
ナノポアはnm (ナノメートル) サイズの細孔。ナノポアシーケンサーでは、ナノポアを持つ人工膜タンパク質を用い、DNAがナノポアを通る際の電流変化から塩基配列を決定する。ナノポアシーケンサーは、従来の次世代シーケンサーよりもロングリードのDNA解析が可能である点が特長。・MinKNOWとは
ナノポアシーケンサー「MinION」でシーケンスを行うための専用ソフト。
MinION自体はUSBで直接PCにつなげるタイプのシーケンサーで、ある程度のマシンスペックが要求される。参考:Laboratory and IT Requirements (Oxford Nanopore Technologies) ※外部サイトへ飛びます
・Guppyとは
Guppyは遺伝子配列データをグラフィカルに表示する遺伝子情報表示プログラム。配列中のタンパク質に翻訳される領域や、マーカとして知られている部位に対する注釈などをわかりやすく表示、または編集することができる。事例追加日:2023/01/31
- 事例No.PC-10706
-

次世代シーケンサー解析用ワークステーション
用途:BWA、GATK、Samtoolsの利用参考価格:1201200円お客さまからのご相談内容
バイオインフォマティクス分野で次世代シーケンサー解析を行うためのワークステーションが欲しい。解析パイプラインで使用するソフトウェアは「BWA」「GATK」「Samtools」などを予定。希望条件は以下の通り。
・CPU:32スレッド以上
・メモリ:予算内で限界まで搭載 (将来的には1TBまで増設予定)
・ストレージ:512GB~1TBのSSD NVMeタイプ
・GPU:画面が表示できればOK
・OS:インストールなし (ubuntu 20.04を予定)
・予算:120万円程度テガラからのご提案
ご希望の条件に合わせて構成を検討しました。
CPUはRyzen ThreadripperPRO 5969WX (24コア 48スレッド) を採用しています。
ストレージはNVMeタイプの1TB SSDとしています。メモリは256GB搭載しており、1TBまでの拡張が可能です。
ただし、出荷時点でのメモリモジュール構成は64GB x4枚であり、メモリの空きスロットが4つであることを踏まえると、増設だけで1TBを達成するのは難しい構成です。
初期状態のメモリを活かす場合は追加で64GB x4枚を増設し、512GBまで拡張可能です。
1TBまで拡張する場合には、既存の64GBモジュールを取り外し、128GBモジュール x8枚を搭載する必要があります。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen ThreadripperPRO 5965WX (3.80GHz 24コア) メモリ 256GB REG ECC ストレージ1 1TB SSD M.2 ビデオ NVIDIA GeForce GT710 ネットワーク on board (1GbE x1 10GBase-T x1) 筐体+電源 タワー型筐体 + 1000W OS なし キーワード
・BWAとは
BWAはヒトゲノムなどの大規模な参照ゲノムに対して、低発散配列をマッピングするためのソフトウェアパッケージ。BWA-backtrack、BWA-SW、BWA-MEMの3つのアルゴリズムで構成されている。・GATKとは
GATK (Genome Analysis Toolkit) は、次世代シーケンサーから出力された塩基配列データからバリアントの解析 (遺伝子の変異解析) を行うための解析ツール群。内包するツールは、個別に使用することも連携させて使用することもできる。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)事例追加日:2023/01/19
- 事例No.PC-10539
-

Nextseq2000システムで取得したNGSデータを解析するためのマシン
用途:RNA-Seqマッピングツール「HISAT2」「Bowtie2」、マッピング結果解析ツール「samtools」、相同性検索プログラム「BLAST」、ゲノムアセンブリ用プログラム「Velvet」の利用参考価格:2015200円お客さまからのご相談内容
Nextseq2000システムで取得したNGSデータを解析するためのマシンを導入したい。
以下の条件に近い構成を提案して欲しい。・CPU:Intel Xeon 24コア以上 x2
・メモリ:768GB程度
・ストレージ1:SSD 2TB M.2
・ストレージ2:HDD 4TB S-ATA
・OS:Ubuntu
・予算:200万円になるべく近くなるようにテガラからのご提案
ご要望のCPUコア数を満たす構成にてご提案しました。
1CPUあたり28コア x2で合計56コアとなるようにCPUを選定しています。第3世代Xeon Scalableは、メモリチャンネルが8ですので、ご要望の768GBを超える容量で最適な構成とした場合、1TBを選択する必要があります。しかし、その場合には予算を大幅に超過してしまうため、ひとまずご希望よりも少ない容量でモジュール構成を最適化した512GBをご提案し、スペックと価格感をご確認いただく流れとしました。
本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。





通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon Gold 6338 (2.00Hz 32コア) メモリ 512GB REG ECC (32GB x16) ストレージ1 2TB SSD M.2 ストレージ2 8TB HDD S-ATA ビデオ on board (VGAx1) ネットワーク on board (1000Base-T x2) 筐体+電源 タワー型筐体 + 850W OS Ubuntu 22.04 キーワード
・HISAT2とは
HISAT2は、次世代シーケンシングにおけるリード (DNAとRNAの両方) をヒトゲノムの集団および単一の参照ゲノムにマッピングするためアライメントプログラム。高速でメモリ使用量が少ない。・Bowtie2とは
Bowtie2は、シーケンスリードを参照配列にアライメントするためのツール。哺乳類のような比較的長いゲノムのアライメントに優れている。・Samtoolsとは
Samtoolsは次世代シーケンサーから出力されたデータを操作するためのプログラム群。
Samtools (SAM/BAM/CRAM 形式の読み取り/書き込み/編集/インデックス作成/表示)
BCFtools (BCF2/VCF/gVCF ファイルの読み取り/書き込みと、SNPおよび変異データの呼び出し/フィルタリング/要約)
HTSlib (次世代シーケンスデータの読み取り/書き込み用のACライブラリ)・Velvetとは
Velvetはゲノム配列をアセンブリするためのプログラム。de Bruijnグラフに基づくde novoアセンブリのためのツールであり、高いカバレッジを持つ短いリードデータに適している。また、de Bruijnグラフを操作することで、シーケンスエラーを除去し、リピートを解消するアルゴリズムが実装されている。事例追加日:2023/01/06
- 事例No.PC-10483
-

タンパク質のドメイン検索用マシン
用途:BLASTによるDNA塩基配列の検索、HMMERによるタンパク質のドメイン検索参考価格:474100円お客さまからのご相談内容
BLASTによるDNA塩基配列の検索や、HMMERによるタンパク質のドメイン検索を行うためのマシンを導入したい。
教員と複数の学生が使用し、学内の有線LAN経由でマシンにアクセスする使い方を予定している。
BLASTでのクエリ配列は数百から数千程度で、データベース配列は10万程度を予定。
HMMERによるドメイン検索は、10万程度のクエリ配列を想定している。
マシン性能が十分であれば、植物のゲノムde novo解析も行いたい。 現時点で考えているマシンスペックは以下の通り。・CPU:Intel Core i7 16コア以上
・メモリ:64GB
・ストレージ1:1TB SSD S-ATA
・ストレージ2:8TB HDD S-ATA
・ビデオカード:Geforce GT1030程度
・ネットワーク:ギガビットイーサネット対応テガラからのご提案
ご要望に合わせて構成を検討しました。
データベースはHDD 8TBへの格納を想定していますが、サイズによってはストレージ容量が不足する場合があるため、容量面で問題ないことをお客様にご確認いただいています。de novo解析の実行も可能な構成ですが、優先度の高い要件として考慮する場合には、仕様上の最大メモリ容量となる128GBを搭載するのが良いかと思われます。
また、ネットワークアクセスで利用し、研究室内で小規模な簡易サーバーとして利用するのみでしたら、本事例の構成でもコスト重視の選択として成立します。ただし、学部レベルの人数で利用する想定の場合は、明らかにスペックが不足します。
マシンの重要度や求める可用性などの条件によっては、より本格的なサーバー構成を検討いただく必要があるため、お客様にはご提案と合わせてお伝えしています。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7950X (4.50Hz 16コア) メモリ 64GB ストレージ1 1TB SSD S-ATA ストレージ2 8TB HDD S-ATA ビデオ NVIDIA Geforce GT1030 ネットワーク on board (2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー筐体 + 850W OS Rocky Linux 8 キーワード
・BLASTとは
BLAST (Basic Local Alignment Search Tool) は、DNAの塩基配列やタンパク質のアミノ酸配列のシーケンスアライメントを行う相同性検索プログラム。手元にあるシーケンスで、シーケンスデータベースもしくはライブラリに対して検索を行うことにより、ある閾値以上のスコアで類似するシーケンス群を発見することができる。参考:BLAST (NAtional Center for Biotechnology Information) ※外部サイトに飛びます
・HMMERとは
HMMERはシーケンス解析用のフリーソフトウェア。相同タンパク質またはヌクレオチド配列を特定し、シーケンスアライメントを実行する。参考:HMMER ※外部サイトに飛びます
・de novo解析とは
タンデム質量分析からペプチドのアミノ酸配列を決定する方法。参照配列を必要とせず、非モデル生物の遺伝子解析で用いられる。事例追加日:2022/12/22
- 事例No.PC-10596
-

NGS解析用マシン
用途:統計分析ソフトウェア「R」、画像解析ソフトウェア「WinRHIZO」の利用参考価格:423500円お客さまからのご相談内容
NGS解析用マシンの導入を考えている。
バイオインフォマティクスを専門にはしていないため、それほど高度な作業を行う予定はない。
WinRHIZOで画像解析したデータや遺伝子発現データをExcelやRなどで解析したり、シーケンスデータから定量データに計算させる処理を考えている。3Dモデルを動かすような処理は行わない。想定スペックは以下の通り。
・CPU:32スレッド程度
・メモリ:64GB
・ストレージ:SSD 1TB S-ATA
・OS:Windows
・予算:30万~50万円上記の想定スペックは知人からのアドバイスによるもので、自分自身はPCに詳しくない。
一般的な大手メーカー製PCと比べて、セットアップの手間が多いなどの問題はないか。また、購入した場合にはどのようなソフトが付属するのか知りたい。テガラからのご提案
ご要望に合わせて、構成をご提案しました。
CPUは、AMD Ryzen9 Threadripper 7950Xを選択し、32スレッド程度の条件を満たしています。
また、3Dモデルの表示や操作は行わないと伺いましたので、ビデオ出力はコストを優先してオンボードとしています。一般的な大手メーカー製マシンと比較した場合、納入後に行っていただくセットアップ内容には、それほど大きな違いはありません。しかし、弊社製PCにはセキュリティソフトの試用版などはバンドルされませんので、必要な場合にはご相談ください。
また、OS以外のソフトウェアに関しては、Windowsが標準で提供するもの以外は付属・インストールしておりません。そのため、利用予定のない多数のソフトウェアにマシンのリソースを占有されたり、煩わしいポップアップが表示されることなく、快適にお使いいただくことができます。
なお、現在のWindowsでは、DVDへの書き込みや読み込みが標準サポートされています。DVDビデオの作成や再生を行う場合には別途ソフトウェアが必要ですが、そのような用途での利用がない場合には追加のソフトウェアは不要です。本事例の構成は、お客様から頂戴した条件を元に検討した内容です。
掲載内容とは異なる条件でご検討の場合でも、お気軽にご相談ください。




通常24時間以内に担当者からご連絡いたします
主な仕様
CPU AMD Ryzen9 7950X (4.50GHz 16コア) メモリ 64GB ストレージ 1TB SSD S-ATA ビデオ on board (DisplayPort x1 HDMI x1) ネットワーク on board (2.5G x1 10/100/1000Base-T x1) Wi-Fi x1 筐体+電源 ミドルタワー型筐体 + 850W OS Microsoft Windows 11 Pro 64bit キーワード
・NGS解析とは
NGS (Next Generation Sequencer:次世代シーケンサー) は、核酸 (DNAとRNA)の塩基配列情報を決定するための基盤技術。数百万のDNA分子を同時に配列決定することが可能。
NGSは高速でシークエンシングを行うことができるため、臨床サンプルの劣化の早いRNAウイルスの塩基配列同定などで用いられる。・Rとは
Rとはオープンソース・フリーソフトウェアの統計解析向けプログラミング言語/開発実行環境。統計処理のための計算やグラフ化で利用される。
多くのライブラリが存在するため、ライブラリを呼び出すだけで複雑な手法を扱うことができる。参考:The R Project for Statistical Computing ※外部サイトに飛びます
・WinRHIZOとは
WinRHIZOはRegent Instruments社による画像解析ソフトウェア。植物の根長や形態、構造、色を測定・解析を行う。参考:WinRHIZO (Regent Instruments) ※外部サイトに飛びます
事例追加日:2022/12/09
- 事例No.PC-8561
-

次世代シーケンサー解析用マシン (Bioconda3の利用を想定)
用途:Bioconda3の利用参考価格:750200円お客さまからのご相談内容
次世代シーケンサー解析ソフト「Bioconda3」を利用するためのマシンを導入したい。
想定しているスペックは以下の通り。・CPU:Xeon 36スレッド程度
・メモリ:ECC 64~128GB
・ストレージ:SSD 1TB + HDD 6TB
・OS:Ubuntu 20.04
・その他:Bioconda3プリインストールBioconda3の他にも、BWA、GATK、STAR-Fusion、SAMtools、Bedtoolsなどを利用する予定。
予算140万円の範囲で提案して欲しい。テガラからのご提案
ご要望に合わせて36スレッドのXeon Wを採用した構成にてお見積もりしました。
HDDは6TB製品がほとんど流通しておらず、入手できた場合でもコスト面でもメリットが少ないため、代替品として8TB製品を選択しています。また、ご予算の上限には余裕がありますが、ご利用予定のソフトの中にはGPGPUを利用するものがないため、ビデオカードは画面出力のみを考慮したエントリークラスの製品としています。GPUの利用も想定する場合、より上位の製品への変更が可能です。
その他のスペックはひとまずご要望のスペックを優先した選定としていますが、ご予算上限にあわせたご提案をご希望の場合には気兼ねなくお申し付けください。なお、Bioconda3はminiconda (Anacondaのコンパクト版) のチャンネルとして導入する形ですので、Biocondaチャンネルの登録を行った状態での出荷を想定しています。
■Bioconda3
condaチャンネルのディストリビューションの1つ。
バイオインフォマティクス関連のツールが登録されたパッケージマネージャー。■miniconda
Pythonとパッケージマネージャー「conda」に加え、必要最低限のパッケージの入ったディストリビューション。



通常24時間以内に担当者からご連絡いたします
主な仕様
CPU Xeon W-2295 (3.00GHz 18コア) メモリ 128GB ストレージ1 1TB SSD M.2 ストレージ2 8TB HDD S-ATA ビデオ NVIDIA T400 ネットワーク on board (10/100/1000Base-T x1 5G x1) 筐体+電源 ミドルタワー筐体 + 850W OS Ubuntu 20.04 その他 Bioconda3インストール設定 事例追加日:2022/10/13
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
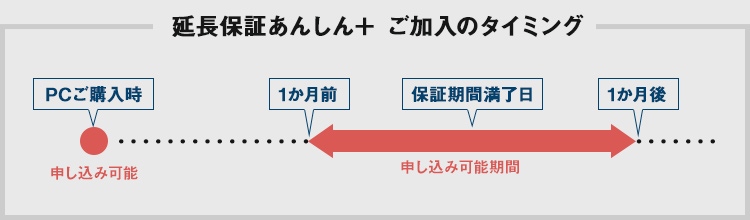
| 「あんしん+」 もしもの時の延長保証サービス |
|
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 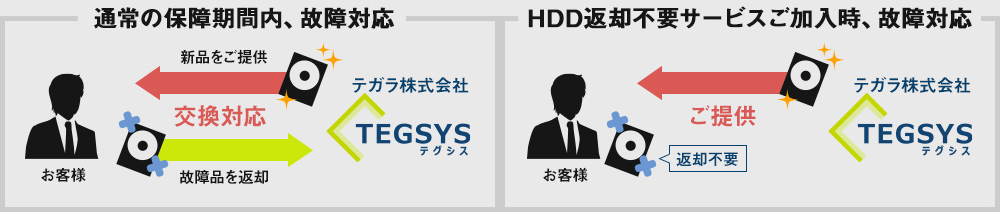
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。