- 事例No.PC-TS2J253952
-
 参考価格 (税込):
参考価格 (税込):
1,794,100円事例追加日:2026/2/27大規模ゲノム解析向け2CPU・512GBメモリ搭載ワークステーション
用途:NGSゲノム解析、RNA-seq解析 (VCFtools、PLINK2、RFMIX2)お客さまからのご相談内容
ゲノムデータを用いた集団遺伝学・ゲノム進化学解析に適したワークステーションを導入したい。 主な作業として、1万人規模の全ゲノムデータの解析 (VCF形式でRFMIX2やVCFtools、PLINK2などを利用)。 さらには、RNA-seq データのリファレンスゲノムへのマッピング・データ間比較解析を想定している。 CPU 32コア以上、メモリ256または512GB、4TB SSDを備えた構成を基準…テガラからのご提案
CPU構成について PLINK2やVCFtoolsはマルチスレッド並列処理が中心のため、コア数の確保が処理時間に大きく影響します。 そこで、Intel Xeon 6517P (16コア) を2基搭載し、合計32コア環境を構築しました。 併せて、2CPU構成とすることで、各CPUが8チャネルずつ、合計16チャネルのメモリ帯域を並列に利用可能です。 これにより、大規模データを扱うゲノム解析でも、安定し…主な仕様
CPU Intel Xeon 6517P 3.20GHz(TB 4.20GHz) 16C/32T ×2基構成 メモリ 合計512GB DDR5 5600 REG ECC 32GB x 16 ストレージ 4TB SSD M.2 NVMe Gen4 ビデオ NVIDIA RTX A400 4GB (MiniDisplayPort x4) ネットワーク on board (10GbE x2) 筐体+電源 タワー型筐体+1000W 80PLUS PLATINUM OS Ubuntu 24.04 保証 HDD返却不要サービス 1年
- 事例No.PC-TE1J254011
-
 参考価格 (税込):
参考価格 (税込):
3,261,500円事例追加日:2026/2/12シーケンスデータ解析/機械学習用ワークステーション (システム要件に最適化)
用途:エピジェネティクス解析、de novoアセンブリ、RNA-Seq解析、メタゲノム解析、機械学習お客さまからのご相談内容
事例No. PC-25000268を見ての問い合わせ。ナノポアのシーケンスデータ解析と機械学習の双方に対応するワークステーションを導入したい。 エピジェネティクス解析やde novoアセンブリ、RNA-Seq解析、メタゲノム解析などを想定している。 使用するソフトウェアは、以下の通り。 汎用解析・ML基盤:Samtools、XGBoost、LightGBM ゲノムアセンブリ・評価:SPAdes・B…テガラからのご提案
ツール要件を重視した大容量メモリ構成 本構成は「システム要件を基準に最適化した構成」としてご案内したスペックです。特に大規模アセンブリや多数サンプルのバッチ処理を想定し、CPUコア数とメモリ容量を優先。EPYC 9554 (64コア) と768GBメモリにより、メモリ負荷の大きい解析に強みを持たせています。 事例No. PC-25000268をグレードアップしつつ、機械学習にも対応できる汎用性を重…主な仕様
CPU AMD EPYC 9554 3.1GHz 64C/128T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ1 4TB SSD M.2 NVMe Gen5 x 2 ストレージ2 24TB HDD S-ATA ビデオ NVIDIA RTX PRO6000 Max-Q 96GB ネットワーク on board (10GBase-T x2) 筐体+電源 ミドルタワー 1500W 80PLUS PLATINUM OS Ubuntu 24.04 その他 現地設置作業(開梱・設置・ケーブリング・起動確認)
- 事例No.PC-TW3J253928
-
 参考価格 (税込):
参考価格 (税込):
3,169,100円事例追加日:2026/2/12シーケンスデータ解析/機械学習用ワークステーション (汎用構成)
用途:エピジェネティクス解析、de novoアセンブリ、RNA-Seq解析、メタゲノム解析、機械学習お客さまからのご相談内容
事例No. PC-25000268を見ての問い合わせ。ナノポアのシーケンスデータ解析と機械学習の双方に対応するワークステーションを導入したい。 エピジェネティクス解析やde novoアセンブリ、RNA-Seq解析、メタゲノム解析などを想定している。 使用するソフトウェアは、以下の通り。 汎用解析・ML基盤:Samtools、XGBoost、LightGBM ゲノムアセンブリ・評価:SPAdes・B…テガラからのご提案
機械学習を見据えたバランス強化構成 本構成は「事例No. PC-25000268をグレードアップしつつ、機械学習にも対応できる汎用性」を重視した案としてご案内しました。Xeon W プロセッサと512GBメモリを組み合わせ、シーケンス解析に必要なスループットと、機械学習処理に必要な演算性能の両立を図っています。 システム要件を基準に最適化した構成は、事例No.PC- TE1J254011をご覧くだ…主な仕様
CPU Intel Xeon W7-3565X 2.50GHz (TB3.0時 最大4.8GHz) 32C/64T メモリ 合計512GB DDR5 5600 REG ECC 64GB x 8 ストレージ1 4TB SSD M.2 NVMe Gen5 ストレージ2 24TB HDD S-ATA ビデオ NVIDIA RTX PRO5000 48GB ネットワーク on board (1GbE x1 /10GbE x1) 筐体+電源 ミドルタワー筐体 1500W 80PLUS PLATINUM OS Ubuntu 24.04
- 事例No.PC-TRNX254496
-
 参考価格 (税込):
参考価格 (税込):
1,156,100円事例追加日:2026/2/9Gaussian・LAMMPS・GROMACS 併用向けワークステーション
用途:Gaussian16、LAMMPS、GROMACSお客さまからのご相談内容
反応機構解析、タンパク質ドッキング、インシリコ (計算化学) スクリーニングを想定した計算用PCを導入したい。 現在はGaussian16 を中心に、LAMMPSとGROMACS も併用しているが、計算負荷が増え、現行PCでは性能不足が顕著になっている。 将来的にはLinux系のOSに変更し、LAMMPSとGROMACSをメインにすることも視野に入れている。 予算は約100万円 (超過も可)。 想…テガラからのご提案
CPUとメモリについて Gaussian は計算の多くを CPU で処理するため、並列利用するコア数と実効クロックが計算時間に直結します。 今回は、ご予算内で並列計算時の性能を確保できる、Ryzen 9 9950X (16コア) を採用しました。 メモリはご要望に合わせて128GB (32GB×4枚) を搭載しています。 Ryzen 9 9950X は最大 192GB まで対応しますが、今回の構成…主な仕様
CPU AMD Ryzen9 9950X 4.30GHz (Boost時最大5.70GHz) 16C/32T メモリ 合計128GB DDR5 5600 32GB x 4 ストレージ1 2TB SSD M.2 NVMe Gen4 ビデオ NVIDIA GeForce RTX5090 32GB ネットワーク on board (2.5G x1) Wi-Fi,Bluetooth 筐体+電源 ミドルタワー型筐体+1500W 80PLUS TITANIUM OS Microsoft Windows 11 Professional 64bit
ご注文の流れ
 |
お問い合わせフォームよりご相談内容をお書き添えの上、 お問い合わせください。 (お電話でもご相談を承っております) |
 |
弊社より24時間以内にメールにてご連絡します。 |
 |
必要に応じてメールにて打ち合わせさせていただいた上で、 メール添付にてお見積書をお送りします。 |
 |
お見積もり内容にご納得いただけましたら、メールにてご注文ください。 ご注文確定後、必要な部材を手配し PCを組み立てます。 (掛売りの場合、最初に新規取引票のご記入をお願いしております) |
 |
動作チェックなどを行い、納期が確定いたしましたらご連絡いたします。 (納期は仕様や製造ラインの状況により異なります) |
 |
お客様のお手元にお届けいたします (ヤマト運輸/西濃運輸) |
お支払い方法
お支払い方法は、お見積もりメール・お見積書でもご案内しています。
| 法人掛売りのお客様 |
| 原則として、月末締、翌月末日払いの後払いとなります。 |
| 学校、公共機関、独立行政法人のお客様 |
| 納入と同時に書類三点セット(見積書、納品書、請求書)をお送りしますのでご請求金額を弊社銀行口座へ期日までにお振込み願います。 先に書面での正式見積書(社印、代表者印付)が必要な場合はお知らせください。 |
| 企業のお客様 |
| 納品時に、代表者印つきの正式書類(納品書、請求書)を添付いたします。 ご検収後、請求金額を弊社銀行口座へお支払い期日までにお振込み願います。 |
| 銀行振込(先振込み)のお客様 |
| ご注文のご連絡をいただいた後、お振込みを確認した時点で注文の確定とさせていただきます。 |
修理のご依頼・サポートについて
弊社製PCの保証内容は、お見積もりメールでもご案内しています。
■お問合せ先
テガラの取り扱い製品に関する総合サポート受付のWEBサイトをご用意しております。
テガラ株式会社 サポートサイト
※お問い合わせの際には、「ご購入前」と「ご購入後」で受付フォームが分かれておりますので、ご注意ください。
| メール | support@tegara.com |
| 電話 | 053-543-6688 |
■テグシスのサポートについて
保証期間内の修理について
保証期間内におけるハードウェアの故障や不具合につきましては、無償で修理いたします。
ただし、お客様による破損や、ソフトウェアに起因するトラブルなど保証規定にて定める項目に該当する場合は保証対象外となります。
保証期間経過後も、PCをお預かりしての初期診断は無料で実施しております。
無料メール相談
PCの運用やトラブルにつきまして、メールでのご相談を承ります。経験・知識の豊富な技術コンサルタントが無料でアドバイスいたします。
※調査や検証が必要な場合はお答えできなかったり、有償対応となることがあります
オプション保証サービス
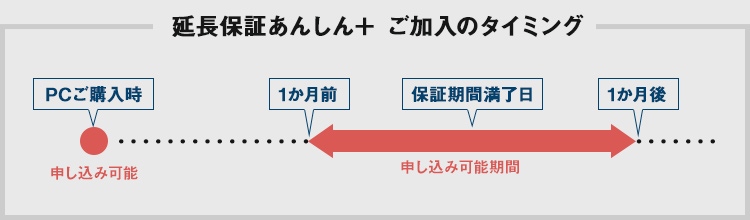
| 「あんしん+」 もしもの時の延長保証サービス |
|
PCのご購入時にトータル5年までの延長保証をご選択いただけます。また、ご購入後にも延長保証を申し込むことができます。
|
| HDD返却不要サービス |
|
保証期間内にPCのHDD(SSD)が故障した場合、通常、新品のHDDとの交換対応となり、故障したHDDはご返却いたしません。 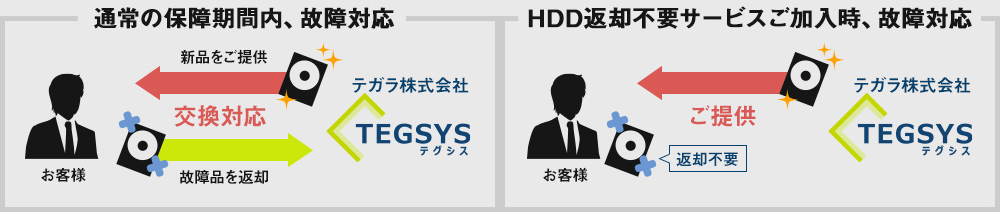
|
| オンサイト保守サポート | |
|
故障発生時、必要に応じエンジニアスタッフが現地へ訪問し、保守対応を行うサービスです。
|
「お客様だけのオーダーメイドPC」を製作しています。
用途に応じた細かなアドバイスや迅速な対応がテガラの強みです。
上記の仕様はテガラでお客様に提案したPC構成の一例です。
掲載内容は提案当時のものであり、また使用する部材の供給状況によっては、現在では提供がむずかしいものや、部材を変更してのご提案となる場合がございます。
参考価格については、提案当時の価格(送料込・税込)になります。
ご相談時期によっては価格が異なる場合がございますので、あらかじめご了承ください。